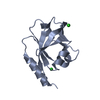
登録情報 データベース : PDB / ID : 5cm4タイトル Crystal structure of human Frizzled 4 Cysteine-Rich Domain (CRD) Frizzled-4 キーワード / / / / 機能・相同性 生物種 Homo sapiens (ヒト)手法 / / / 解像度 : 2.4 Å データ登録者 Ke, J. / Parker, N. / Gu, X. / Zhang, C. / Melcher, K. / Xu, H.E. 資金援助 組織 認可番号 国 National Institutes of Health/National Institute of Diabetes and Digestive and Kidney Disease (NIH/NIDDK) DK071662 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) GM102545 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) GM104212 Michigan Economic Development Corporation and the Michigan Technology Tri-Corridor 085P1000817
ジャーナル : Cell Res. / 年 : 2015タイトル : Structural basis of the Norrin-Frizzled 4 interaction.著者 : Shen, G. / Ke, J. / Wang, Z. / Cheng, Z. / Gu, X. / Wei, Y. / Melcher, K. / Xu, H.E. / Xu, W. 履歴 登録 2015年7月16日 登録サイト / 処理サイト 改定 1.0 2015年8月12日 Provider / タイプ 改定 1.1 2015年9月16日 Group 改定 1.2 2017年9月27日 Group / Derived calculations / カテゴリ / pdbx_struct_oper_listItem / _pdbx_struct_oper_list.symmetry_operation改定 1.3 2019年12月25日 Group / カテゴリ / Item 改定 2.0 2020年7月29日 Group Advisory / Atomic model ... Advisory / Atomic model / Data collection / Derived calculations / Structure summary カテゴリ atom_site / chem_comp ... atom_site / chem_comp / entity / pdbx_branch_scheme / pdbx_chem_comp_identifier / pdbx_entity_branch / pdbx_entity_branch_descriptor / pdbx_entity_branch_link / pdbx_entity_branch_list / pdbx_entity_nonpoly / pdbx_nonpoly_scheme / pdbx_struct_assembly_gen / pdbx_struct_special_symmetry / pdbx_validate_close_contact / struct_asym / struct_conn / struct_site / struct_site_gen Item _atom_site.B_iso_or_equiv / _atom_site.Cartn_x ... _atom_site.B_iso_or_equiv / _atom_site.Cartn_x / _atom_site.Cartn_y / _atom_site.Cartn_z / _atom_site.auth_asym_id / _atom_site.auth_seq_id / _atom_site.label_asym_id / _atom_site.label_entity_id / _chem_comp.name / _chem_comp.type / _pdbx_entity_nonpoly.entity_id / _pdbx_entity_nonpoly.name / _pdbx_struct_assembly_gen.asym_id_list / _pdbx_struct_special_symmetry.label_asym_id / _pdbx_validate_close_contact.auth_asym_id_2 / _pdbx_validate_close_contact.auth_seq_id_2 / _struct_conn.pdbx_role / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id 解説 / Provider / タイプ 改定 2.1 2023年9月27日 Group Data collection / Database references ... Data collection / Database references / Refinement description / Structure summary カテゴリ chem_comp / chem_comp_atom ... chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_ncs_dom_lim Item _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI ... _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ncs_dom_lim.beg_auth_comp_id / _struct_ncs_dom_lim.beg_label_asym_id / _struct_ncs_dom_lim.beg_label_comp_id / _struct_ncs_dom_lim.beg_label_seq_id / _struct_ncs_dom_lim.end_auth_comp_id / _struct_ncs_dom_lim.end_label_asym_id / _struct_ncs_dom_lim.end_label_comp_id / _struct_ncs_dom_lim.end_label_seq_id
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素
 キーワード
キーワード SIGNALING PROTEIN /
SIGNALING PROTEIN /  Wnt signaling (Wntシグナル経路) / Norrin signaling / Frizzled 4 extracelluar domain / Cysteine-Rich Domain
Wnt signaling (Wntシグナル経路) / Norrin signaling / Frizzled 4 extracelluar domain / Cysteine-Rich Domain 機能・相同性情報
機能・相同性情報 Wnt signaling pathway, calcium modulating pathway / Norrin signaling pathway / extracellular matrix-cell signaling / progesterone secretion / retinal blood vessel morphogenesis / locomotion involved in locomotory behavior / retina vasculature morphogenesis in camera-type eye / regulation of vascular endothelial growth factor receptor signaling pathway / Signaling by RNF43 mutants ...cerebellum vasculature morphogenesis /
Wnt signaling pathway, calcium modulating pathway / Norrin signaling pathway / extracellular matrix-cell signaling / progesterone secretion / retinal blood vessel morphogenesis / locomotion involved in locomotory behavior / retina vasculature morphogenesis in camera-type eye / regulation of vascular endothelial growth factor receptor signaling pathway / Signaling by RNF43 mutants ...cerebellum vasculature morphogenesis /  Wnt signaling pathway, calcium modulating pathway / Norrin signaling pathway / extracellular matrix-cell signaling / progesterone secretion / retinal blood vessel morphogenesis / locomotion involved in locomotory behavior / retina vasculature morphogenesis in camera-type eye / regulation of vascular endothelial growth factor receptor signaling pathway / Signaling by RNF43 mutants / WNT5A-dependent internalization of FZD4 /
Wnt signaling pathway, calcium modulating pathway / Norrin signaling pathway / extracellular matrix-cell signaling / progesterone secretion / retinal blood vessel morphogenesis / locomotion involved in locomotory behavior / retina vasculature morphogenesis in camera-type eye / regulation of vascular endothelial growth factor receptor signaling pathway / Signaling by RNF43 mutants / WNT5A-dependent internalization of FZD4 /  Wnt receptor activity / non-canonical Wnt signaling pathway / positive regulation of neuron projection arborization / endothelial cell differentiation / Wnt-protein binding / establishment of blood-brain barrier / Class B/2 (Secretin family receptors) / negative regulation of cell-substrate adhesion / positive regulation of dendrite morphogenesis /
Wnt receptor activity / non-canonical Wnt signaling pathway / positive regulation of neuron projection arborization / endothelial cell differentiation / Wnt-protein binding / establishment of blood-brain barrier / Class B/2 (Secretin family receptors) / negative regulation of cell-substrate adhesion / positive regulation of dendrite morphogenesis /  cytokine receptor activity /
cytokine receptor activity /  cytokine binding / canonical Wnt signaling pathway /
cytokine binding / canonical Wnt signaling pathway /  脈管形成 / cellular response to retinoic acid / Regulation of FZD by ubiquitination / substrate adhesion-dependent cell spreading / cellular response to leukemia inhibitory factor / Asymmetric localization of PCP proteins / G protein-coupled receptor activity /
脈管形成 / cellular response to retinoic acid / Regulation of FZD by ubiquitination / substrate adhesion-dependent cell spreading / cellular response to leukemia inhibitory factor / Asymmetric localization of PCP proteins / G protein-coupled receptor activity /  PDZ domain binding / sensory perception of sound / clathrin-coated endocytic vesicle membrane / neuron differentiation /
PDZ domain binding / sensory perception of sound / clathrin-coated endocytic vesicle membrane / neuron differentiation /  Wntシグナル経路 / positive regulation of DNA-binding transcription factor activity / cell-cell junction / Cargo recognition for clathrin-mediated endocytosis /
Wntシグナル経路 / positive regulation of DNA-binding transcription factor activity / cell-cell junction / Cargo recognition for clathrin-mediated endocytosis /  Clathrin-mediated endocytosis / Ca2+ pathway /
Clathrin-mediated endocytosis / Ca2+ pathway /  signaling receptor activity /
signaling receptor activity /  amyloid-beta binding /
amyloid-beta binding /  血管新生 / cell population proliferation / response to hypoxia / positive regulation of cell migration / protein heterodimerization activity / glutamatergic synapse /
血管新生 / cell population proliferation / response to hypoxia / positive regulation of cell migration / protein heterodimerization activity / glutamatergic synapse /  ubiquitin protein ligase binding /
ubiquitin protein ligase binding /  樹状突起 / protein-containing complex binding / positive regulation of DNA-templated transcription /
樹状突起 / protein-containing complex binding / positive regulation of DNA-templated transcription /  細胞膜 / protein homodimerization activity /
細胞膜 / protein homodimerization activity /  細胞膜
細胞膜
 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.4 Å
分子置換 / 解像度: 2.4 Å  データ登録者
データ登録者 米国, 4件
米国, 4件  引用
引用 ジャーナル: Cell Res. / 年: 2015
ジャーナル: Cell Res. / 年: 2015 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5cm4.cif.gz
5cm4.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5cm4.ent.gz
pdb5cm4.ent.gz PDB形式
PDB形式 5cm4.json.gz
5cm4.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/cm/5cm4
https://data.pdbj.org/pub/pdb/validation_reports/cm/5cm4 ftp://data.pdbj.org/pub/pdb/validation_reports/cm/5cm4
ftp://data.pdbj.org/pub/pdb/validation_reports/cm/5cm4 リンク
リンク 集合体
集合体


 要素
要素 / hFz4 / FzE4
/ hFz4 / FzE4
 Homo sapiens (ヒト) / 遺伝子: FZD4 / プラスミド: pcDNA6-Fz4CRD-FcH6 / 細胞株 (発現宿主): HEK293 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: FZD4 / プラスミド: pcDNA6-Fz4CRD-FcH6 / 細胞株 (発現宿主): HEK293 / 発現宿主: 
 Homo sapiens (ヒト) / 参照: UniProt: Q9ULV1
Homo sapiens (ヒト) / 参照: UniProt: Q9ULV1 オリゴ糖 / 分子量: 424.401 Da / 分子数: 1 / 由来タイプ: 組換発現
オリゴ糖 / 分子量: 424.401 Da / 分子数: 1 / 由来タイプ: 組換発現 N-アセチルグルコサミン
N-アセチルグルコサミン 水
水 X線回折
X線回折 試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 21-ID-D / 波長: 1.078 Å
/ ビームライン: 21-ID-D / 波長: 1.078 Å : 1.078 Å / 相対比: 1
: 1.078 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj






