[English] 日本語
 Yorodumi
Yorodumi- PDB-3l9v: Crystal Structure of Salmonella enterica serovar Typhimurium SrgA -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3l9v | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal Structure of Salmonella enterica serovar Typhimurium SrgA | ||||||
 Components Components | Putative thiol-disulfide isomerase or thioredoxin | ||||||
 Keywords Keywords |  OXIDOREDUCTASE / thioredoxin-fold / SrgA / thiol-disulfide oxidoreductase / OXIDOREDUCTASE / thioredoxin-fold / SrgA / thiol-disulfide oxidoreductase /  Isomerase Isomerase | ||||||
| Function / homology |  Function and homology information Function and homology information protein-disulfide reductase activity / protein-disulfide reductase activity /  isomerase activity / cell redox homeostasis / isomerase activity / cell redox homeostasis /  periplasmic space periplasmic spaceSimilarity search - Function | ||||||
| Biological species |   Salmonella enterica subsp. enterica serovar Typhimurium (bacteria) Salmonella enterica subsp. enterica serovar Typhimurium (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 2.151 Å SAD / Resolution: 2.151 Å | ||||||
 Authors Authors | Heras, B. / Jarrott, R. / Shouldice, S.R. / Guncar, G. | ||||||
 Citation Citation |  Journal: J.Biol.Chem. / Year: 2010 Journal: J.Biol.Chem. / Year: 2010Title: Structural and functional characterization of three DsbA paralogues from Salmonella enterica serovar typhimurium Authors: Heras, B. / Totsika, M. / Jarrott, R. / Shouldice, S.R. / Guncar, G. / Achard, M.E.S. / Wells, T.J. / Argente, M.P. / McEwan, A.G. / Schembri, M.A. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3l9v.cif.gz 3l9v.cif.gz | 241.6 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3l9v.ent.gz pdb3l9v.ent.gz | 207.1 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3l9v.json.gz 3l9v.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/l9/3l9v https://data.pdbj.org/pub/pdb/validation_reports/l9/3l9v ftp://data.pdbj.org/pub/pdb/validation_reports/l9/3l9v ftp://data.pdbj.org/pub/pdb/validation_reports/l9/3l9v | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 4 | 
| ||||||||
| 5 | 
| ||||||||
| Unit cell |
|
- Components
Components
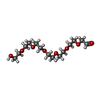
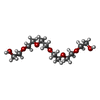
| #1: Protein | Mass: 21480.438 Da / Num. of mol.: 5 / Fragment: UNP residues 32-217 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Salmonella enterica subsp. enterica serovar Typhimurium (bacteria) Salmonella enterica subsp. enterica serovar Typhimurium (bacteria)Strain: SL1344 / Gene: PSLT011, srgA / Plasmid: pETLIC / Production host:   Escherichia coli (E. coli) / Strain (production host): Bl21(de3)/plyss Escherichia coli (E. coli) / Strain (production host): Bl21(de3)/plyssReferences: UniProt: Q04815*PLUS,  protein disulfide-isomerase protein disulfide-isomerase#2: Chemical | ChemComp-PE8 / |  Polyethylene glycol Polyethylene glycol#3: Chemical | #4: Chemical | ChemComp-P6G / |  Polyethylene glycol Polyethylene glycol#5: Water | ChemComp-HOH / |  Water WaterSequence details | THE SEQUENCE OF THE ENTITY 100% MATCHES WITH DATABASE UNIPROTKB/SWISS-PROT Q04612 (ORF3_HEVMY), UNP ...THE SEQUENCE OF THE ENTITY 100% MATCHES WITH DATABASE UNIPROTKB/SWISS-PROT Q04612 (ORF3_HEVMY), UNP RESIDUES 32-217, BUT HAS THE DIFFERENT STRAIN OF SOURCE. THE N-TERMINAL RESIDUES SER-ASN-ALA BELONG TO EXPRESSION | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.01 Å3/Da / Density % sol: 59.08 % |
|---|---|
Crystal grow | Temperature: 293 K / Method: vapor diffusion, hanging drop / pH: 7 Details: 1.45M sodium malonate, 0.5% (w/v) Jeffamine ED-2001, 100mM HEPES pH 7, VAPOR DIFFUSION, HANGING DROP, temperature 293K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Australian Synchrotron Australian Synchrotron  / Beamline: MX1 / Wavelength: 0.956661 Å / Beamline: MX1 / Wavelength: 0.956661 Å |
| Detector | Type: ADSC QUANTUM 210r / Detector: CCD / Date: Nov 28, 2008 / Details: Mirrors |
| Radiation | Monochromator: Double Si with sagittaly bent second crystal / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength : 0.956661 Å / Relative weight: 1 : 0.956661 Å / Relative weight: 1 |
| Reflection | Resolution: 2.15→50 Å / Num. all: 67898 / Num. obs: 67898 / % possible obs: 98.1 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / Redundancy: 15.5 % / Biso Wilson estimate: 38.11 Å2 / Rmerge(I) obs: 0.08 / Χ2: 1.065 / Net I/σ(I): 15.3 |
| Reflection shell | Resolution: 2.15→2.19 Å / Redundancy: 15.6 % / Rmerge(I) obs: 0.48 / Mean I/σ(I) obs: 5.63 / Num. unique all: 3314 / Χ2: 1.1 / % possible all: 97.2 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD / Resolution: 2.151→36.477 Å / Occupancy max: 1 / Occupancy min: 0 / FOM work R set: 0.799 / SU ML: 0.34 / σ(F): 1.34 / Stereochemistry target values: ML SAD / Resolution: 2.151→36.477 Å / Occupancy max: 1 / Occupancy min: 0 / FOM work R set: 0.799 / SU ML: 0.34 / σ(F): 1.34 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL / Bsol: 82.446 Å2 / ksol: 0.388 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 183.54 Å2 / Biso mean: 48.594 Å2 / Biso min: 12.73 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.151→36.477 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 10
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller




















 PDBj
PDBj