+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1jtb | ||||||
|---|---|---|---|---|---|---|---|
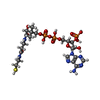
| タイトル | LIPID TRANSFER PROTEIN COMPLEXED WITH PALMITOYL COENZYME A, NMR, 16 STRUCTURES | ||||||
 要素 要素 | LIPID TRANSFER PROTEIN Plant lipid transfer proteins Plant lipid transfer proteins | ||||||
 キーワード キーワード | LIPID TRANSPORT /  LIPID TRANSFER PROTEIN LIPID TRANSFER PROTEIN | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |   Hordeum vulgare (オオムギ) Hordeum vulgare (オオムギ) | ||||||
| 手法 |  溶液NMR 溶液NMR | ||||||
 データ登録者 データ登録者 | Lerche, M.H. / Kragelund, B.B. / Bech, L.M. / Poulsen, F.M. | ||||||
 引用 引用 |  ジャーナル: Structure / 年: 1997 ジャーナル: Structure / 年: 1997タイトル: Barley lipid-transfer protein complexed with palmitoyl CoA: the structure reveals a hydrophobic binding site that can expand to fit both large and small lipid-like ligands. 著者: Lerche, M.H. / Kragelund, B.B. / Bech, L.M. / Poulsen, F.M. #1:  ジャーナル: Protein Sci. / 年: 1996 ジャーナル: Protein Sci. / 年: 1996タイトル: Structure in Solution of a Four-Helix Lipid Binding Protein 著者: Heinemann, B. / Andersen, K.V. / Nielsen, P.R. / Bech, L.M. / Poulsen, F.M. #2:  ジャーナル: Structure / 年: 1995 ジャーナル: Structure / 年: 1995タイトル: High-Resolution Crystal Structure of the Non-Specific Lipid-Transfer Protein from Maize Seedlings 著者: Shin, D.H. / Lee, J.Y. / Hwang, K.Y. / Kim, K.K. / Suh, S.W. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1jtb.cif.gz 1jtb.cif.gz | 456.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1jtb.ent.gz pdb1jtb.ent.gz | 380 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1jtb.json.gz 1jtb.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/jt/1jtb https://data.pdbj.org/pub/pdb/validation_reports/jt/1jtb ftp://data.pdbj.org/pub/pdb/validation_reports/jt/1jtb ftp://data.pdbj.org/pub/pdb/validation_reports/jt/1jtb | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質 |  Plant lipid transfer proteins / LTP Plant lipid transfer proteins / LTP分子量: 9704.965 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)   Hordeum vulgare (オオムギ) / 器官: SEEDS Hordeum vulgare (オオムギ) / 器官: SEEDS 種子 / 参照: UniProt: P07597 種子 / 参照: UniProt: P07597 |
|---|---|
| #2: 化合物 | ChemComp-COA /  補酵素A 補酵素A |
| #3: 化合物 | ChemComp-PLM /  パルミチン酸 パルミチン酸 |
-実験情報
-実験
| 実験 | 手法:  溶液NMR 溶液NMR |
|---|
- 試料調製
試料調製
| 試料状態 | pH: 7.2 / 温度: 310 K |
|---|---|
結晶化 | *PLUS 手法: その他 / 詳細: NMR |
- 解析
解析
| ソフトウェア |
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR software | 名称:  X-PLOR / バージョン: 3.1 / 開発者: BRUNGER / 分類: 精密化 X-PLOR / バージョン: 3.1 / 開発者: BRUNGER / 分類: 精密化 | ||||||||||||
| NMRアンサンブル | 計算したコンフォーマーの数: 20 / 登録したコンフォーマーの数: 16 |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj