+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24745 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM map of KIFBP | ||||||||||||||||||
 マップデータ マップデータ | |||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | kinesin regulation protein /  MOTOR PROTEIN (モータータンパク質) MOTOR PROTEIN (モータータンパク質) | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 central nervous system projection neuron axonogenesis / mitochondrial transport / central nervous system projection neuron axonogenesis / mitochondrial transport /  kinesin binding / neuron projection maintenance / microtubule cytoskeleton organization / in utero embryonic development / kinesin binding / neuron projection maintenance / microtubule cytoskeleton organization / in utero embryonic development /  細胞骨格 / 細胞骨格 /  ミトコンドリア ミトコンドリア類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.6 Å クライオ電子顕微鏡法 / 解像度: 4.6 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Tan Z / Solon AL | ||||||||||||||||||
| 資金援助 |  米国, 5件 米国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2021 ジャーナル: Sci Adv / 年: 2021タイトル: Kinesin-binding protein remodels the kinesin motor to prevent microtubule binding. 著者: April L Solon / Zhenyu Tan / Katherine L Schutt / Lauren Jepsen / Sarah E Haynes / Alexey I Nesvizhskii / David Sept / Jason Stumpff / Ryoma Ohi / Michael A Cianfrocco /  要旨: Kinesins are regulated in space and time to ensure activation only in the presence of cargo. Kinesin-binding protein (KIFBP), which is mutated in Goldberg-Shprintzen syndrome, binds to and inhibits ...Kinesins are regulated in space and time to ensure activation only in the presence of cargo. Kinesin-binding protein (KIFBP), which is mutated in Goldberg-Shprintzen syndrome, binds to and inhibits the catalytic motor heads of 8 of 45 kinesin superfamily members, but the mechanism remains poorly defined. Here, we used cryo–electron microscopy and cross-linking mass spectrometry to determine high-resolution structures of KIFBP alone and in complex with two mitotic kinesins, revealing structural remodeling of kinesin by KIFBP. We find that KIFBP remodels kinesin motors and blocks microtubule binding (i) via allosteric changes to kinesin and (ii) by sterically blocking access to the microtubule. We identified two regions of KIFBP necessary for kinesin binding and cellular regulation during mitosis. Together, this work further elucidates the molecular mechanism of KIFBP-mediated kinesin inhibition and supports a model in which structural rearrangement of kinesin motor domains by KIFBP abrogates motor protein activity. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24745.map.gz emd_24745.map.gz | 52.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24745-v30.xml emd-24745-v30.xml emd-24745.xml emd-24745.xml | 17.8 KB 17.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_24745.png emd_24745.png | 37 KB | ||
| マスクデータ |  emd_24745_msk_1.map emd_24745_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-24745.cif.gz emd-24745.cif.gz | 5.6 KB | ||
| その他 |  emd_24745_additional_1.map.gz emd_24745_additional_1.map.gz emd_24745_half_map_1.map.gz emd_24745_half_map_1.map.gz emd_24745_half_map_2.map.gz emd_24745_half_map_2.map.gz | 51.2 MB 95.6 MB 95.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24745 http://ftp.pdbj.org/pub/emdb/structures/EMD-24745 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24745 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24745 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24745.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24745.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.98 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_24745_msk_1.map emd_24745_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
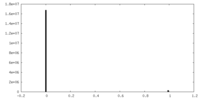
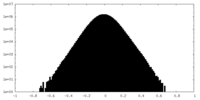
| 密度ヒストグラム |
-追加マップ: unsharpened Map
| ファイル | emd_24745_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | unsharpened Map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
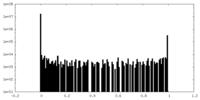
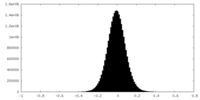
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_24745_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
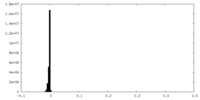
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_24745_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
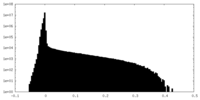
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : KIFBP molecule
| 全体 | 名称: KIFBP molecule |
|---|---|
| 要素 |
|
-超分子 #1: KIFBP molecule
| 超分子 | 名称: KIFBP molecule / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: KIF-binding protein
| 分子 | 名称: KIF-binding protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 71.913945 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MANVPWAEVC EKFQAALALS RVELHKNPEK EPYKSKYSAR ALLEEVKALL GPAPEDEDER PEAEDGPGAG DHALGLPAEV VEPEGPVAQ RAVRLAVIEF HLGVNHIDTE ELSAGEEHLV KCLRLLRRYR LSHDCISLCI QAQNNLGILW SEREEIETAQ A YLESSEAL ...文字列: MANVPWAEVC EKFQAALALS RVELHKNPEK EPYKSKYSAR ALLEEVKALL GPAPEDEDER PEAEDGPGAG DHALGLPAEV VEPEGPVAQ RAVRLAVIEF HLGVNHIDTE ELSAGEEHLV KCLRLLRRYR LSHDCISLCI QAQNNLGILW SEREEIETAQ A YLESSEAL YNQYMKEVGS PPLDPTERFL PEEEKLTEQE RSKRFEKVYT HNLYYLAQVY QHLEMFEKAA HYCHSTLKRQ LE HNAYHPI EWAINAATLS QFYINKLCFM EARHCLSAAN VIFGQTGKIS ATEDTPEAEG EVPELYHQRK GEIARCWIKY CLT LMQNAQ LSMQDNIGEL DLDKQSELRA LRKKELDEEE SIRKKAVQFG TGELCDAISA VEEKVSYLRP LDFEEARELF LLGQ HYVFE AKEFFQIDGY VTDHIEVVQD HSALFKVLAF FETDMERRCK MHKRRIAMLE PLTVDLNPQY YLLVNRQIQF EIAHA YYDM MDLKVAIADR LRDPDSHIVK KINNLNKSAL KYYQLFLDSL RDPNKVFPEH IGEDVLRPAM LAKFRVARLY GKIITA DPK KELENLATSL EHYKFIVDYC EKHPEAAQEI EVELELSKEM VSLLPTKMER FRTKMALT UniProtKB: KIF-binding protein |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 7.7 |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS GLACIOS |
|---|---|
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 65.0 e/Å2 |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC / 使用した粒子像数: 154176 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-7ryq: |
 ムービー
ムービー コントローラー
コントローラー




















 Z
Z Y
Y X
X