+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0077 | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Narrow Pick Filament from Pick's disease brain | |||||||||||||||||||||
 マップデータ マップデータ | ||||||||||||||||||||||
 試料 試料 |
| |||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報plus-end-directed organelle transport along microtubule /  軸索輸送 / histone-dependent DNA binding / 軸索輸送 / histone-dependent DNA binding /  neurofibrillary tangle assembly / positive regulation of diacylglycerol kinase activity / negative regulation of establishment of protein localization to mitochondrion / neurofibrillary tangle assembly / positive regulation of diacylglycerol kinase activity / negative regulation of establishment of protein localization to mitochondrion /  neurofibrillary tangle / positive regulation of protein localization to synapse / microtubule lateral binding / neurofibrillary tangle / positive regulation of protein localization to synapse / microtubule lateral binding /  tubulin complex ...plus-end-directed organelle transport along microtubule / tubulin complex ...plus-end-directed organelle transport along microtubule /  軸索輸送 / histone-dependent DNA binding / 軸索輸送 / histone-dependent DNA binding /  neurofibrillary tangle assembly / positive regulation of diacylglycerol kinase activity / negative regulation of establishment of protein localization to mitochondrion / neurofibrillary tangle assembly / positive regulation of diacylglycerol kinase activity / negative regulation of establishment of protein localization to mitochondrion /  neurofibrillary tangle / positive regulation of protein localization to synapse / microtubule lateral binding / neurofibrillary tangle / positive regulation of protein localization to synapse / microtubule lateral binding /  tubulin complex / tubulin complex /  phosphatidylinositol bisphosphate binding / main axon / regulation of long-term synaptic depression / negative regulation of kinase activity / negative regulation of tubulin deacetylation / generation of neurons / regulation of chromosome organization / positive regulation of protein localization / rRNA metabolic process / internal protein amino acid acetylation / phosphatidylinositol bisphosphate binding / main axon / regulation of long-term synaptic depression / negative regulation of kinase activity / negative regulation of tubulin deacetylation / generation of neurons / regulation of chromosome organization / positive regulation of protein localization / rRNA metabolic process / internal protein amino acid acetylation /  regulation of mitochondrial fission / intracellular distribution of mitochondria / axonal transport of mitochondrion / axon development / regulation of mitochondrial fission / intracellular distribution of mitochondria / axonal transport of mitochondrion / axon development /  central nervous system neuron development / central nervous system neuron development /  regulation of microtubule polymerization / regulation of microtubule polymerization /  微小管 / minor groove of adenine-thymine-rich DNA binding / 微小管 / minor groove of adenine-thymine-rich DNA binding /  lipoprotein particle binding / lipoprotein particle binding /  dynactin binding / glial cell projection / negative regulation of mitochondrial membrane potential / dynactin binding / glial cell projection / negative regulation of mitochondrial membrane potential /  apolipoprotein binding / protein polymerization / negative regulation of mitochondrial fission / apolipoprotein binding / protein polymerization / negative regulation of mitochondrial fission /  axolemma / Caspase-mediated cleavage of cytoskeletal proteins / regulation of microtubule polymerization or depolymerization / positive regulation of axon extension / Activation of AMPK downstream of NMDARs / regulation of microtubule cytoskeleton organization / supramolecular fiber organization / axolemma / Caspase-mediated cleavage of cytoskeletal proteins / regulation of microtubule polymerization or depolymerization / positive regulation of axon extension / Activation of AMPK downstream of NMDARs / regulation of microtubule cytoskeleton organization / supramolecular fiber organization /  stress granule assembly / regulation of cellular response to heat / cytoplasmic microtubule organization / regulation of calcium-mediated signaling / positive regulation of microtubule polymerization / axon cytoplasm / somatodendritic compartment / cellular response to brain-derived neurotrophic factor stimulus / stress granule assembly / regulation of cellular response to heat / cytoplasmic microtubule organization / regulation of calcium-mediated signaling / positive regulation of microtubule polymerization / axon cytoplasm / somatodendritic compartment / cellular response to brain-derived neurotrophic factor stimulus /  synapse assembly / synapse assembly /  phosphatidylinositol binding / nuclear periphery / cellular response to nerve growth factor stimulus / positive regulation of superoxide anion generation / protein phosphatase 2A binding / phosphatidylinositol binding / nuclear periphery / cellular response to nerve growth factor stimulus / positive regulation of superoxide anion generation / protein phosphatase 2A binding /  regulation of autophagy / astrocyte activation / response to lead ion / synapse organization / microglial cell activation / regulation of autophagy / astrocyte activation / response to lead ion / synapse organization / microglial cell activation /  Hsp90 protein binding / Hsp90 protein binding /  regulation of synaptic plasticity / PKR-mediated signaling / protein homooligomerization / regulation of synaptic plasticity / PKR-mediated signaling / protein homooligomerization /  記憶 / cellular response to reactive oxygen species / microtubule cytoskeleton organization / 記憶 / cellular response to reactive oxygen species / microtubule cytoskeleton organization /  SH3 domain binding / cytoplasmic ribonucleoprotein granule / activation of cysteine-type endopeptidase activity involved in apoptotic process / neuron projection development / microtubule cytoskeleton / cell-cell signaling / protein-macromolecule adaptor activity / cellular response to heat / SH3 domain binding / cytoplasmic ribonucleoprotein granule / activation of cysteine-type endopeptidase activity involved in apoptotic process / neuron projection development / microtubule cytoskeleton / cell-cell signaling / protein-macromolecule adaptor activity / cellular response to heat /  actin binding / actin binding /  single-stranded DNA binding / single-stranded DNA binding /  cell body / protein-folding chaperone binding / cell body / protein-folding chaperone binding /  成長円錐 / 成長円錐 /  microtubule binding / microtubule binding /  double-stranded DNA binding / double-stranded DNA binding /  微小管 / sequence-specific DNA binding / amyloid fibril formation / 微小管 / sequence-specific DNA binding / amyloid fibril formation /  樹状突起スパイン / learning or memory / nuclear speck / neuron projection / 樹状突起スパイン / learning or memory / nuclear speck / neuron projection /  脂質ラフト / 脂質ラフト /  神経繊維 / negative regulation of gene expression / neuronal cell body / DNA damage response / 神経繊維 / negative regulation of gene expression / neuronal cell body / DNA damage response /  樹状突起 / 樹状突起 /  protein kinase binding / protein kinase binding /  enzyme binding / enzyme binding /  ミトコンドリア / ミトコンドリア /  DNA binding DNA binding類似検索 - 分子機能 | |||||||||||||||||||||
| 生物種 |   Homo sapiens (ヒト) / Homo sapiens (ヒト) /   Human (ヒト) Human (ヒト) | |||||||||||||||||||||
| 手法 | らせん対称体再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.2 Å クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||||||||||||||
 データ登録者 データ登録者 | Falcon B / Zhang W / Murzin AG / Murshudov G / Garringer HJ / Vidal R / Crowther RA / Ghetti B / Scheres SHW / Goedert M | |||||||||||||||||||||
| 資金援助 |  英国, 英国,  米国, 6件 米国, 6件
| |||||||||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2018 ジャーナル: Nature / 年: 2018タイトル: Structures of filaments from Pick's disease reveal a novel tau protein fold. 著者: Benjamin Falcon / Wenjuan Zhang / Alexey G Murzin / Garib Murshudov / Holly J Garringer / Ruben Vidal / R Anthony Crowther / Bernardino Ghetti / Sjors H W Scheres / Michel Goedert /   要旨: The ordered assembly of tau protein into abnormal filamentous inclusions underlies many human neurodegenerative diseases. Tau assemblies seem to spread through specific neural networks in each ...The ordered assembly of tau protein into abnormal filamentous inclusions underlies many human neurodegenerative diseases. Tau assemblies seem to spread through specific neural networks in each disease, with short filaments having the greatest seeding activity. The abundance of tau inclusions strongly correlates with disease symptoms. Six tau isoforms are expressed in the normal adult human brain-three isoforms with four microtubule-binding repeats each (4R tau) and three isoforms that lack the second repeat (3R tau). In various diseases, tau filaments can be composed of either 3R or 4R tau, or of both. Tau filaments have distinct cellular and neuroanatomical distributions, with morphological and biochemical differences suggesting that they may be able to adopt disease-specific molecular conformations. Such conformers may give rise to different neuropathological phenotypes, reminiscent of prion strains. However, the underlying structures are not known. Using electron cryo-microscopy, we recently reported the structures of tau filaments from patients with Alzheimer's disease, which contain both 3R and 4R tau. Here we determine the structures of tau filaments from patients with Pick's disease, a neurodegenerative disorder characterized by frontotemporal dementia. The filaments consist of residues Lys254-Phe378 of 3R tau, which are folded differently from the tau filaments in Alzheimer's disease, establishing the existence of conformers of assembled tau. The observed tau fold in the filaments of patients with Pick's disease explains the selective incorporation of 3R tau in Pick bodies, and the differences in phosphorylation relative to the tau filaments of Alzheimer's disease. Our findings show how tau can adopt distinct folds in the human brain in different diseases, an essential step for understanding the formation and propagation of molecular conformers. | |||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0077.map.gz emd_0077.map.gz | 201.8 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0077-v30.xml emd-0077-v30.xml emd-0077.xml emd-0077.xml | 17.9 KB 17.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
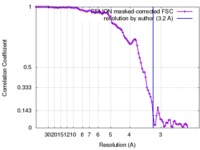
| FSC (解像度算出) |  emd_0077_fsc.xml emd_0077_fsc.xml | 9.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_0077.png emd_0077.png | 119.7 KB | ||
| マスクデータ |  emd_0077_msk_1.map emd_0077_msk_1.map | 75.1 MB |  マスクマップ マスクマップ | |
| その他 |  emd_0077_half_map_1.map.gz emd_0077_half_map_1.map.gz emd_0077_half_map_2.map.gz emd_0077_half_map_2.map.gz | 58.4 MB 58.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0077 http://ftp.pdbj.org/pub/emdb/structures/EMD-0077 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0077 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0077 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0077.map.gz / 形式: CCP4 / 大きさ: 75.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0077.map.gz / 形式: CCP4 / 大きさ: 75.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.15 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
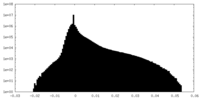
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_0077_msk_1.map emd_0077_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
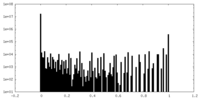
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_0077_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
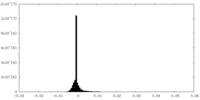
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_0077_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
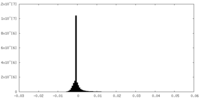
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tau filaments extracted from the frontotemporal cortex of a patie...
| 全体 | 名称: Tau filaments extracted from the frontotemporal cortex of a patient with Pick's disease |
|---|---|
| 要素 |
|
-超分子 #1: Tau filaments extracted from the frontotemporal cortex of a patie...
| 超分子 | 名称: Tau filaments extracted from the frontotemporal cortex of a patient with Pick's disease タイプ: tissue / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) / 器官: Brain / 組織: Frontotemporal cortex Homo sapiens (ヒト) / 器官: Brain / 組織: Frontotemporal cortex |
-分子 #1: Microtubule-associated protein tau
| 分子 | 名称: Microtubule-associated protein tau / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human (ヒト) / 器官: Brain / 組織: Frontotemporal cortex Human (ヒト) / 器官: Brain / 組織: Frontotemporal cortex |
| 分子量 | 理論値: 10.135665 KDa |
| 配列 | 文字列: KNVKSKIGST ENLKHQPGGG KVQIVYKPVD LSKVTSKCGS LGNIHHKPGG GQVEVKSEKL DFKDRVQSKI GSLDNITHVP GGGNKKIET HKLTF |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | tissue |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV | ||||||||||||
| 詳細 | Dispersed filaments |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm Bright-field microscopy / Cs: 2.7 mm最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 1.7 µm |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS |
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 平均電子線量: 1.06 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 詳細 | Fourier-space refinement of the complete atomic model against the narrow Pick filament map was performed in REFMAC. A stack of three consecutive monomers was refined to preserve nearest-neighbour interactions for the middle chain. |
|---|---|
| 精密化 | 空間: RECIPROCAL / プロトコル: AB INITIO MODEL / 温度因子: 57 / 当てはまり具合の基準: Fourier shell correlation |
| 得られたモデル |  PDB-6gx5: |
 ムービー
ムービー コントローラー
コントローラー

















 Z
Z Y
Y X
X