+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
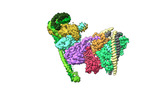
| タイトル | Structure of the human CCAN bound to alpha satellite DNA | ||||||||||||
 マップデータ マップデータ | Unsharpened map from Relion Refine3D | ||||||||||||
 試料 試料 |
| ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of protein localization to kinetochore / Mis6-Sim4 complex / FANCM-MHF complex / centromere complex assembly / kinetochore organization / metaphase chromosome alignment / Fanconi anaemia nuclear complex / inner kinetochore /  kinetochore binding / kinetochore binding /  sex differentiation ...positive regulation of protein localization to kinetochore / Mis6-Sim4 complex / FANCM-MHF complex / centromere complex assembly / kinetochore organization / metaphase chromosome alignment / Fanconi anaemia nuclear complex / inner kinetochore / sex differentiation ...positive regulation of protein localization to kinetochore / Mis6-Sim4 complex / FANCM-MHF complex / centromere complex assembly / kinetochore organization / metaphase chromosome alignment / Fanconi anaemia nuclear complex / inner kinetochore /  kinetochore binding / kinetochore binding /  sex differentiation / CENP-A containing chromatin assembly / resolution of meiotic recombination intermediates / chordate embryonic development / negative regulation of epithelial cell apoptotic process / sex differentiation / CENP-A containing chromatin assembly / resolution of meiotic recombination intermediates / chordate embryonic development / negative regulation of epithelial cell apoptotic process /  kinetochore assembly / replication fork processing / mitotic sister chromatid segregation / kinetochore assembly / replication fork processing / mitotic sister chromatid segregation /  chromosome, centromeric region / centriolar satellite / chromosome organization / Amplification of signal from unattached kinetochores via a MAD2 inhibitory signal / interstrand cross-link repair / Mitotic Prometaphase / EML4 and NUDC in mitotic spindle formation / Deposition of new CENPA-containing nucleosomes at the centromere / Resolution of Sister Chromatid Cohesion / NRIF signals cell death from the nucleus / mitotic spindle organization / positive regulation of protein ubiquitination / positive regulation of epithelial cell proliferation / chromosome, centromeric region / centriolar satellite / chromosome organization / Amplification of signal from unattached kinetochores via a MAD2 inhibitory signal / interstrand cross-link repair / Mitotic Prometaphase / EML4 and NUDC in mitotic spindle formation / Deposition of new CENPA-containing nucleosomes at the centromere / Resolution of Sister Chromatid Cohesion / NRIF signals cell death from the nucleus / mitotic spindle organization / positive regulation of protein ubiquitination / positive regulation of epithelial cell proliferation /  chromosome segregation / RHO GTPases Activate Formins / Fanconi Anemia Pathway / PKR-mediated signaling / chromosome segregation / RHO GTPases Activate Formins / Fanconi Anemia Pathway / PKR-mediated signaling /  動原体 / 動原体 /  nuclear matrix / Separation of Sister Chromatids / nuclear matrix / Separation of Sister Chromatids /  マイクロフィラメント / mitotic cell cycle / マイクロフィラメント / mitotic cell cycle /  染色体 / 染色体 /  nuclear body / nuclear body /  細胞接着 / protein heterodimerization activity / 細胞接着 / protein heterodimerization activity /  細胞分裂 / 細胞分裂 /  DNA修復 / apoptotic process / DNA damage response / DNA修復 / apoptotic process / DNA damage response /  chromatin binding / chromatin binding /  クロマチン / クロマチン /  核小体 / regulation of DNA-templated transcription / 核小体 / regulation of DNA-templated transcription /  シグナル伝達 / シグナル伝達 /  DNA binding / DNA binding /  核質 / 核質 /  生体膜 / 生体膜 /  細胞核 / 細胞核 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
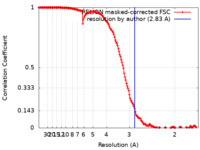
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.83 Å クライオ電子顕微鏡法 / 解像度: 2.83 Å | ||||||||||||
 データ登録者 データ登録者 | Yatskevich S / Muir KW / Bellini D / Zhang Z / Yang J / Tischer T / Predin M / Dendooven T / McLaughlin SH / Barford D | ||||||||||||
| 資金援助 |  英国, 英国,  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Science / 年: 2022 ジャーナル: Science / 年: 2022タイトル: Structure of the human inner kinetochore bound to a centromeric CENP-A nucleosome. 著者: Stanislau Yatskevich / Kyle W Muir / Dom Bellini / Ziguo Zhang / Jing Yang / Thomas Tischer / Masa Predin / Tom Dendooven / Stephen H McLaughlin / David Barford /  要旨: Kinetochores assemble onto specialized centromeric CENP-A (centromere protein A) nucleosomes (CENP-A) to mediate attachments between chromosomes and the mitotic spindle. We describe cryo-electron ...Kinetochores assemble onto specialized centromeric CENP-A (centromere protein A) nucleosomes (CENP-A) to mediate attachments between chromosomes and the mitotic spindle. We describe cryo-electron microscopy structures of the human inner kinetochore constitutive centromere associated network (CCAN) complex bound to CENP-A reconstituted onto α-satellite DNA. CCAN forms edge-on contacts with CENP-A, and a linker DNA segment of the α-satellite repeat emerges from the fully wrapped end of the nucleosome to thread through the central CENP-LN channel that tightly grips the DNA. The CENP-TWSX histone-fold module further augments DNA binding and partially wraps the linker DNA in a manner reminiscent of canonical nucleosomes. Our study suggests that the topological entrapment of the linker DNA by CCAN provides a robust mechanism by which kinetochores withstand both pushing and pulling forces exerted by the mitotic spindle. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14336.map.gz emd_14336.map.gz | 245.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14336-v30.xml emd-14336-v30.xml emd-14336.xml emd-14336.xml | 31.3 KB 31.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14336_fsc.xml emd_14336_fsc.xml | 15.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14336.png emd_14336.png | 90.8 KB | ||
| その他 |  emd_14336_additional_1.map.gz emd_14336_additional_1.map.gz | 18 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14336 http://ftp.pdbj.org/pub/emdb/structures/EMD-14336 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14336 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14336 | HTTPS FTP |
-関連構造データ
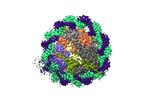
| 関連構造データ |  7r5sMC  7pb4C  7pb8C  7piiC  7pknC 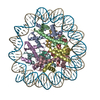 7r5rC  7r5vC  7ywxC  7yyhC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14336.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14336.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map from Relion Refine3D | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.853 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Sharpened map from Relion PostProcess
| ファイル | emd_14336_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map from Relion PostProcess | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
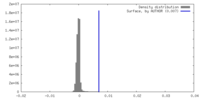
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Human CCAN complex with bound alpha-satellite DNA
+超分子 #1: Human CCAN complex with bound alpha-satellite DNA
+分子 #1: Centromere protein H
+分子 #2: Centromere protein I
+分子 #4: Centromere protein K
+分子 #5: Centromere protein L
+分子 #6: Centromere protein M
+分子 #7: Centromere protein N
+分子 #8: Centromere protein O
+分子 #9: Centromere protein P
+分子 #10: Centromere protein Q
+分子 #11: Centromere protein U
+分子 #12: Centromere protein R
+分子 #13: Centromere protein T
+分子 #14: Centromere protein W
+分子 #15: Centromere protein S
+分子 #16: Centromere protein X
+分子 #3: DNA (66-MER)
+分子 #17: DNA (66-MER)
+分子 #18: water
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.5 µm Bright-field microscopy / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.5 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)