+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7zbd | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | HaloTag with TRaQ-G ligand | ||||||
 要素 要素 | Haloalkane dehalogenase | ||||||
 キーワード キーワード |  HYDROLASE (加水分解酵素) / HYDROLASE (加水分解酵素) /  HaloTag / HaloTag /  haloalkane dehalogenase / silicon rhodamine haloalkane dehalogenase / silicon rhodamine | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Rhodococcus sp. (バクテリア) Rhodococcus sp. (バクテリア) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.68 Å 分子置換 / 解像度: 1.68 Å | ||||||
 データ登録者 データ登録者 | Emmert, S. / Rivera-Fuentes, P. / Pojer, F. / Lau, K. | ||||||
| 資金援助 |  スイス, 1件 スイス, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat.Chem. / 年: 2023 ジャーナル: Nat.Chem. / 年: 2023タイトル: A locally activatable sensor for robust quantification of organellar glutathione. 著者: Emmert, S. / Quargnali, G. / Thallmair, S. / Rivera-Fuentes, P. #1:  ジャーナル: Biorxiv / 年: 2022 ジャーナル: Biorxiv / 年: 2022タイトル: A Locally Activatable Sensor for Robust Quantification of Organellar Glutathione 著者: Hubner, S. / Quargnali, G. / Thallmair, S. / Rivera-Fuentes, P. #2: ジャーナル: Acta Crystallogr.,Sect.D / 年: 2012 タイトル: Towards automated crystallographic structure refinement with phenix.refine. 著者: Afonine, P.V. / Grosse-Kunstleve, R.W. / Echols, N. / Headd, J.J. / Moriarty, N.W. / Mustyakimov, M. / Terwilliger, T.C. / Urzhumtsev, A. / Zwart, P.H. / Adams, P.D. #3: ジャーナル: Acta Crystallogr D Struct Biol / 年: 2019 タイトル: Macromolecular structure determination using X-rays, neutrons and electrons: recent developments in Phenix. 著者: Dorothee Liebschner / Pavel V Afonine / Matthew L Baker / Gábor Bunkóczi / Vincent B Chen / Tristan I Croll / Bradley Hintze / Li Wei Hung / Swati Jain / Airlie J McCoy / Nigel W Moriarty / ...著者: Dorothee Liebschner / Pavel V Afonine / Matthew L Baker / Gábor Bunkóczi / Vincent B Chen / Tristan I Croll / Bradley Hintze / Li Wei Hung / Swati Jain / Airlie J McCoy / Nigel W Moriarty / Robert D Oeffner / Billy K Poon / Michael G Prisant / Randy J Read / Jane S Richardson / David C Richardson / Massimo D Sammito / Oleg V Sobolev / Duncan H Stockwell / Thomas C Terwilliger / Alexandre G Urzhumtsev / Lizbeth L Videau / Christopher J Williams / Paul D Adams /    要旨: Diffraction (X-ray, neutron and electron) and electron cryo-microscopy are powerful methods to determine three-dimensional macromolecular structures, which are required to understand biological ...Diffraction (X-ray, neutron and electron) and electron cryo-microscopy are powerful methods to determine three-dimensional macromolecular structures, which are required to understand biological processes and to develop new therapeutics against diseases. The overall structure-solution workflow is similar for these techniques, but nuances exist because the properties of the reduced experimental data are different. Software tools for structure determination should therefore be tailored for each method. Phenix is a comprehensive software package for macromolecular structure determination that handles data from any of these techniques. Tasks performed with Phenix include data-quality assessment, map improvement, model building, the validation/rebuilding/refinement cycle and deposition. Each tool caters to the type of experimental data. The design of Phenix emphasizes the automation of procedures, where possible, to minimize repetitive and time-consuming manual tasks, while default parameters are chosen to encourage best practice. A graphical user interface provides access to many command-line features of Phenix and streamlines the transition between programs, project tracking and re-running of previous tasks. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7zbd.cif.gz 7zbd.cif.gz | 177.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7zbd.ent.gz pdb7zbd.ent.gz | 111.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7zbd.json.gz 7zbd.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zb/7zbd https://data.pdbj.org/pub/pdb/validation_reports/zb/7zbd ftp://data.pdbj.org/pub/pdb/validation_reports/zb/7zbd ftp://data.pdbj.org/pub/pdb/validation_reports/zb/7zbd | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  7zbaC  7zbbC  6u32S S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| 2 | 
| ||||||||||||
| 単位格子 |
| ||||||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 2分子 AB
| #1: タンパク質 |  分子量: 34473.312 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)  Rhodococcus sp. (バクテリア) / 遺伝子: dhaA / 発現宿主: Rhodococcus sp. (バクテリア) / 遺伝子: dhaA / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / 参照: UniProt: P0A3G3, Escherichia coli BL21(DE3) (大腸菌) / 参照: UniProt: P0A3G3,  haloalkane dehalogenase haloalkane dehalogenase |
|---|
-非ポリマー , 5種, 440分子 
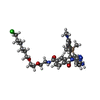







| #2: 化合物 |  グリセリン グリセリン#3: 化合物 | ChemComp-ILQ / ( | #4: 化合物 |  塩化物 塩化物#5: 化合物 | ChemComp-ILU / [ | #6: 水 | ChemComp-HOH / |  水 水 |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.15 Å3/Da / 溶媒含有率: 42.74 % |
|---|---|
結晶化 | 温度: 291 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 6 詳細: 20% v/v PEG 6000, 10% ethylene glycol, 0.1M magnesium chloride hexahydrate and 0.1M MES |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X06DA / 波長: 1 Å / ビームライン: X06DA / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M-F / 検出器: PIXEL / 日付: 2021年4月26日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 1 Å / 相対比: 1 : 1 Å / 相対比: 1 |
| 反射 | 解像度: 1.68→50 Å / Num. obs: 127898 / % possible obs: 98.4 % / 冗長度: 3 % / Biso Wilson estimate: 21.94 Å2 / CC1/2: 0.99 / Rrim(I) all: 0.12 / Net I/σ(I): 7.24 |
| 反射 シェル | 解像度: 1.68→1.79 Å / Mean I/σ(I) obs: 0.98 / Num. unique obs: 20136 / CC1/2: 0.61 / Rrim(I) all: 1.2 / % possible all: 96.2 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: 6U32 解像度: 1.68→47.75 Å / SU ML: 0.1983 / 交差検証法: FREE R-VALUE / σ(F): 1.34 / 位相誤差: 26.0217 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.1 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 27.09 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.68→47.75 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj






