+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase | ||||||||||||
 マップデータ マップデータ | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード |  Primase (DNAプライマーゼ) / Primase (DNAプライマーゼ) /  DNA polymerase (DNAポリメラーゼ) / chimeric RNA-DNA primer / RNA/DNA hybrid / DNA polymerase (DNAポリメラーゼ) / chimeric RNA-DNA primer / RNA/DNA hybrid /  DNA replication (DNA複製) / DNA replication (DNA複製) /  DNA synthesis (DNA合成) / DNA synthesis (DNA合成) /  REPLICATION (DNA複製) / TRANSFERASE-DNA-RNA complex REPLICATION (DNA複製) / TRANSFERASE-DNA-RNA complex | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報alpha DNA polymerase:primase complex / lagging strand elongation / mitotic DNA replication initiation /  DNA replication, synthesis of primer / DNA strand elongation involved in DNA replication / leading strand elongation / DNA replication initiation / DNA replication, synthesis of primer / DNA strand elongation involved in DNA replication / leading strand elongation / DNA replication initiation /  nuclear matrix / double-strand break repair via nonhomologous end joining / nuclear matrix / double-strand break repair via nonhomologous end joining /  核膜 ...alpha DNA polymerase:primase complex / lagging strand elongation / mitotic DNA replication initiation / 核膜 ...alpha DNA polymerase:primase complex / lagging strand elongation / mitotic DNA replication initiation /  DNA replication, synthesis of primer / DNA strand elongation involved in DNA replication / leading strand elongation / DNA replication initiation / DNA replication, synthesis of primer / DNA strand elongation involved in DNA replication / leading strand elongation / DNA replication initiation /  nuclear matrix / double-strand break repair via nonhomologous end joining / nuclear matrix / double-strand break repair via nonhomologous end joining /  核膜 / 核膜 /  DNA複製 / DNA複製 /  DNAポリメラーゼ / DNAポリメラーゼ /  DNA-directed DNA polymerase activity / DNA-directed DNA polymerase activity /  nucleotide binding / nucleotide binding /  chromatin binding / chromatin binding /  クロマチン / クロマチン /  核小体 / 核小体 /  DNA binding / DNA binding /  核質 / 核質 /  metal ion binding / metal ion binding /  細胞核 細胞核類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Xenopus laevis (アフリカツメガエル) / synthetic construct (人工物) Xenopus laevis (アフリカツメガエル) / synthetic construct (人工物) | ||||||||||||
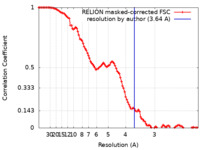
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.64 Å クライオ電子顕微鏡法 / 解像度: 3.64 Å | ||||||||||||
 データ登録者 データ登録者 | Mullins EA / Chazin WC / Eichman BF | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: bioRxiv / 年: 2023 ジャーナル: bioRxiv / 年: 2023タイトル: A mechanistic model of primer synthesis from catalytic structures of DNA polymerase α-primase. 著者: Elwood A Mullins / Lauren E Salay / Clarissa L Durie / Noah P Bradley / Jane E Jackman / Melanie D Ohi / Walter J Chazin / Brandt F Eichman 要旨: The mechanism by which polymerase α-primase (polα-primase) synthesizes chimeric RNA-DNA primers of defined length and composition, necessary for replication fidelity and genome stability, is ...The mechanism by which polymerase α-primase (polα-primase) synthesizes chimeric RNA-DNA primers of defined length and composition, necessary for replication fidelity and genome stability, is unknown. Here, we report cryo-EM structures of polα-primase in complex with primed templates representing various stages of DNA synthesis. Our data show how interaction of the primase regulatory subunit with the primer 5'-end facilitates handoff of the primer to polα and increases polα processivity, thereby regulating both RNA and DNA composition. The structures detail how flexibility within the heterotetramer enables synthesis across two active sites and provide evidence that termination of DNA synthesis is facilitated by reduction of polα and primase affinities for the varied conformations along the chimeric primer/template duplex. Together, these findings elucidate a critical catalytic step in replication initiation and provide a comprehensive model for primer synthesis by polα-primase. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_42142.map.gz emd_42142.map.gz | 80.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-42142-v30.xml emd-42142-v30.xml emd-42142.xml emd-42142.xml | 26 KB 26 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_42142_fsc.xml emd_42142_fsc.xml | 10.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_42142.png emd_42142.png | 27.6 KB | ||
| Filedesc metadata |  emd-42142.cif.gz emd-42142.cif.gz | 7.4 KB | ||
| その他 |  emd_42142_additional_1.map.gz emd_42142_additional_1.map.gz emd_42142_half_map_1.map.gz emd_42142_half_map_1.map.gz emd_42142_half_map_2.map.gz emd_42142_half_map_2.map.gz | 92.6 MB 80.9 MB 80.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-42142 http://ftp.pdbj.org/pub/emdb/structures/EMD-42142 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42142 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42142 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8ucwMC  8g99C  8g9fC  8g9lC  8g9nC  8g9oC  8ucuC  8ucvC  8v5mC  8v5nC  8v5oC  8v6gC  8v6hC  8v6iC  8v6jC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_42142.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_42142.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.09333 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Complete DNA termination subcomplex 2 of Xenopus laevis...
| ファイル | emd_42142_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase (locally sharpened) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Complete DNA termination subcomplex 2 of Xenopus laevis...
| ファイル | emd_42142_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase (half 1) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Complete DNA termination subcomplex 2 of Xenopus laevis...
| ファイル | emd_42142_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Complete DNA termination subcomplex 2 of Xenopus laevis DNA polymerase alpha-primase (half 2) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Polymerase alpha-primase with a DNA termination substrate
| 全体 | 名称: Polymerase alpha-primase with a DNA termination substrate |
|---|---|
| 要素 |
|
-超分子 #1: Polymerase alpha-primase with a DNA termination substrate
| 超分子 | 名称: Polymerase alpha-primase with a DNA termination substrate タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 詳細: Heterotetrameric protein complex with an RNA-DNA/DNA duplex |
|---|---|
| 分子量 | 理論値: 330 KDa |
-超分子 #2: Polymerase alpha
| 超分子 | 名称: Polymerase alpha / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 / 詳細: Heterodimer consisting of POLA1 and POLA2 |
|---|---|
| 由来(天然) | 生物種:  Xenopus laevis (アフリカツメガエル) Xenopus laevis (アフリカツメガエル) |
| 分子量 | 理論値: 200 KDa |
-超分子 #3: Primase
| 超分子 | 名称: Primase / タイプ: complex / ID: 3 / 親要素: 1 / 詳細: Heterodimer consisting of PRIM1 and PRIM2 |
|---|---|
| 由来(天然) | 生物種:  Xenopus laevis (アフリカツメガエル) Xenopus laevis (アフリカツメガエル) |
| 分子量 | 理論値: 110 KDa |
-超分子 #4: DNA termination substrate
| 超分子 | 名称: DNA termination substrate / タイプ: complex / ID: 4 / 親要素: 1 / 含まれる分子: #2-#3 / 詳細: RNA-DNA/DNA duplex |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 30 KDa |
-分子 #1: DNA polymerase alpha catalytic subunit
| 分子 | 名称: DNA polymerase alpha catalytic subunit / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号:  DNAポリメラーゼ DNAポリメラーゼ |
|---|---|
| 由来(天然) | 生物種:  Xenopus laevis (アフリカツメガエル) Xenopus laevis (アフリカツメガエル) |
| 分子量 | 理論値: 129.009414 KDa |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ) |
| 配列 | 文字列: SNAADGSQVF RFYWLDAYED QYSQPGVVYL FGKVWIESAD AYVSCCVSVK NIERTVYLLP RENRVQLSTG KDTGAPVSMM HVYQEFNEA VAEKYKIMKF KSKKVDKDYA FEIPDVPASS EYLEVRYSAD SPQLPQDLKG ETFSHVFGTN TSSLELFLLS R KIKGPSWL ...文字列: SNAADGSQVF RFYWLDAYED QYSQPGVVYL FGKVWIESAD AYVSCCVSVK NIERTVYLLP RENRVQLSTG KDTGAPVSMM HVYQEFNEA VAEKYKIMKF KSKKVDKDYA FEIPDVPASS EYLEVRYSAD SPQLPQDLKG ETFSHVFGTN TSSLELFLLS R KIKGPSWL EIKSPQLSSQ PMSWCKVEAV VTRPDQVSVV KDLAPPPVVV LSLSMKTVQN AKTHQNEIVA IAALVHHTFP LD KAPPQPP FQTHFCVLSK LNDCIFPYDY NEAVKQKNAN IEIALTERTL LGFFLAKIHK IDPDVIVGHD IYGFDLEVLL QRI NSCKVP FWSKIGRLRR SVMPKLGGRS GFAERNAACG RIICDIEISA KELIRCKSYH LSELVHQILK AERVVIPPEN IRNA YNDSV HLLYMLENTW IDAKFILQIM CELNVLPLAL QITNIAGNVM SRTLMGGRSE RNEYLLLHAF TENNFIVPDK PVFKK MQQT TVEDNDDMGT DQNKNKSRKK AAYAGGLVLE PKVGFYDKFI LLLDFNSLYP SIIQEYNICF TTVHREAPST QKGEDQ DEI PELPHSDLEM GILPREIRKL VERRRHVKQL MKQPDLNPDL YLQYDIRQKA LKLTANSMYG CLGFSYSRFY AKPLAAL VT HQGREILLHT KEMVQKMNLE VIYGDTDSIM INTNCNNLEE VFKLGNRVKS EINKSYKLLE IDIDGIFKSL LLLKKKKY A ALTVEPTGDG KYVTKQELKG LDIVRRDWCE LAKQAGNYVI SQILSDQPRD SIVENIQKKL TEIGENVTNG TVPITQYEI NKALTKDPQD YPDKKSLPHV HVALWINSQG GRKVKAGDTI SYVICQDGSN LSASQRAYAQ EQLQKQENLS IDTQYYLSQQ VHPVVARIC EPIDGIDSAL IAMWLGLDPS QFRAHRHYQQ DEENDALLGG PSQLTDEEKY RDCERFKFFC PKCGTENIYD N VFDGSGLQ IEPGLKRCSK PECDASPLDY VIQVHNKLLL DIRRYIKKYY SGWLVCEEKT CQNRTRRLPL SFSRNGPICQ AC SKATLRS EYPEKALYTQ LCFYRFIFDW DYALEKVVSE QERGHLKKKL FQESENQYKK LKSTVDQVLS RSGYSEVNLS KLF QTLNTI K UniProtKB: DNA polymerase alpha catalytic subunit |
-分子 #2: DNA template
| 分子 | 名称: DNA template / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 18.203668 KDa |
| 配列 | 文字列: (DT)(DG)(DT)(DA)(DT)(DG)(DT)(DA)(DT)(DG) (DT)(DA)(DT)(DG)(DT)(DC)(DG)(DC)(DT)(DA) (DC)(DA)(DA)(DT)(DC)(DG)(DC)(DT)(DA) (DA)(DG)(DT)(DT)(DC)(DA)(DC)(DG)(DC)(DA) (DG) (DT)(DA)(DT)(DC)(DC) ...文字列: (DT)(DG)(DT)(DA)(DT)(DG)(DT)(DA)(DT)(DG) (DT)(DA)(DT)(DG)(DT)(DC)(DG)(DC)(DT)(DA) (DC)(DA)(DA)(DT)(DC)(DG)(DC)(DT)(DA) (DA)(DG)(DT)(DT)(DC)(DA)(DC)(DG)(DC)(DA) (DG) (DT)(DA)(DT)(DC)(DC)(DT)(DG)(DT) (DA)(DT)(DG)(DT)(DA)(DT)(DG)(DT)(DA)(DT) (DG) |
-分子 #3: RNA-DNA/DNA primer
| 分子 | 名称: RNA-DNA/DNA primer / タイプ: other / ID: 3 / コピー数: 1 / 分類: polydeoxyribonucleotide/polyribonucleotide hybrid |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 9.249697 KDa |
| 配列 | 文字列: (GTP)GAUACUGC(DG) (DT)(DG)(DA)(DA)(DC)(DT)(DT)(DA)(DG)(DC) (DG)(DA)(DT)(DT)(DG) (DT)(DA)(DG)(DOC) |
-分子 #4: 2'-DEOXYGUANOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: 2'-DEOXYGUANOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 1 / 式: DGT |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information | 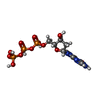 ChemComp-DGT: |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 2 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.9 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 105000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 105000 |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 22893 / 平均電子線量: 55.8 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





















 Z
Z Y
Y X
X