+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 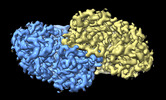 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The cryo-EM structure of GSNOR with NYY001 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Alcohol dehydrogenase class-3 /  OXIDOREDUCTASE (酸化還元酵素) OXIDOREDUCTASE (酸化還元酵素) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 formaldehyde dehydrogenase activity / formaldehyde dehydrogenase activity /  S-(ヒドロキシメチル)グルタチオンデヒドロゲナーゼ / S-(hydroxymethyl)glutathione dehydrogenase (NADP+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD(P)+) activity / fatty acid omega-oxidation / formaldehyde catabolic process / response to nitrosative stress / S-(ヒドロキシメチル)グルタチオンデヒドロゲナーゼ / S-(hydroxymethyl)glutathione dehydrogenase (NADP+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD(P)+) activity / fatty acid omega-oxidation / formaldehyde catabolic process / response to nitrosative stress /  respiratory system process / Ethanol oxidation ... respiratory system process / Ethanol oxidation ... formaldehyde dehydrogenase activity / formaldehyde dehydrogenase activity /  S-(ヒドロキシメチル)グルタチオンデヒドロゲナーゼ / S-(hydroxymethyl)glutathione dehydrogenase (NADP+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD(P)+) activity / fatty acid omega-oxidation / formaldehyde catabolic process / response to nitrosative stress / S-(ヒドロキシメチル)グルタチオンデヒドロゲナーゼ / S-(hydroxymethyl)glutathione dehydrogenase (NADP+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD+) activity / S-(hydroxymethyl)glutathione dehydrogenase (NAD(P)+) activity / fatty acid omega-oxidation / formaldehyde catabolic process / response to nitrosative stress /  respiratory system process / Ethanol oxidation / alcohol dehydrogenase (NAD+) activity, zinc-dependent / : / positive regulation of blood pressure / respiratory system process / Ethanol oxidation / alcohol dehydrogenase (NAD+) activity, zinc-dependent / : / positive regulation of blood pressure /  アルコールデヒドロゲナーゼ / アルコールデヒドロゲナーゼ /  酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; NAD又はNADPを用いる / response to redox state / retinoid metabolic process / 酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; NAD又はNADPを用いる / response to redox state / retinoid metabolic process /  fatty acid binding / response to lipopolysaccharide / fatty acid binding / response to lipopolysaccharide /  electron transfer activity / electron transfer activity /  ミトコンドリア / extracellular exosome / zinc ion binding / identical protein binding / ミトコンドリア / extracellular exosome / zinc ion binding / identical protein binding /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
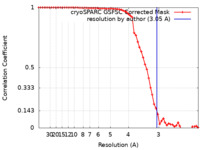
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.05 Å クライオ電子顕微鏡法 / 解像度: 3.05 Å | |||||||||
 データ登録者 データ登録者 | Xia Y / Zhang Q / Yao D / Zhao S / Xie L / Ji Y / Cao Y | |||||||||
| 資金援助 |  中国, 2件 中国, 2件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: The cryo-EM structure of GSNOR with NYY001 著者: Cao Y / Xia Y | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
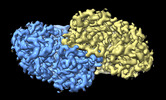
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_34282.map.gz emd_34282.map.gz | 20.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-34282-v30.xml emd-34282-v30.xml emd-34282.xml emd-34282.xml | 13.9 KB 13.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_34282_fsc.xml emd_34282_fsc.xml | 5.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_34282.png emd_34282.png | 108.7 KB | ||
| その他 |  emd_34282_half_map_1.map.gz emd_34282_half_map_1.map.gz emd_34282_half_map_2.map.gz emd_34282_half_map_2.map.gz | 20.6 MB 20.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-34282 http://ftp.pdbj.org/pub/emdb/structures/EMD-34282 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34282 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34282 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8gv3MC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_34282.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_34282.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_34282_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
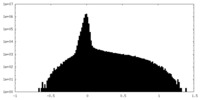
| 投影像・断面図 |
| ||||||||||||
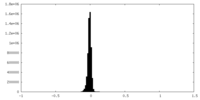
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_34282_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
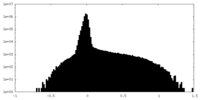
| 投影像・断面図 |
| ||||||||||||
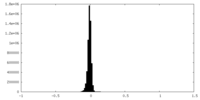
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Alcohol dehydrogenase class-3
| 全体 | 名称: Alcohol dehydrogenase class-3 |
|---|---|
| 要素 |
|
-超分子 #1: Alcohol dehydrogenase class-3
| 超分子 | 名称: Alcohol dehydrogenase class-3 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Alcohol dehydrogenase class-3
| 分子 | 名称: Alcohol dehydrogenase class-3 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO / EC番号:  アルコールデヒドロゲナーゼ アルコールデヒドロゲナーゼ |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 39.901305 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MANEVIKCKA AVAWEAGKPL SIEEIEVAPP KAHEVRIKII ATAVCHTDAY TLSGADPEGC FPVILGHEGA GIVESVGEGV TKLKAGDTV IPLYIPQCGE CKFCLNPKTN LCQKIRVTQG KGLMPDGTSR FTCKGKTILH YMGTSTFSEY TVVADISVAK I DPLAPLDK ...文字列: MANEVIKCKA AVAWEAGKPL SIEEIEVAPP KAHEVRIKII ATAVCHTDAY TLSGADPEGC FPVILGHEGA GIVESVGEGV TKLKAGDTV IPLYIPQCGE CKFCLNPKTN LCQKIRVTQG KGLMPDGTSR FTCKGKTILH YMGTSTFSEY TVVADISVAK I DPLAPLDK VCLLGCGIST GYGAAVNTAK LEPGSVCAVF GLGGVGLAVI MGCKVAGASR IIGVDINKDK FARAKEFGAT EC INPQDFS KPIQEVLIEM TDGGVDYSFE CIGNVKVMRA ALEACHKGWG VSVVVGVAAS GEEIATRPFQ LVTGRTWKGT AFG GWKSVE SVPKLVSEYM SKKIKVDEFV THNLSFDEIN KAFELMHSGK SIRTVVKIE UniProtKB: Alcohol dehydrogenase class-3 |
-分子 #2: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 2 / コピー数: 4 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #3: NICOTINAMIDE-ADENINE-DINUCLEOTIDE
| 分子 | 名称: NICOTINAMIDE-ADENINE-DINUCLEOTIDE / タイプ: ligand / ID: 3 / コピー数: 2 / 式: NAD |
|---|---|
| 分子量 | 理論値: 663.425 Da |
| Chemical component information |  ChemComp-NAD: |
-分子 #4: (4P)-4-{2-[4-(1H-imidazol-1-yl)phenyl]-5-[3-oxo-3-(2-oxo-1,3-thia...
| 分子 | 名称: (4P)-4-{2-[4-(1H-imidazol-1-yl)phenyl]-5-[3-oxo-3-(2-oxo-1,3-thiazolidin-3-yl)propyl]-1H-pyrrol-1-yl}-3-methylbenzamide タイプ: ligand / ID: 4 / コピー数: 2 / 式: WKZ |
|---|---|
| 分子量 | 理論値: 499.584 Da |
| Chemical component information | 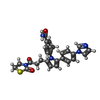 ChemComp-WKZ: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 26.0 µm / 最小 デフォーカス(公称値): 10.0 µm Bright-field microscopy / 最大 デフォーカス(公称値): 26.0 µm / 最小 デフォーカス(公称値): 10.0 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X