+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9uus | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The NuA3 histone acetyltransferase complex bound to acetyl-CoA and H3 tail | ||||||||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||||||||
 キーワード キーワード | METAL BINDING PROTEIN / DNA / nucleosome / histone acetylation | ||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報PI5P Regulates TP53 Acetylation / NuA3b histone acetyltransferase complex / NuA3a histone acetyltransferase complex / NuA3 histone acetyltransferase complex / sexual sporulation resulting in formation of a cellular spore / cupric reductase (NADH) activity / global genome nucleotide-excision repair / RNA polymerase I upstream activating factor complex / histone H3K36me3 reader activity / Condensation of Prophase Chromosomes ...PI5P Regulates TP53 Acetylation / NuA3b histone acetyltransferase complex / NuA3a histone acetyltransferase complex / NuA3 histone acetyltransferase complex / sexual sporulation resulting in formation of a cellular spore / cupric reductase (NADH) activity / global genome nucleotide-excision repair / RNA polymerase I upstream activating factor complex / histone H3K36me3 reader activity / Condensation of Prophase Chromosomes / : / : / Platelet degranulation / : / SUMOylation of transcription cofactors / Assembly of the ORC complex at the origin of replication / transcription factor TFIIF complex / mediator complex / Ino80 complex / Oxidative Stress Induced Senescence / histone H3K4me3 reader activity / silent mating-type cassette heterochromatin formation / SWI/SNF complex / transcription factor TFIID complex / RNA polymerase II general transcription initiation factor activity / histone acetyltransferase activity / RNA Polymerase I Promoter Escape / positive regulation of transcription by RNA polymerase I / NuA4 histone acetyltransferase complex / nucleolar large rRNA transcription by RNA polymerase I / Estrogen-dependent gene expression / rRNA transcription / intracellular copper ion homeostasis / subtelomeric heterochromatin formation / RNA polymerase II preinitiation complex assembly / histone acetyltransferase / CENP-A containing nucleosome / aerobic respiration / transcription coregulator activity / transcription initiation at RNA polymerase II promoter / positive regulation of transcription elongation by RNA polymerase II / structural constituent of chromatin / nucleosome / chromatin organization / histone binding / transcription by RNA polymerase II / chromosome, telomeric region / chromatin remodeling / protein heterodimerization activity / DNA repair / chromatin binding / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / DNA-templated transcription / chromatin / positive regulation of transcription by RNA polymerase II / DNA binding / zinc ion binding / nucleus / cytoplasm 類似検索 - 分子機能 | ||||||||||||||||||||||||
| 生物種 |  | ||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | ||||||||||||||||||||||||
 データ登録者 データ登録者 | Wang, Y.R. / Zhang, H.Q. | ||||||||||||||||||||||||
| 資金援助 | 1件
| ||||||||||||||||||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Apo HAT complex 著者: Wang, Y.R. / Zhang, H.Q. | ||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9uus.cif.gz 9uus.cif.gz | 268.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9uus.ent.gz pdb9uus.ent.gz | 202.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9uus.json.gz 9uus.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/uu/9uus https://data.pdbj.org/pub/pdb/validation_reports/uu/9uus ftp://data.pdbj.org/pub/pdb/validation_reports/uu/9uus ftp://data.pdbj.org/pub/pdb/validation_reports/uu/9uus | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  64517MC  9uuoC C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質・ペプチド , 1種, 1分子 H
| #1: タンパク質・ペプチド | 分子量: 2263.667 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: HHT1, YBR010W, YBR0201, HHT2, SIN2, YNL031C, N2749 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P61830 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P61830 |
|---|
-タンパク質 , 5種, 5分子 ABCED
| #2: タンパク質 | 分子量: 97723.445 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: SAS3, YBL052C, YBL0507, YBL0515 / 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P34218, histone acetyltransferase Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P34218, histone acetyltransferase |
|---|---|
| #3: タンパク質 | 分子量: 85102.188 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: NTO1, YPR031W / 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q12311 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q12311 |
| #4: タンパク質 | 分子量: 25391.049 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: YNG1, YOR064C, YOR29-15 / 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q08465 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q08465 |
| #5: タンパク質 | 分子量: 27473.154 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: TAF14, ANC1, CST10, SWP29, TAF30, TFG3, YPL129W / 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P35189 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P35189 |
| #6: タンパク質 | 分子量: 12915.704 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: EAF6, YJR082C, J1854 / 発現宿主:  Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P47128 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P47128 |
-非ポリマー , 2種, 6分子 
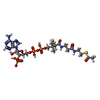

| #7: 化合物 | ChemComp-ZN / #8: 化合物 | ChemComp-ACO / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: HAT complex / タイプ: COMPLEX / Entity ID: #2, #1, #3-#4 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:  |
| 由来(組換発現) | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 緩衝液 | pH: 8 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 顕微鏡 | モデル: FEI/PHILIPS CM300FEG/T |
|---|---|
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: OTHER / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 1200 nm |
| 撮影 | 電子線照射量: 50 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 176266 / クラス平均像の数: 6 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 立体化学のターゲット値: REAL-SPACE (WEIGHTED MAP SUM AT ATOM CENTERS) | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj












