+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9duq | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | HURP(65-174) bound to GMPCPP-stabilized microtubule | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | CELL CYCLE / microtubule / nucleation / spindle / oncogene | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報mitotic chromosome movement towards spindle pole / signaling / kinetochore assembly / positive regulation of mitotic metaphase/anaphase transition / spindle pole centrosome / Microtubule-dependent trafficking of connexons from Golgi to the plasma membrane / Resolution of Sister Chromatid Cohesion / Hedgehog 'off' state / Cilium Assembly / Intraflagellar transport ...mitotic chromosome movement towards spindle pole / signaling / kinetochore assembly / positive regulation of mitotic metaphase/anaphase transition / spindle pole centrosome / Microtubule-dependent trafficking of connexons from Golgi to the plasma membrane / Resolution of Sister Chromatid Cohesion / Hedgehog 'off' state / Cilium Assembly / Intraflagellar transport / COPI-dependent Golgi-to-ER retrograde traffic / Mitotic Prometaphase / Carboxyterminal post-translational modifications of tubulin / RHOH GTPase cycle / EML4 and NUDC in mitotic spindle formation / Sealing of the nuclear envelope (NE) by ESCRT-III / Kinesins / PKR-mediated signaling / Separation of Sister Chromatids / The role of GTSE1 in G2/M progression after G2 checkpoint / Aggrephagy / RHO GTPases activate IQGAPs / RHO GTPases Activate Formins / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / MHC class II antigen presentation / Recruitment of NuMA to mitotic centrosomes / NOTCH3 Intracellular Domain Regulates Transcription / COPI-mediated anterograde transport / centrosome localization / regulation of mitotic cell cycle / mitotic spindle organization / chromosome segregation / structural constituent of cytoskeleton / microtubule cytoskeleton organization / neuron migration / mitotic spindle / mitotic cell cycle / microtubule cytoskeleton / microtubule binding / 加水分解酵素; 酸無水物に作用; GTPに作用・細胞または細胞小器官の運動に関与 / microtubule / GTPase activity / GTP binding / metal ion binding / nucleus / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.8 Å | ||||||
 データ登録者 データ登録者 | Ma, M. / Valdez, V. / Petry, S. / Zhang, R. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: HURP facilitates spindle assembly by stabilizing microtubules and working synergistically with TPX2. 著者: Venecia Alexandria Valdez / Meisheng Ma / Bernardo Gouveia / Rui Zhang / Sabine Petry /   要旨: In vertebrate spindles, most microtubules are formed via branching microtubule nucleation, whereby microtubules nucleate along the side of pre-existing microtubules. Hepatoma up-regulated protein ...In vertebrate spindles, most microtubules are formed via branching microtubule nucleation, whereby microtubules nucleate along the side of pre-existing microtubules. Hepatoma up-regulated protein (HURP) is a microtubule-associated protein that has been implicated in spindle assembly, but its mode of action is yet to be defined. In this study, we show that HURP is necessary for RanGTP-induced branching microtubule nucleation in Xenopus egg extract. Specifically, HURP stabilizes the microtubule lattice to promote microtubule formation from γ-TuRC. This function is shifted to promote branching microtubule nucleation through enhanced localization to TPX2 condensates, which form the core of the branch site on microtubules. Lastly, we provide a high-resolution cryo-EM structure of HURP on the microtubule, revealing how HURP binding stabilizes the microtubule lattice. We propose a model in which HURP stabilizes microtubules during their formation, and TPX2 preferentially enriches HURP to microtubules to promote branching microtubule nucleation and thus spindle assembly. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9duq.cif.gz 9duq.cif.gz | 1.5 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9duq.ent.gz pdb9duq.ent.gz | 1.3 MB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9duq.json.gz 9duq.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  9duq_validation.pdf.gz 9duq_validation.pdf.gz | 2.4 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  9duq_full_validation.pdf.gz 9duq_full_validation.pdf.gz | 2.5 MB | 表示 | |
| XML形式データ |  9duq_validation.xml.gz 9duq_validation.xml.gz | 219.4 KB | 表示 | |
| CIF形式データ |  9duq_validation.cif.gz 9duq_validation.cif.gz | 328.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/du/9duq https://data.pdbj.org/pub/pdb/validation_reports/du/9duq ftp://data.pdbj.org/pub/pdb/validation_reports/du/9duq ftp://data.pdbj.org/pub/pdb/validation_reports/du/9duq | HTTPS FTP |
-関連構造データ
| 関連構造データ |  47173MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質・ペプチド , 1種, 9分子 rstuvwxyz
| #1: タンパク質・ペプチド | 分子量: 5682.775 Da / 分子数: 9 / 断片: UNP residues 87-132 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: DLGAP5, DLG7, KIAA0008 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: DLGAP5, DLG7, KIAA0008 / 発現宿主:  |
|---|
-タンパク質 , 2種, 18分子 BDFHJLNPRACEGIKMOQ
| #2: タンパク質 | 分子量: 47940.945 Da / 分子数: 9 / 由来タイプ: 天然 / 由来: (天然)  #3: タンパク質 | 分子量: 48867.195 Da / 分子数: 9 / 由来タイプ: 天然 / 由来: (天然)  |
|---|
-非ポリマー , 3種, 36分子 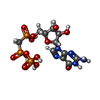




| #4: 化合物 | ChemComp-G2P / #5: 化合物 | ChemComp-MG / #6: 化合物 | ChemComp-GTP / |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: FILAMENT / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: HURP(65-174) bound to GMPCPP-stabilized microtubule / タイプ: COMPLEX / Entity ID: #1-#3 / 由来: MULTIPLE SOURCES |
|---|---|
| 分子量 | 実験値: NO |
| 由来(天然) | 生物種:  |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 6.8 詳細: BRB80 (1X): 80 mM PIPES, 1 mM MgCl2, 1 mM EGTA, pH 6.8 with KOH |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: C-flat-1.2/1.3 |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 95 % / 凍結前の試料温度: 298.15 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 81000 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 1000 nm / Cs: 0.01 mm / アライメント法: ZEMLIN TABLEAU |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 9 sec. / 電子線照射量: 39.6 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 2 / 実像数: 1728 |
| 画像スキャン | 横: 3838 / 縦: 3710 / 動画フレーム数/画像: 30 / 利用したフレーム数/画像: 1-30 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 348514 | ||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 2936725 / アルゴリズム: FOURIER SPACE / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: BACKBONE TRACE / 空間: RECIPROCAL | ||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj






