+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8v1t | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Herpes simplex virus 1 polymerase holoenzyme bound to DNA and acyclovir triphosphate in closed conformation | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード | TRANSFERASE/DNA / herpes simplex virus / replication / DNA polymerase / ACYCLOVIR / antiherpesvirus drug / TRANSFERASE-DNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報viral DNA genome replication / DNA-templated DNA replication / RNA-DNA hybrid ribonuclease activity / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / DNA replication / nucleotide binding / host cell nucleus / DNA binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス)synthetic construct (人工物) | |||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.8 Å | |||||||||
 データ登録者 データ登録者 | Pan, J. / Abraham, J. / Coen, D.M. / Shankar, S. / Yang, P. / Hogle, J. | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2024 ジャーナル: Cell / 年: 2024タイトル: Viral DNA polymerase structures reveal mechanisms of antiviral drug resistance. 著者: Sundaresh Shankar / Junhua Pan / Pan Yang / Yuemin Bian / Gábor Oroszlán / Zishuo Yu / Purba Mukherjee / David J Filman / James M Hogle / Mrinal Shekhar / Donald M Coen / Jonathan Abraham /    要旨: DNA polymerases are important drug targets, and many structural studies have captured them in distinct conformations. However, a detailed understanding of the impact of polymerase conformational ...DNA polymerases are important drug targets, and many structural studies have captured them in distinct conformations. However, a detailed understanding of the impact of polymerase conformational dynamics on drug resistance is lacking. We determined cryoelectron microscopy (cryo-EM) structures of DNA-bound herpes simplex virus polymerase holoenzyme in multiple conformations and interacting with antivirals in clinical use. These structures reveal how the catalytic subunit Pol and the processivity factor UL42 bind DNA to promote processive DNA synthesis. Unexpectedly, in the absence of an incoming nucleotide, we observed Pol in multiple conformations with the closed state sampled by the fingers domain. Drug-bound structures reveal how antivirals may selectively bind enzymes that more readily adopt the closed conformation. Molecular dynamics simulations and the cryo-EM structure of a drug-resistant mutant indicate that some resistance mutations modulate conformational dynamics rather than directly impacting drug binding, thus clarifying mechanisms that drive drug selectivity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8v1t.cif.gz 8v1t.cif.gz | 316 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8v1t.ent.gz pdb8v1t.ent.gz | 237.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8v1t.json.gz 8v1t.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/v1/8v1t https://data.pdbj.org/pub/pdb/validation_reports/v1/8v1t ftp://data.pdbj.org/pub/pdb/validation_reports/v1/8v1t ftp://data.pdbj.org/pub/pdb/validation_reports/v1/8v1t | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  42890MC  8exxC  8v1qC  8v1rC  8v1sC C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 133614.344 Da / 分子数: 1 / 由来タイプ: 組換発現 詳細: Herpes simplex virus type 1 (KOS strain) DNA polymerase catalytic subunit UL30 with its N-terminal 42 residues deleted and replaced by an N-terminal poly-histidine tag in the expression construct 由来: (組換発現)   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス)遺伝子: UL30, HHV1gp046 / 細胞株 (発現宿主): Sf9 発現宿主:  参照: UniProt: H9E937, DNA-directed DNA polymerase |
|---|---|
| #2: タンパク質 | 分子量: 36346.180 Da / 分子数: 1 / 由来タイプ: 組換発現 詳細: Herpes simplex virus 1 (KOS strain) DNA polymerase processivity factor UL42 residues 1-340 tagged with a prescission protease cleavage site followed by a maltose binding proten (MBP) tag in ...詳細: Herpes simplex virus 1 (KOS strain) DNA polymerase processivity factor UL42 residues 1-340 tagged with a prescission protease cleavage site followed by a maltose binding proten (MBP) tag in the expression construct 由来: (組換発現)   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス)遺伝子: UL42, HHV1gp061 / プラスミド: PMAL-C2 / 発現宿主:  |
-DNA鎖 , 2種, 2分子 PT
| #3: DNA鎖 | 分子量: 9866.353 Da / 分子数: 1 / 由来タイプ: 合成 詳細: 3'-deoxyl primer DNA strand, no mismatch with template strand 由来: (合成) synthetic construct (人工物) |
|---|---|
| #4: DNA鎖 | 分子量: 15199.773 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-非ポリマー , 3種, 9分子 
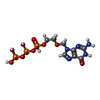



| #5: 化合物 | ChemComp-MG / #6: 化合物 | ChemComp-AVP / | #7: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: HERPES SIMPLEX VIRUS TYPE 1 POLYMERASE HOLOENZYME UL30:UL42 IN COMPLEX WITH dsDNA AND ACYCLOVIR TRIPHOSPHATE タイプ: COMPLEX 詳細: EACH COMPLEX CONSISTS OF ONE HSV-1 UL30 (expressed in insect cells), ONE HSV-1 UL42 (expressed in E.coli), ONE TEMPLATE DNA (synthetic), ONE PRIMER DNA (synthetic), AND ONE ACYCLOVIR ...詳細: EACH COMPLEX CONSISTS OF ONE HSV-1 UL30 (expressed in insect cells), ONE HSV-1 UL42 (expressed in E.coli), ONE TEMPLATE DNA (synthetic), ONE PRIMER DNA (synthetic), AND ONE ACYCLOVIR TRIPHOSPHATE MOLECULE (synthetic). Entity ID: #1-#4 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 0.197 MDa / 実験値: NO |
| 由来(天然) | 生物種:   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス)株: KOS |
| 由来(組換発現) | 生物種:  細胞: SF9 |
| 緩衝液 | pH: 7.5 詳細: 25 mM HEPES, pH 7.5, 150 mM NaCl, 2 mM tris(2-carboxyethyl)phosphine (TCEP) |
| 試料 | 濃度: 1.38 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | 詳細: GRIDS WERE GLOW DISCHARGED IN A PELCO EASIGLOW AT 15 MA FOR 30 SECONDS UNDER 0.39 MBAR. グリッドの材料: COPPER / グリッドのサイズ: 400 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 298 K 詳細: 3 MICROLITERS OF SAMPLE WERE BLOTTED FOR 3 SECONDS WITH FILTER PAPER SATURATED UNDER 100% HUMIDITY PRIOR TO PLUNGING. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 倍率(補正後): 60606 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 1000 nm / Calibrated defocus min: 1000 nm / 最大 デフォーカス(補正後): 2500 nm / Cs: 2.7 mm / C2レンズ絞り径: 50 µm / アライメント法: COMA FREE |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER 最高温度: 77 K / 最低温度: 70 K |
| 撮影 | 電子線照射量: 53 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 3268 |
| 電子光学装置 | エネルギーフィルター名称: GIF Bioquantum / エネルギーフィルタースリット幅: 20 eV |
| 画像スキャン | サンプリングサイズ: 5 µm / 横: 5760 / 縦: 4092 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 1214260 | ||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 187300 / アルゴリズム: FOURIER SPACE / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | B value: 33.64 / プロトコル: OTHER / 空間: REAL / Target criteria: CORRELATION COEFFICIENT 詳細: RIGID BODY, MINIMIZATION_GLOBAL, LOCAL_GRID_SEARCH, ADP REFINEMENT | ||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | 最高解像度: 2.8 Å |
 ムービー
ムービー コントローラー
コントローラー









 PDBj
PDBj










































