| 登録情報 | データベース: PDB / ID: 7up2
|
|---|
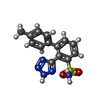
| タイトル | NDM1-inhibitor co-structure |
|---|
 要素 要素 | Beta-lactamase VIM-1 |
|---|
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / Metallo-beta-lactamase inhibitor / HYDROLASE / HYDROLASE-HYDROLASE INHIBITOR complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
: / : / Metallo-beta-lactamase superfamily / Ribonuclease Z/Hydroxyacylglutathione hydrolase-like / Metallo-beta-lactamase superfamily / Metallo-beta-lactamase; Chain A / Metallo-beta-lactamase / Ribonuclease Z/Hydroxyacylglutathione hydrolase-like / 4-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |   Pseudomonas aeruginosa (緑膿菌) Pseudomonas aeruginosa (緑膿菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.13 Å 分子置換 / 解像度: 1.13 Å |
|---|
 データ登録者 データ登録者 | Scapin, G. / Fischmann, T.O. |
|---|
| 資金援助 | 1件 |
|---|
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2022 ジャーナル: J.Med.Chem. / 年: 2022
タイトル: Rapid Evolution of a Fragment-like Molecule to Pan-Metallo-Beta-Lactamase Inhibitors: Initial Leads toward Clinical Candidates.
著者: Mandal, M. / Xiao, L. / Pan, W. / Scapin, G. / Li, G. / Tang, H. / Yang, S.W. / Pan, J. / Root, Y. / de Jesus, R.K. / Yang, C. / Prosise, W. / Dayananth, P. / Mirza, A. / Therien, A.G. / ...著者: Mandal, M. / Xiao, L. / Pan, W. / Scapin, G. / Li, G. / Tang, H. / Yang, S.W. / Pan, J. / Root, Y. / de Jesus, R.K. / Yang, C. / Prosise, W. / Dayananth, P. / Mirza, A. / Therien, A.G. / Young, K. / Flattery, A. / Garlisi, C. / Zhang, R. / Chu, D. / Sheth, P. / Chu, I. / Wu, J. / Markgraf, C. / Kim, H.Y. / Painter, R. / Mayhood, T.W. / DiNunzio, E. / Wyss, D.F. / Buevich, A.V. / Fischmann, T. / Pasternak, A. / Dong, S. / Hicks, J.D. / Villafania, A. / Liang, L. / Murgolo, N. / Black, T. / Hagmann, W.K. / Tata, J. / Parmee, E.R. / Weber, A.E. / Su, J. / Tang, H. |
|---|
| 履歴 | | 登録 | 2022年4月14日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2023年3月8日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年10月25日 | Group: Data collection / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond / pdbx_initial_refinement_model |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.13 Å
分子置換 / 解像度: 1.13 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2022
ジャーナル: J.Med.Chem. / 年: 2022 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 7up2.cif.gz
7up2.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb7up2.ent.gz
pdb7up2.ent.gz PDB形式
PDB形式 7up2.json.gz
7up2.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 7up2_validation.pdf.gz
7up2_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 7up2_full_validation.pdf.gz
7up2_full_validation.pdf.gz 7up2_validation.xml.gz
7up2_validation.xml.gz 7up2_validation.cif.gz
7up2_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/up/7up2
https://data.pdbj.org/pub/pdb/validation_reports/up/7up2 ftp://data.pdbj.org/pub/pdb/validation_reports/up/7up2
ftp://data.pdbj.org/pub/pdb/validation_reports/up/7up2 リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 17-ID / 波長: 1 Å
/ ビームライン: 17-ID / 波長: 1 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー






 PDBj
PDBj