+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7uoy | ||||||
|---|---|---|---|---|---|---|---|
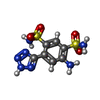
| タイトル | NDM1-inhibitor co-structure | ||||||
 要素 要素 | Metallo beta-lactamase | ||||||
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / Metallo-beta-lactamase inhibitor / HYDROLASE / HYDROLASE-HYDROLASE INHIBITOR complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報antibiotic catabolic process / beta-lactamase activity / beta-lactamase / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  Klebsiella pneumoniae (肺炎桿菌) Klebsiella pneumoniae (肺炎桿菌) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  フーリエ合成 / 解像度: 1.47 Å フーリエ合成 / 解像度: 1.47 Å | ||||||
 データ登録者 データ登録者 | Scapin, G. / Fischmann, T.O. | ||||||
| 資金援助 | 1件
| ||||||
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2022 ジャーナル: J.Med.Chem. / 年: 2022タイトル: Rapid Evolution of a Fragment-like Molecule to Pan-Metallo-Beta-Lactamase Inhibitors: Initial Leads toward Clinical Candidates. 著者: Mandal, M. / Xiao, L. / Pan, W. / Scapin, G. / Li, G. / Tang, H. / Yang, S.W. / Pan, J. / Root, Y. / de Jesus, R.K. / Yang, C. / Prosise, W. / Dayananth, P. / Mirza, A. / Therien, A.G. / ...著者: Mandal, M. / Xiao, L. / Pan, W. / Scapin, G. / Li, G. / Tang, H. / Yang, S.W. / Pan, J. / Root, Y. / de Jesus, R.K. / Yang, C. / Prosise, W. / Dayananth, P. / Mirza, A. / Therien, A.G. / Young, K. / Flattery, A. / Garlisi, C. / Zhang, R. / Chu, D. / Sheth, P. / Chu, I. / Wu, J. / Markgraf, C. / Kim, H.Y. / Painter, R. / Mayhood, T.W. / DiNunzio, E. / Wyss, D.F. / Buevich, A.V. / Fischmann, T. / Pasternak, A. / Dong, S. / Hicks, J.D. / Villafania, A. / Liang, L. / Murgolo, N. / Black, T. / Hagmann, W.K. / Tata, J. / Parmee, E.R. / Weber, A.E. / Su, J. / Tang, H. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7uoy.cif.gz 7uoy.cif.gz | 194.1 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7uoy.ent.gz pdb7uoy.ent.gz | 150.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7uoy.json.gz 7uoy.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7uoy_validation.pdf.gz 7uoy_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7uoy_full_validation.pdf.gz 7uoy_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  7uoy_validation.xml.gz 7uoy_validation.xml.gz | 23.2 KB | 表示 | |
| CIF形式データ |  7uoy_validation.cif.gz 7uoy_validation.cif.gz | 34.1 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/uo/7uoy https://data.pdbj.org/pub/pdb/validation_reports/uo/7uoy ftp://data.pdbj.org/pub/pdb/validation_reports/uo/7uoy ftp://data.pdbj.org/pub/pdb/validation_reports/uo/7uoy | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 26294.578 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)  Klebsiella pneumoniae (肺炎桿菌) Klebsiella pneumoniae (肺炎桿菌)遺伝子: blaNDM-1, bla NDM-1, blaNDM1, NDM-1, D647_p47098, DDJ63_29735, EC13450_007, NCTC13443_00040, p2146_00143, pCRE380_21, pN11x00042NDM_090, pNDM-SX04_5, pNDM10469_138, SAMEA3499901_05193, TR3_031, TR4_031 発現宿主:  #2: 化合物 | #3: 化合物 | ChemComp-CD / #4: 化合物 | #5: 水 | ChemComp-HOH / | 研究の焦点であるリガンドがあるか | Y | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.87 Å3/Da / 溶媒含有率: 34.15 % |
|---|---|
| 結晶化 | 温度: 291 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 4.6 詳細: 0.2 M ammonium acetate 0.1 M sodium acetate pH 4.6 20.0 w/v polyethylene glycol 4000 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 17-ID / 波長: 1 Å / ビームライン: 17-ID / 波長: 1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 検出器 | タイプ: DECTRIS PILATUS 6M / 検出器: PIXEL / 日付: 2012年6月29日 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射波長 | 波長: 1 Å / 相対比: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 | 解像度: 1.468→128.034 Å / Num. all: 63605 / Num. obs: 63605 / % possible obs: 93.3 % / 冗長度: 5.3 % / Biso Wilson estimate: 14.46 Å2 / Rpim(I) all: 0.025 / Rrim(I) all: 0.06 / Rsym value: 0.048 / Net I/av σ(I): 13 / Net I/σ(I): 20.5 / Num. measured all: 336677 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 シェル | Diffraction-ID: 1
|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  フーリエ合成 フーリエ合成開始モデル: 3ZR9 解像度: 1.47→21.52 Å / Cor.coef. Fo:Fc: 0.9259 / Cor.coef. Fo:Fc free: 0.8978 / SU R Cruickshank DPI: 0.073 / 交差検証法: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.077 / SU Rfree Blow DPI: 0.076 / SU Rfree Cruickshank DPI: 0.074
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 99.81 Å2 / Biso mean: 17.95 Å2 / Biso min: 5.86 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.16 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 1.47→21.52 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.47→1.51 Å / Rfactor Rfree error: 0 / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー







 PDBj
PDBj