+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7tqe | ||||||
|---|---|---|---|---|---|---|---|
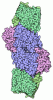
| タイトル | Selenium-incorporated nitrogenase Fe protein (Av2-Se) from A. vinelandii (22 mM KSeCN) | ||||||
 要素 要素 | Nitrogenase iron protein 1 | ||||||
 キーワード キーワード | OXIDOREDUCTASE / nitrogenase / metalloprotein / iron sulfur cluster | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nitrogenase / : / nitrogenase activity / nitrogen fixation / 4 iron, 4 sulfur cluster binding / ATP binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.59 Å 分子置換 / 解像度: 1.59 Å | ||||||
 データ登録者 データ登録者 | Buscagan, T.M. / Kaiser, J.T. / Rees, D.C. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Elife / 年: 2022 ジャーナル: Elife / 年: 2022タイトル: Selenocyanate derived Se-incorporation into the Nitrogenase Fe protein cluster. 著者: Buscagan, T.M. / Kaiser, J.T. / Rees, D.C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7tqe.cif.gz 7tqe.cif.gz | 74.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7tqe.ent.gz pdb7tqe.ent.gz | 52.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7tqe.json.gz 7tqe.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7tqe_validation.pdf.gz 7tqe_validation.pdf.gz | 802.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7tqe_full_validation.pdf.gz 7tqe_full_validation.pdf.gz | 804.1 KB | 表示 | |
| XML形式データ |  7tqe_validation.xml.gz 7tqe_validation.xml.gz | 13.5 KB | 表示 | |
| CIF形式データ |  7tqe_validation.cif.gz 7tqe_validation.cif.gz | 19.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/tq/7tqe https://data.pdbj.org/pub/pdb/validation_reports/tq/7tqe ftp://data.pdbj.org/pub/pdb/validation_reports/tq/7tqe ftp://data.pdbj.org/pub/pdb/validation_reports/tq/7tqe | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7t4hC  7tneC  7tpnC  7tpoC  7tpvC  7tpwC  7tpxC  7tpyC  7tpzC  7tq0C  7tq9C  7tqcC  7tqfC  7tqhC  7tqiC  7tqjC  7tqkC  6n4lS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 単位格子 |
| ||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 31548.240 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase |
|---|
-非ポリマー , 5種, 144分子 
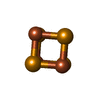



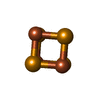



| #2: 化合物 | ChemComp-SF4 / |
|---|---|
| #3: 化合物 | ChemComp-SFS / |
| #4: 化合物 | ChemComp-MG / |
| #5: 化合物 | ChemComp-ADP / |
| #6: 水 | ChemComp-HOH / |
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|---|
| 非ポリマーの詳細 | Individual instances of the Fe-S/Se cluster represented by residues 301 SF4 and 302 SFS may contain ...Individual instances of the Fe-S/Se cluster represented by residues 301 SF4 and 302 SFS may contain both sulfur and selenium. The primary citation should be consulted for a detailed description of the cluster refinement. |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.03 Å3/Da / 溶媒含有率: 39.41 % |
|---|---|
| 結晶化 | 温度: 298 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 36-41% PEG400, 0.1-0.3 M sodium chloride, 0.1 M HEPES, pH 7.5, 2.5 mM dithionite, 0.17 mM Cymal-7 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SSRL SSRL  / ビームライン: BL12-2 / 波長: 0.97869, 0.98062 / ビームライン: BL12-2 / 波長: 0.97869, 0.98062 | |||||||||
| 検出器 | タイプ: DECTRIS PILATUS 6M / 検出器: PIXEL / 日付: 2020年7月10日 | |||||||||
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||
| 放射波長 |
| |||||||||
| 反射 | 解像度: 1.59→45.88 Å / Num. obs: 35230 / % possible obs: 99.8 % / 冗長度: 13.1 % / Biso Wilson estimate: 19.54 Å2 / CC1/2: 1 / Rmerge(I) obs: 0.068 / Rpim(I) all: 0.028 / Rrim(I) all: 0.073 / Net I/σ(I): 21.1 | |||||||||
| 反射 シェル | 解像度: 1.59→1.62 Å / 冗長度: 12.9 % / Rmerge(I) obs: 1.405 / Num. unique obs: 1813 / CC1/2: 0.873 / Rpim(I) all: 0.583 / Rrim(I) all: 1.523 / % possible all: 99.5 |
-位相決定
| 位相決定 | 手法:  分子置換 分子置換 | ||||||
|---|---|---|---|---|---|---|---|
| Phasing MR | R rigid body: 0.452
|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB entry 6N4L 解像度: 1.59→37.38 Å / SU ML: 0.15 / 交差検証法: THROUGHOUT / σ(F): 1.34 / 位相誤差: 22.59 / 立体化学のターゲット値: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 96.02 Å2 / Biso mean: 27.4524 Å2 / Biso min: 13.87 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 1.59→37.38 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0 / Total num. of bins used: 23
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj