+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7sca | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Synechocystis PCC 6803 Phycobilisome rod from OCP-PBS complex sample | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | PHOTOSYNTHESIS / Complex / light harvesting / pigment | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | ||||||
 データ登録者 データ登録者 | Sauer, P.V. / Sutter, M. / Dominguez-Martin, M.A. / Kirst, H. / Kerfeld, C.A. | ||||||
| 資金援助 | European Union, 1件
| ||||||
 引用 引用 |  ジャーナル: Nature / 年: 2022 ジャーナル: Nature / 年: 2022タイトル: Structures of a phycobilisome in light-harvesting and photoprotected states. 著者: María Agustina Domínguez-Martín / Paul V Sauer / Henning Kirst / Markus Sutter / David Bína / Basil J Greber / Eva Nogales / Tomáš Polívka / Cheryl A Kerfeld /    要旨: Phycobilisome (PBS) structures are elaborate antennae in cyanobacteria and red algae. These large protein complexes capture incident sunlight and transfer the energy through a network of embedded ...Phycobilisome (PBS) structures are elaborate antennae in cyanobacteria and red algae. These large protein complexes capture incident sunlight and transfer the energy through a network of embedded pigment molecules called bilins to the photosynthetic reaction centres. However, light harvesting must also be balanced against the risks of photodamage. A known mode of photoprotection is mediated by orange carotenoid protein (OCP), which binds to PBS when light intensities are high to mediate photoprotective, non-photochemical quenching. Here we use cryogenic electron microscopy to solve four structures of the 6.2 MDa PBS, with and without OCP bound, from the model cyanobacterium Synechocystis sp. PCC 6803. The structures contain a previously undescribed linker protein that binds to the membrane-facing side of PBS. For the unquenched PBS, the structures also reveal three different conformational states of the antenna, two previously unknown. The conformational states result from positional switching of two of the rods and may constitute a new mode of regulation of light harvesting. Only one of the three PBS conformations can bind to OCP, which suggests that not every PBS is equally susceptible to non-photochemical quenching. In the OCP-PBS complex, quenching is achieved through the binding of four 34 kDa OCPs organized as two dimers. The complex reveals the structure of the active form of OCP, in which an approximately 60 Å displacement of its regulatory carboxy terminal domain occurs. Finally, by combining our structure with spectroscopic properties, we elucidate energy transfer pathways within PBS in both the quenched and light-harvesting states. Collectively, our results provide detailed insights into the biophysical underpinnings of the control of cyanobacterial light harvesting. The data also have implications for bioengineering PBS regulation in natural and artificial light-harvesting systems. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7sca.cif.gz 7sca.cif.gz | 1.2 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7sca.ent.gz pdb7sca.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7sca.json.gz 7sca.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7sca_validation.pdf.gz 7sca_validation.pdf.gz | 4.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7sca_full_validation.pdf.gz 7sca_full_validation.pdf.gz | 4.3 MB | 表示 | |
| XML形式データ |  7sca_validation.xml.gz 7sca_validation.xml.gz | 186.6 KB | 表示 | |
| CIF形式データ |  7sca_validation.cif.gz 7sca_validation.cif.gz | 278.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/sc/7sca https://data.pdbj.org/pub/pdb/validation_reports/sc/7sca ftp://data.pdbj.org/pub/pdb/validation_reports/sc/7sca ftp://data.pdbj.org/pub/pdb/validation_reports/sc/7sca | HTTPS FTP |
-関連構造データ
| 関連構造データ |  25031MC  7sc7C  7sc8C  7sc9C  7scbC  7sccC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
| 実験データセット #1 | データ参照:  10.6019/EMPIAR-11133 / データの種類: EMPIAR / 詳細: EMPIAR-11133 10.6019/EMPIAR-11133 / データの種類: EMPIAR / 詳細: EMPIAR-11133 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-C-phycocyanin ... , 2種, 36分子 AAACAEAGAIAKAMAOAQASAUAWAYBABCBEBGBIABADAFAHAJALANAPARATAVAX...
| #1: タンパク質 | 分子量: 17602.529 Da / 分子数: 18 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: Q54715 #2: タンパク質 | 分子量: 18142.426 Da / 分子数: 18 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: Q54714 |
|---|
-Phycobilisome ... , 4種, 4分子 BKBLBMBN
| #3: タンパク質 | 分子量: 28938.758 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: P73093 |
|---|---|
| #4: タンパク質 | 分子量: 32558.607 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: P73203 |
| #5: タンパク質 | 分子量: 30836.346 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: P73204 |
| #6: タンパク質 | 分子量: 9333.342 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  株: PCC 6803 / Kazusa / 参照: UniProt: P73202 |
-非ポリマー , 2種, 1379分子 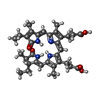


| #7: 化合物 | ChemComp-CYC / #8: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Complex of phycobilisome from Synechocystis PCC 6803 with OCP タイプ: COMPLEX / Entity ID: #1-#6 / 由来: NATURAL |
|---|---|
| 分子量 | 実験値: NO |
| 由来(天然) | 生物種:  |
| 緩衝液 | pH: 7.5 |
| 試料 | 濃度: 3.8 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R2/1 |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE-PROPANE / 詳細: Manual blotting |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1600 nm / 最小 デフォーカス(公称値): 500 nm |
| 試料ホルダ | 凍結剤: NITROGEN |
| 撮影 | 電子線照射量: 50 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||
| 画像処理 | 詳細: Streptavidin lattice was subtracted after movie alignment. | ||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 2133253 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: BACKBONE TRACE / 空間: REAL | ||||||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 25.42 Å2 | ||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj
