+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7pge | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | copper transporter PcoB | ||||||
 要素 要素 | Copper resistance protein B | ||||||
 キーワード キーワード | TRANSPORT PROTEIN / transporter | ||||||
| 機能・相同性 | Copper resistance B precursor / Copper resistance protein B precursor (CopB) / intracellular copper ion homeostasis / cell outer membrane / copper ion binding / THIOCYANATE ION / Copper resistance protein B 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  単波長異常分散 / 解像度: 2 Å 単波長異常分散 / 解像度: 2 Å | ||||||
 データ登録者 データ登録者 | Li, P. / Gourdon, P.E. | ||||||
| 資金援助 |  スウェーデン, 1件 スウェーデン, 1件
| ||||||
 引用 引用 |  ジャーナル: Protein Sci. / 年: 2022 ジャーナル: Protein Sci. / 年: 2022タイトル: PcoB is a defense outer membrane protein that facilitates cellular uptake of copper. 著者: Li, P. / Nayeri, N. / Gorecki, K. / Becares, E.R. / Wang, K. / Mahato, D.R. / Andersson, M. / Abeyrathna, S.S. / Lindkvist-Petersson, K. / Meloni, G. / Missel, J.W. / Gourdon, P. #1:  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: PcoB is a defense outer membrane protein that facilitate cellular uptake of copper 著者: Ping, L. / Pontus, G. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7pge.cif.gz 7pge.cif.gz | 116.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7pge.ent.gz pdb7pge.ent.gz | 74.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7pge.json.gz 7pge.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7pge_validation.pdf.gz 7pge_validation.pdf.gz | 631.8 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7pge_full_validation.pdf.gz 7pge_full_validation.pdf.gz | 636.4 KB | 表示 | |
| XML形式データ |  7pge_validation.xml.gz 7pge_validation.xml.gz | 10.4 KB | 表示 | |
| CIF形式データ |  7pge_validation.cif.gz 7pge_validation.cif.gz | 13.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/pg/7pge https://data.pdbj.org/pub/pdb/validation_reports/pg/7pge ftp://data.pdbj.org/pub/pdb/validation_reports/pg/7pge ftp://data.pdbj.org/pub/pdb/validation_reports/pg/7pge | HTTPS FTP |
-関連構造データ
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
|---|
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 24375.934 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|---|
| #2: 化合物 | ChemComp-C8E / ( |
| #3: 化合物 | ChemComp-LDA / |
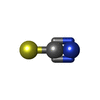
| #4: 化合物 | ChemComp-SCN / |
| #5: 水 | ChemComp-HOH / |
| 研究の焦点であるリガンドがあるか | N |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.51 Å3/Da / 溶媒含有率: 50.98 % |
|---|---|
| 結晶化 | 温度: 291 K / 手法: 蒸気拡散法, ハンギングドロップ法 / 詳細: PEG4000, NaSCN, sodium acetate |
-データ収集
| 回折 | 平均測定温度: 173 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X06SA / 波長: 1 Å / ビームライン: X06SA / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS EIGER R 4M / 検出器: PIXEL / 日付: 2017年5月26日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1 Å / 相対比: 1 |
| 反射 | 解像度: 1.97→43.53 Å / Num. obs: 30731 / % possible obs: 99.3 % / 冗長度: 6.6 % / Biso Wilson estimate: 38.19 Å2 / CC1/2: 0.99 / Net I/σ(I): 11.47 |
| 反射 シェル | 解像度: 1.972→2.043 Å / Num. unique obs: 4965 / CC1/2: 0.67 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  単波長異常分散 / 解像度: 2→43.53 Å / SU ML: 0.2399 / 交差検証法: FREE R-VALUE / σ(F): 1.21 / 位相誤差: 27.0962 単波長異常分散 / 解像度: 2→43.53 Å / SU ML: 0.2399 / 交差検証法: FREE R-VALUE / σ(F): 1.21 / 位相誤差: 27.0962 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 48.02 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2→43.53 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ | Refine-ID: X-RAY DIFFRACTION / Auth asym-ID: B / Label asym-ID: A
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj