+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7nev | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the hemiacetal complex between the SARS-CoV-2 Main Protease and Leupeptin | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード | PEPTIDE BINDING PROTEIN / SARS-CoV-2 / mPro / COVID-!9 | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / ISG15-specific peptidase activity / TRAF3-dependent IRF activation pathway ...protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / ISG15-specific peptidase activity / TRAF3-dependent IRF activation pathway / Transcription of SARS-CoV-2 sgRNAs / Translation of Replicase and Assembly of the Replication Transcription Complex / snRNP Assembly / Replication of the SARS-CoV-2 genome / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エキソリボヌクレアーゼ / double membrane vesicle viral factory outer membrane / host cell endoplasmic reticulum-Golgi intermediate compartment / SARS coronavirus main proteinase / 5'-3' DNA helicase activity / 3'-5'-RNA exonuclease activity / host cell endosome / symbiont-mediated degradation of host mRNA / mRNA guanylyltransferase / symbiont-mediated suppression of host ISG15-protein conjugation / G-quadruplex RNA binding / symbiont-mediated suppression of host toll-like receptor signaling pathway / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of IRF3 activity / omega peptidase activity / mRNA (guanine-N7)-methyltransferase / SARS-CoV-2 modulates host translation machinery / methyltransferase cap1 / host cell Golgi apparatus / symbiont-mediated suppression of host NF-kappaB cascade / symbiont-mediated perturbation of host ubiquitin-like protein modification / DNA helicase / methyltransferase cap1 activity / ubiquitinyl hydrolase 1 / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / cysteine-type deubiquitinase activity / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; システインプロテアーゼ / single-stranded RNA binding / host cell perinuclear region of cytoplasm / regulation of autophagy / viral protein processing / lyase activity / host cell endoplasmic reticulum membrane / RNA helicase / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / symbiont-mediated suppression of host gene expression / copper ion binding / viral translational frameshifting / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / lipid binding / DNA-templated transcription / SARS-CoV-2 activates/modulates innate and adaptive immune responses / host cell nucleus / ATP hydrolysis activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Streptomyces roseus (バクテリア) Streptomyces roseus (バクテリア) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.7 Å 分子置換 / 解像度: 1.7 Å | |||||||||
 データ登録者 データ登録者 | Guenther, S. / Reinke, P.Y.A. / Oberthuer, D. / Yefanov, O. / Gelisio, L. / Ginn, H.M. / Lieske, J. / Domaracky, M. / Brehm, W. / Rahmani Mashhour, A. ...Guenther, S. / Reinke, P.Y.A. / Oberthuer, D. / Yefanov, O. / Gelisio, L. / Ginn, H.M. / Lieske, J. / Domaracky, M. / Brehm, W. / Rahmani Mashhour, A. / White, T.A. / Knoska, J. / Pena Esperanza, G. / Koua, F. / Tolstikova, A. / Groessler, M. / Fischer, P. / Hennicke, V. / Fleckenstein, H. / Trost, F. / Galchenkova, M. / Gevorkov, Y. / Li, C. / Awel, S. / Xavier, P.L. / Ullah, N. / Andaleeb, H. / Falke, S. / Alves Franca, B. / Schwinzer, M. / Brognaro, H. / Werner, N. / Perbandt, M. / Tidow, H. / Seychell, B. / Beck, T. / Meier, S. / Zaitsev-Doyle, J.J. / Rogers, C. / Gieseler, H. / Melo, D. / Monteiro, D.C.F. / Dunkel, I. / Lane, T.J. / Peck, A. / Saouane, S. / Hakanpaeae, J. / Meyer, J. / Noei, H. / Gribbon, P. / Ellinger, B. / Kuzikov, M. / Wolf, M. / Zhang, L. / Ehrt, C. / Pletzer-Zelgert, J. / Wollenhaupt, J. / Feiler, C. / Weiss, M. / Schluenzen, F. / Schulz, E.C. / Mehrabi, P. / Norton-Baker, B. / Schmidt, C. / Lorenzen, K. / Schubert, R. / Sun, X. / Han, H. / Chari, A. / Fernandez Garcia, Y. / Turk, D. / Hilgenfeld, R. / Rarey, M. / Zaliani, A. / Chapman, H.N. / Pearson, A. / Betzel, C. / Meents, A. | |||||||||
| 資金援助 |  ドイツ, European Union, 2件 ドイツ, European Union, 2件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2021 ジャーナル: Science / 年: 2021タイトル: X-ray screening identifies active site and allosteric inhibitors of SARS-CoV-2 main protease. 著者: Gunther, S. / Reinke, P.Y.A. / Fernandez-Garcia, Y. / Lieske, J. / Lane, T.J. / Ginn, H.M. / Koua, F.H.M. / Ehrt, C. / Ewert, W. / Oberthuer, D. / Yefanov, O. / Meier, S. / Lorenzen, K. / ...著者: Gunther, S. / Reinke, P.Y.A. / Fernandez-Garcia, Y. / Lieske, J. / Lane, T.J. / Ginn, H.M. / Koua, F.H.M. / Ehrt, C. / Ewert, W. / Oberthuer, D. / Yefanov, O. / Meier, S. / Lorenzen, K. / Krichel, B. / Kopicki, J.D. / Gelisio, L. / Brehm, W. / Dunkel, I. / Seychell, B. / Gieseler, H. / Norton-Baker, B. / Escudero-Perez, B. / Domaracky, M. / Saouane, S. / Tolstikova, A. / White, T.A. / Hanle, A. / Groessler, M. / Fleckenstein, H. / Trost, F. / Galchenkova, M. / Gevorkov, Y. / Li, C. / Awel, S. / Peck, A. / Barthelmess, M. / Schlunzen, F. / Lourdu Xavier, P. / Werner, N. / Andaleeb, H. / Ullah, N. / Falke, S. / Srinivasan, V. / Franca, B.A. / Schwinzer, M. / Brognaro, H. / Rogers, C. / Melo, D. / Zaitseva-Doyle, J.J. / Knoska, J. / Pena-Murillo, G.E. / Mashhour, A.R. / Hennicke, V. / Fischer, P. / Hakanpaa, J. / Meyer, J. / Gribbon, P. / Ellinger, B. / Kuzikov, M. / Wolf, M. / Beccari, A.R. / Bourenkov, G. / von Stetten, D. / Pompidor, G. / Bento, I. / Panneerselvam, S. / Karpics, I. / Schneider, T.R. / Garcia-Alai, M.M. / Niebling, S. / Gunther, C. / Schmidt, C. / Schubert, R. / Han, H. / Boger, J. / Monteiro, D.C.F. / Zhang, L. / Sun, X. / Pletzer-Zelgert, J. / Wollenhaupt, J. / Feiler, C.G. / Weiss, M.S. / Schulz, E.C. / Mehrabi, P. / Karnicar, K. / Usenik, A. / Loboda, J. / Tidow, H. / Chari, A. / Hilgenfeld, R. / Uetrecht, C. / Cox, R. / Zaliani, A. / Beck, T. / Rarey, M. / Gunther, S. / Turk, D. / Hinrichs, W. / Chapman, H.N. / Pearson, A.R. / Betzel, C. / Meents, A. #1:  ジャーナル: Biorxiv / 年: 2020 ジャーナル: Biorxiv / 年: 2020タイトル: Inhibition of SARS-CoV-2 main protease by allosteric drug-binding 著者: Guenther, S. / Reinke, P. / Oberthuer, D. / Yefanov, O. / Gelisio, L. / Ginn, H. / Lieske, J. / Brehm, W. / Rahmani Mashour, A. / Knoska, J. / Pena Esperanza, G. / Koua, F. / Tolstikova, A. / ...著者: Guenther, S. / Reinke, P. / Oberthuer, D. / Yefanov, O. / Gelisio, L. / Ginn, H. / Lieske, J. / Brehm, W. / Rahmani Mashour, A. / Knoska, J. / Pena Esperanza, G. / Koua, F. / Tolstikova, A. / Groessler, M. / Fleckenstein, H. / Trost, F. / Galchenkova, M. / Gevorkov, Y. / Li, C. / Awel, S. / Paulraj, L.X. / Ullah, N. / Falke, S. / Alves Franca, B. / Schwinzer, M. / Brognaro, H. / Werner, N. / Perbandt, M. / Seychell, B. / Meier, S. / Giseler, H. / Melo, D. / Dunkel, I. / Lane, T.J. / Peck, A. / Saouane, S. / Hakanpaeae, J. / Meyer, J. / Noei, H. / Gribbon, P. / Ellinger, B. / Kuzikov, M. / Wolf, M. / Zhang, L. / Ehrt, C. / Pletzer-Zelgert, J. / Wollenhaupt, J. / Feiler, C. / Weiss, M. / Schulz, E.C. / Mehrabi, P. / Norton-Baker, B. / Schmidt, C. / Lorenzen, K. / Schubert, R. / Han, H. / Chari, A. / Fernandez Garcia, Y. / Hilgenfeld, R. / Rarey, M. / Zaliani, A. / Chapman, H.N. / Pearson, A. / Betzel, C. / Meents, A. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7nev.cif.gz 7nev.cif.gz | 179.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7nev.ent.gz pdb7nev.ent.gz | 115.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7nev.json.gz 7nev.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7nev_validation.pdf.gz 7nev_validation.pdf.gz | 460.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7nev_full_validation.pdf.gz 7nev_full_validation.pdf.gz | 460.2 KB | 表示 | |
| XML形式データ |  7nev_validation.xml.gz 7nev_validation.xml.gz | 22.7 KB | 表示 | |
| CIF形式データ |  7nev_validation.cif.gz 7nev_validation.cif.gz | 34.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ne/7nev https://data.pdbj.org/pub/pdb/validation_reports/ne/7nev ftp://data.pdbj.org/pub/pdb/validation_reports/ne/7nev ftp://data.pdbj.org/pub/pdb/validation_reports/ne/7nev | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6ynqSC  6yvfC  7a1uC  7abuC  7adwC  7af0C  7agaC  7ahaC  7ak4C  7akuC  7amjC  7ansC  7aolC  7ap6C  7aphC  7aqeC  7aqiC  7aqjC  7ar5C  7ar6C  7arfC  7avdC  7awrC  7awsC  7awuC  7awwC  7ax6C  7axmC  7axoC  7ay7C  7b83C S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||||||||
| 単位格子 |
| |||||||||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 / タンパク質・ペプチド , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 33825.547 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: rep, 1a-1b / 発現宿主:  |
|---|---|
| #2: タンパク質・ペプチド | |
-非ポリマー , 4種, 583分子 
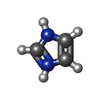





| #3: 化合物 | ChemComp-DMS / #4: 化合物 | ChemComp-IMD / | #5: 化合物 | ChemComp-CL / | #6: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.97 Å3/Da / 溶媒含有率: 37.68 % |
|---|---|
| 結晶化 | 温度: 291 K / 手法: 蒸気拡散法 詳細: Co-crystallization with the compounds was achieved by equilibrating a 6.25 mg/ml protein solution in 20 mM HEPES buffer (pH 7.8) containing 1 mM DTT, 1 mMEDTA, and 150 mM NaCl against a ...詳細: Co-crystallization with the compounds was achieved by equilibrating a 6.25 mg/ml protein solution in 20 mM HEPES buffer (pH 7.8) containing 1 mM DTT, 1 mMEDTA, and 150 mM NaCl against a reservoir solution of 100 mM MIB, pH 7.5, containing 25% w/w PEG 1500 and 5% v/v DMSO. Prior to crystallization compound solutions in DMSO were dried onto the wells of SwissCI 96-well plates. To obtain well-diffracting crystals in a reproducible way seeding was applied for crystal growth. Crystals appeared within a few hours and reached their final size after 2 - 3 days. Crystals were manually harvested and flash-frozen in liquid nitrogen for subsequent X-ray diffraction data collection. |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  PETRA III, DESY PETRA III, DESY  / ビームライン: P11 / 波長: 1.0332 Å / ビームライン: P11 / 波長: 1.0332 Å |
| 検出器 | タイプ: DECTRIS PILATUS3 6M / 検出器: PIXEL / 日付: 2020年4月9日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.0332 Å / 相対比: 1 |
| 反射 | 解像度: 1.69→31.28 Å / Num. obs: 29274 / % possible obs: 97.7 % / 冗長度: 3.7 % / Biso Wilson estimate: 17.23 Å2 / CC1/2: 0.995 / Rmerge(I) obs: 0.067 / Net I/σ(I): 10.2 |
| 反射 シェル | 解像度: 1.69→1.73 Å / 冗長度: 3.7 % / Rmerge(I) obs: 0.528 / Mean I/σ(I) obs: 1.7 / Num. unique obs: 2106 / CC1/2: 0.53 / % possible all: 96.5 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 6YNQ 解像度: 1.7→23.8 Å / SU ML: 0.2025 / 交差検証法: FREE R-VALUE / σ(F): 1.4 / 位相誤差: 24.5517 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 21.9 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.7→23.8 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ | Refine-ID: X-RAY DIFFRACTION / Auth asym-ID: A
|
 ムービー
ムービー コントローラー
コントローラー























 PDBj
PDBj