| 登録情報 | データベース: PDB / ID: 7mss
|
|---|
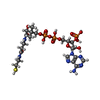
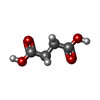
| タイトル | Human E105Qa GTP-specific succinyl-CoA synthetase complexed with succinate, magnesium ion and CoA |
|---|
 要素 要素 | (Succinate--CoA ligase ...) x 2 |
|---|
 キーワード キーワード | LIGASE / Complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
succinate-CoA ligase complex (GDP-forming) / succinate-CoA ligase (GDP-forming) / succinate-CoA ligase (GDP-forming) activity / succinate-CoA ligase complex (ADP-forming) / succinate-CoA ligase (ADP-forming) / succinate-CoA ligase complex / succinate-CoA ligase (ADP-forming) activity / succinyl-CoA catabolic process / succinyl-CoA metabolic process / succinate metabolic process ...succinate-CoA ligase complex (GDP-forming) / succinate-CoA ligase (GDP-forming) / succinate-CoA ligase (GDP-forming) activity / succinate-CoA ligase complex (ADP-forming) / succinate-CoA ligase (ADP-forming) / succinate-CoA ligase complex / succinate-CoA ligase (ADP-forming) activity / succinyl-CoA catabolic process / succinyl-CoA metabolic process / succinate metabolic process / Citric acid cycle (TCA cycle) / tricarboxylic acid cycle / Mitochondrial protein degradation / GDP binding / mitochondrial matrix / nucleotide binding / GTP binding / protein-containing complex binding / magnesium ion binding / mitochondrion / RNA binding / ATP binding / plasma membrane類似検索 - 分子機能 Succinate--CoA ligase [GDP-forming] subunit beta, mitochondrial / Succinyl-CoA ligase, alpha subunit / Succinate--CoA synthetase, beta subunit / ATP-grasp fold, succinyl-CoA synthetase-type / ATP-grasp domain / Succinyl-CoA synthetase domains / ATP-citrate lyase/succinyl-CoA ligase, active site / ATP-citrate lyase/succinyl-CoA ligase, conserved site / ATP-citrate lyase / succinyl-CoA ligases family active site. / ATP-citrate lyase / succinyl-CoA ligases family signature 1. ...Succinate--CoA ligase [GDP-forming] subunit beta, mitochondrial / Succinyl-CoA ligase, alpha subunit / Succinate--CoA synthetase, beta subunit / ATP-grasp fold, succinyl-CoA synthetase-type / ATP-grasp domain / Succinyl-CoA synthetase domains / ATP-citrate lyase/succinyl-CoA ligase, active site / ATP-citrate lyase/succinyl-CoA ligase, conserved site / ATP-citrate lyase / succinyl-CoA ligases family active site. / ATP-citrate lyase / succinyl-CoA ligases family signature 1. / Succinyl-CoA synthetase, beta subunit, conserved site / ATP-citrate lyase / succinyl-CoA ligases family signature 3. / ATP-citrate lyase/succinyl-CoA ligase / CoA-ligase / CoA binding domain / Succinyl-CoA synthetase-like / CoA binding domain / CoA-binding / ATP-grasp fold, subdomain 1 / NAD(P)-binding domain superfamily / Rossmann fold / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 COENZYME A / PHOSPHATE ION / SUCCINIC ACID / Succinate--CoA ligase [ADP/GDP-forming] subunit alpha, mitochondrial / Succinate--CoA ligase [GDP-forming] subunit beta, mitochondrial類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.75 Å 分子置換 / 解像度: 1.75 Å |
|---|
 データ登録者 データ登録者 | Huang, J. / Fraser, M.E. |
|---|
| 資金援助 |  カナダ, 1件 カナダ, 1件 | 組織 | 認可番号 | 国 |
|---|
| Natural Sciences and Engineering Research Council (NSERC, Canada) | 04815-2019 |  カナダ カナダ |
|
|---|
 引用 引用 |  ジャーナル: Acta Crystallogr.,Sect.F / 年: 2022 ジャーナル: Acta Crystallogr.,Sect.F / 年: 2022
タイトル: The structure of succinyl-CoA synthetase bound to the succinyl-phosphate intermediate clarifies the catalytic mechanism of ATP-citrate lyase
著者: Huang, J. / Fraser, M.E. |
|---|
| 履歴 | | 登録 | 2021年5月12日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2022年10月12日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年10月18日 | Group: Data collection / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond / pdbx_initial_refinement_model |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.75 Å
分子置換 / 解像度: 1.75 Å  データ登録者
データ登録者 カナダ, 1件
カナダ, 1件  引用
引用 ジャーナル: Acta Crystallogr.,Sect.F / 年: 2022
ジャーナル: Acta Crystallogr.,Sect.F / 年: 2022 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 7mss.cif.gz
7mss.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb7mss.ent.gz
pdb7mss.ent.gz PDB形式
PDB形式 7mss.json.gz
7mss.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 7mss_validation.pdf.gz
7mss_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 7mss_full_validation.pdf.gz
7mss_full_validation.pdf.gz 7mss_validation.xml.gz
7mss_validation.xml.gz 7mss_validation.cif.gz
7mss_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ms/7mss
https://data.pdbj.org/pub/pdb/validation_reports/ms/7mss ftp://data.pdbj.org/pub/pdb/validation_reports/ms/7mss
ftp://data.pdbj.org/pub/pdb/validation_reports/ms/7mss


 F&H 検索
F&H 検索 リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: SUCLG1 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: SUCLG1 / 発現宿主: 
 Homo sapiens (ヒト) / 遺伝子: SUCLG2 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: SUCLG2 / 発現宿主: 









 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 17-ID / 波長: 1 Å
/ ビームライン: 17-ID / 波長: 1 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj












