+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7f7f | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
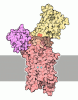
| タイトル | Cryo-EM structure of Dnf1 from Saccharomyces cerevisiae in yeast lipids with beryllium fluoride (resting state) | ||||||||||||||||||||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||||||||||||||||||||
 キーワード キーワード | LIPID TRANSPORT / P4-ATPases | ||||||||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of vacuole organization / glycosylceramide flippase activity / mating projection tip membrane / aminophospholipid translocation / phosphatidylcholine flippase activity / Ion transport by P-type ATPases / phosphatidylserine flippase activity / phospholipid-translocating ATPase complex / ceramide translocation / phosphatidylserine floppase activity ...regulation of vacuole organization / glycosylceramide flippase activity / mating projection tip membrane / aminophospholipid translocation / phosphatidylcholine flippase activity / Ion transport by P-type ATPases / phosphatidylserine flippase activity / phospholipid-translocating ATPase complex / ceramide translocation / phosphatidylserine floppase activity / ATPase-coupled intramembrane lipid carrier activity / phosphatidylethanolamine flippase activity / phosphatidylcholine floppase activity / cell septum / cellular bud neck / P-type phospholipid transporter / phospholipid translocation / establishment or maintenance of cell polarity / Neutrophil degranulation / cell periphery / intracellular protein transport / endocytosis / cell surface receptor signaling pathway / endosome membrane / magnesium ion binding / endoplasmic reticulum / Golgi apparatus / ATP hydrolysis activity / mitochondrion / ATP binding / identical protein binding / plasma membrane / cytoplasm 類似検索 - 分子機能 | ||||||||||||||||||||||||||||||||||||
| 生物種 |  | ||||||||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.81 Å | ||||||||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Xu, J. / He, Y. / Wu, X. / Li, L. | ||||||||||||||||||||||||||||||||||||
| 資金援助 |  中国, 1件 中国, 1件
| ||||||||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2022 ジャーナル: Cell Rep / 年: 2022タイトル: Conformational changes of a phosphatidylcholine flippase in lipid membranes. 著者: Jinkun Xu / Yilin He / Xiaofei Wu / Long Li /  要旨: Type 4 P-type ATPases (P4-ATPases) actively and selectively translocate phospholipids across membrane bilayers. Driven by ATP hydrolysis, P4-ATPases undergo conformational changes during lipid ...Type 4 P-type ATPases (P4-ATPases) actively and selectively translocate phospholipids across membrane bilayers. Driven by ATP hydrolysis, P4-ATPases undergo conformational changes during lipid flipping. It is unclear how the active flipping states of P4-ATPases are regulated in the lipid membranes, especially for phosphatidylcholine (PC)-flipping P4-ATPases whose substrate, PC, is a substantial component of membranes. Here, we report the cryoelectron microscopy structures of a yeast PC-flipping P4-ATPase, Dnf1, in lipid environments. In native yeast lipids, Dnf1 adopts a conformation in which the lipid flipping pathway is disrupted. Only when the lipid composition is changed can Dnf1 be captured in the active conformations that enable lipid flipping. These results suggest that, in the native membrane, Dnf1 may stay in an idle conformation that is unable to support the trans-membrane movement of lipids. Dnf1 may have altered conformational preferences in membranes with different lipid compositions. | ||||||||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7f7f.cif.gz 7f7f.cif.gz | 287.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7f7f.ent.gz pdb7f7f.ent.gz | 221.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7f7f.json.gz 7f7f.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/f7/7f7f https://data.pdbj.org/pub/pdb/validation_reports/f7/7f7f ftp://data.pdbj.org/pub/pdb/validation_reports/f7/7f7f ftp://data.pdbj.org/pub/pdb/validation_reports/f7/7f7f | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  31487MC  7drxC  7dshC  7dsiC  7whvC  7whwC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 178000.172 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  株: ATCC 204508 / S288c / 遺伝子: DNF1, YER166W, SYGP-ORF7 / 発現宿主:  |
|---|---|
| #2: タンパク質 | 分子量: 47490.395 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  株: ATCC 204508 / S288c / 遺伝子: LEM3, BRE3, ROS3, YNL323W, N0333 / 発現宿主:  |
-糖 , 3種, 3分子
| #3: 多糖 | 2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose |
|---|---|
| #4: 多糖 | beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta- ...beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose |
| #5: 多糖 | 2-acetamido-2-deoxy-beta-D-glucopyranose-(1-6)-2-acetamido-2-deoxy-beta-D-glucopyranose |
-非ポリマー , 1種, 1分子 
| #6: 化合物 | ChemComp-MG / |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Dnf1_Lem3 complex / タイプ: COMPLEX / Entity ID: #1-#2 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:  |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: NITROGEN |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: SPOT SCAN FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: SPOT SCAN |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 8 e/Å2 フィルム・検出器のモデル: DIRECT ELECTRON DE-16 (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア | 名称: PHENIX / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.81 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 212294 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj