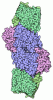
| 登録情報 | データベース: PDB / ID: 6l3g
|
|---|
| タイトル | Structural Basis for DNA Unwinding at Forked dsDNA by two coordinating Pif1 helicases |
|---|
 要素 要素 | - ATP-dependent DNA helicase
- DNA (5'-D(P*TP*TP*TP*TP*TP*TP*TP*CP*GP*CP*GP*CP*GP*CP*GP*CP*GP*TP*TP*TP*T)-3')
|
|---|
 キーワード キーワード | HYDROLASE/DNA / ATP dependent DNA helicase / Pif1 / dsDNA unwinding / HYDROLASE / HYDROLASE-DNA complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
DNA helicase activity / telomere maintenance / DNA repair類似検索 - 分子機能 DNA helicase Pif1-like / PIF1-like helicase / UvrD-like helicase C-terminal domain / UvrD-like helicase C-terminal domain / P-loop containing nucleoside triphosphate hydrolase類似検索 - ドメイン・相同性 ADENOSINE-5'-DIPHOSPHATE / TETRAFLUOROALUMINATE ION / DNA / DNA (> 10) / ATP-dependent DNA helicase類似検索 - 構成要素 |
|---|
| 生物種 |  Bacteroides sp. AF32-8BH (バクテリア) Bacteroides sp. AF32-8BH (バクテリア)
 Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.3 Å 分子置換 / 解像度: 3.3 Å |
|---|
 データ登録者 データ登録者 | Su, N. / Bharath, S.R. / Song, H. |
|---|
| 資金援助 |  中国, 中国,  米国, 2件 米国, 2件 | 組織 | 認可番号 | 国 |
|---|
| National Natural Science Foundation of China | 31670820 |  中国 中国 | | National Institutes of Health/National Human Genome Research Institute (NIH/NHGRI) | R35GM122601 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019
タイトル: Structural basis for DNA unwinding at forked dsDNA by two coordinating Pif1 helicases.
著者: Su, N. / Byrd, A.K. / Bharath, S.R. / Yang, O. / Jia, Y. / Tang, X. / Ha, T. / Raney, K.D. / Song, H. |
|---|
| 履歴 | | 登録 | 2019年10月10日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2019年12月11日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2022年3月23日 | Group: Author supporting evidence / Database references / Derived calculations
カテゴリ: database_2 / pdbx_audit_support ...database_2 / pdbx_audit_support / pdbx_struct_conn_angle / struct_conn
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_audit_support.funding_organization / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_auth_comp_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr2_label_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id |
|---|
| 改定 1.2 | 2023年11月22日 | Group: Data collection / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond / pdbx_initial_refinement_model |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Bacteroides sp. AF32-8BH (バクテリア)
Bacteroides sp. AF32-8BH (バクテリア) Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 3.3 Å
分子置換 / 解像度: 3.3 Å  データ登録者
データ登録者 中国,
中国,  米国, 2件
米国, 2件  引用
引用 ジャーナル: Nat Commun / 年: 2019
ジャーナル: Nat Commun / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6l3g.cif.gz
6l3g.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6l3g.ent.gz
pdb6l3g.ent.gz PDB形式
PDB形式 6l3g.json.gz
6l3g.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6l3g_validation.pdf.gz
6l3g_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6l3g_full_validation.pdf.gz
6l3g_full_validation.pdf.gz 6l3g_validation.xml.gz
6l3g_validation.xml.gz 6l3g_validation.cif.gz
6l3g_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/l3/6l3g
https://data.pdbj.org/pub/pdb/validation_reports/l3/6l3g ftp://data.pdbj.org/pub/pdb/validation_reports/l3/6l3g
ftp://data.pdbj.org/pub/pdb/validation_reports/l3/6l3g
 リンク
リンク 集合体
集合体

 要素
要素 Homo sapiens (ヒト)
Homo sapiens (ヒト) Bacteroides sp. AF32-8BH (バクテリア)
Bacteroides sp. AF32-8BH (バクテリア)





 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SSRF
SSRF  / ビームライン: BL17U1 / 波長: 0.9793 Å
/ ビームライン: BL17U1 / 波長: 0.9793 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj