+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6alt | |||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Solution structure of a DNA dodecamer with 5-methylcytosine at the 3rd and 9th position | |||||||||||||||||||||||||||||||
 要素 要素 | DNA (5'-D(* キーワード キーワードDNA / Drew-Dickerson / non-canonical / modified DNA / epigenetics | 機能・相同性 | DNA / DNA (> 10) |  機能・相同性情報 機能・相同性情報生物種 | synthetic construct (人工物) | 手法 | 溶液NMR / simulated annealing |  データ登録者 データ登録者Gruber, D.R. / Hoppins, J.J. / Miears, H.L. / Zharkov, D.O. / Smirnov, S.L. | 資金援助 | |  米国, 1件 米国, 1件
 引用 引用 ジャーナル: Nucleic Acids Res. / 年: 2018 ジャーナル: Nucleic Acids Res. / 年: 2018タイトル: Oxidative damage to epigenetically methylated sites affects DNA stability, dynamics and enzymatic demethylation. 著者: Gruber, D.R. / Toner, J.J. / Miears, H.L. / Shernyukov, A.V. / Kiryutin, A.S. / Lomzov, A.A. / Endutkin, A.V. / Grin, I.R. / Petrova, D.V. / Kupryushkin, M.S. / Yurkovskaya, A.V. / Johnson, E. ...著者: Gruber, D.R. / Toner, J.J. / Miears, H.L. / Shernyukov, A.V. / Kiryutin, A.S. / Lomzov, A.A. / Endutkin, A.V. / Grin, I.R. / Petrova, D.V. / Kupryushkin, M.S. / Yurkovskaya, A.V. / Johnson, E.C. / Okon, M. / Bagryanskaya, E.G. / Zharkov, D.O. / Smirnov, S.L. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6alt.cif.gz 6alt.cif.gz | 176 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6alt.ent.gz pdb6alt.ent.gz | 142.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6alt.json.gz 6alt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/al/6alt https://data.pdbj.org/pub/pdb/validation_reports/al/6alt ftp://data.pdbj.org/pub/pdb/validation_reports/al/6alt ftp://data.pdbj.org/pub/pdb/validation_reports/al/6alt | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 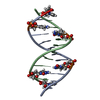
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 3611.466 Da / 分子数: 2 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 | タイプ: solution 内容: 50 mM sodium chloride, 10 mM potassium phosphate, 0.1 mM EDTA, 1 mM DNA (5'-D(*(DC5)P*GP*(DMC)P*GP*AP*AP*TP*TP*(DMC)P*GP*CP*(DG3))-3'), 100% D2O Label: dd06 / 溶媒系: 100% D2O | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 試料 |
| ||||||||||||||||||||
| 試料状態 |
|
-NMR測定
| NMRスペクトロメーター | タイプ: Varian INOVA / 製造業者: Varian / モデル: INOVA / 磁場強度: 500 MHz |
|---|
- 解析
解析
| NMR software |
| |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: simulated annealing / ソフトェア番号: 1 | |||||||||||||||||||||
| 代表構造 | 選択基準: minimized average structure | |||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 18 / 登録したコンフォーマーの数: 11 |
 ムービー
ムービー コントローラー
コントローラー



















 PDBj
PDBj






































 Amber
Amber