| 登録情報 | データベース: PDB / ID: 5x37
|
|---|
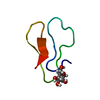
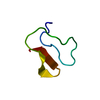
| タイトル | Solution structure of the Family 1 carbohydrate-binding module with mannosylated Ser14 |
|---|
 要素 要素 | Exoglucanase 1 |
|---|
 キーワード キーワード | HYDROLASE / Carbohydrate binding |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
cellulose 1,4-beta-cellobiosidase (non-reducing end) / cellulose 1,4-beta-cellobiosidase activity / cellulose binding / cellulose catabolic process / extracellular region類似検索 - 分子機能 Glycoside hydrolase, family 7 / Glycoside hydrolase family 7, catalytic domain superfamily / Glycosyl hydrolase family 7 / CBM1 (carbohydrate binding type-1) domain signature. / Cellulose-binding domain, fungal / Cellulose-binding domain superfamily / Fungal cellulose binding domain / CBM1 (carbohydrate binding type-1) domain profile. / Fungal-type cellulose-binding domain / Concanavalin A-like lectin/glucanase domain superfamily類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Hypocrea jecorina (菌類) Hypocrea jecorina (菌類) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Feng, Y. / Tan, Z. |
|---|
| 資金援助 |  米国, 米国,  中国, 4件 中国, 4件 | 組織 | 認可番号 | 国 |
|---|
| the NSF CAREER Award | CHE-1454925 |  米国 米国 | | the National Natural Science Foundation of China | 31270784 |  中国 中国 | | the National Natural Science Foundation of China | 31670735 |  中国 中国 | | Chinese Government Scholarship | 201604910035 |  中国 中国 |
|
|---|
 引用 引用 |  ジャーナル: Biochemistry / 年: 2017 ジャーナル: Biochemistry / 年: 2017
タイトル: Structural Insight into the Stabilizing Effect of O-Glycosylation
著者: Chaffey, P.K. / Guan, X. / Chen, C. / Ruan, Y. / Wang, X. / Tran, A.H. / Koelsch, T.N. / Cui, Q. / Feng, Y. / Tan, Z. |
|---|
| 履歴 | | 登録 | 2017年2月4日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2017年5月31日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年6月28日 | Group: Database references / カテゴリ: citation
Item: _citation.country / _citation.journal_id_ASTM ..._citation.country / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.title |
|---|
| 改定 1.2 | 2020年7月29日 | Group: Data collection / Derived calculations / Structure summary
カテゴリ: chem_comp / entity ...chem_comp / entity / pdbx_chem_comp_identifier / pdbx_entity_nonpoly / pdbx_nmr_software / pdbx_nmr_spectrometer / struct_conn / struct_site / struct_site_gen
Item: _chem_comp.name / _chem_comp.type ..._chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_entity_nonpoly.name / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model / _struct_conn.pdbx_role
解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.3 | 2023年6月14日 | Group: Database references / Other / Structure summary / カテゴリ: chem_comp / database_2 / pdbx_database_status
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI ..._chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Hypocrea jecorina (菌類)
Hypocrea jecorina (菌類) データ登録者
データ登録者 米国,
米国,  中国, 4件
中国, 4件  引用
引用 ジャーナル: Biochemistry / 年: 2017
ジャーナル: Biochemistry / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5x37.cif.gz
5x37.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5x37.ent.gz
pdb5x37.ent.gz PDB形式
PDB形式 5x37.json.gz
5x37.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5x37_validation.pdf.gz
5x37_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5x37_full_validation.pdf.gz
5x37_full_validation.pdf.gz 5x37_validation.xml.gz
5x37_validation.xml.gz 5x37_validation.cif.gz
5x37_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/x3/5x37
https://data.pdbj.org/pub/pdb/validation_reports/x3/5x37 ftp://data.pdbj.org/pub/pdb/validation_reports/x3/5x37
ftp://data.pdbj.org/pub/pdb/validation_reports/x3/5x37



 リンク
リンク 集合体
集合体
 要素
要素 Hypocrea jecorina (菌類)
Hypocrea jecorina (菌類) 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj



 HSQC
HSQC