| 登録情報 | データベース: PDB / ID: 4zxp
|
|---|
| タイトル | Crystal structure of Peptidyl- tRNA Hydrolase from Vibrio cholerae |
|---|
 要素 要素 | Peptidyl-tRNA hydrolase |
|---|
 キーワード キーワード | HYDROLASE / PEPTIDYL-TRNA |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
peptidyl-tRNA hydrolase / peptidyl-tRNA hydrolase activity / protein quality control for misfolded or incompletely synthesized proteins / rescue of stalled ribosome / tRNA binding / cytoplasm類似検索 - 分子機能 Peptidyl-tRNA hydrolase / Peptidyl-tRNA hydrolase signature 2. / Peptidyl-tRNA hydrolase signature 1. / Peptidyl-tRNA hydrolase / Peptidyl-tRNA hydrolase, conserved site / Peptidyl-tRNA hydrolase superfamily / Peptidyl-tRNA hydrolase / Rossmann fold / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌) Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌) |
|---|
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 1.63 Å 分子置換 / 解像度: 1.63 Å |
|---|
 データ登録者 データ登録者 | Shahid, S. / Pal, R.K. / Kabra, A. / Yadav, R. / Kumar, A. / Arora, A. |
|---|
 引用 引用 |  ジャーナル: RNA / 年: 2017 ジャーナル: RNA / 年: 2017
タイトル: Unraveling the stereochemical and dynamic aspects of the catalytic site of bacterial peptidyl-tRNA hydrolase.
著者: Kabra, A. / Shahid, S. / Pal, R.K. / Yadav, R. / Pulavarti, S.V. / Jain, A. / Tripathi, S. / Arora, A. |
|---|
| 履歴 | | 登録 | 2015年5月20日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2016年6月22日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年4月5日 | Group: Database references |
|---|
| 改定 1.2 | 2023年11月8日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
| 改定 1.3 | 2023年11月15日 | Group: Data collection / カテゴリ: chem_comp_atom / chem_comp_bond / Item: _chem_comp_atom.atom_id / _chem_comp_bond.atom_id_2 |
|---|
| 改定 1.4 | 2024年11月6日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌)
Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌) X線回折 /
X線回折 /  分子置換 / 解像度: 1.63 Å
分子置換 / 解像度: 1.63 Å  データ登録者
データ登録者 引用
引用 ジャーナル: RNA / 年: 2017
ジャーナル: RNA / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4zxp.cif.gz
4zxp.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4zxp.ent.gz
pdb4zxp.ent.gz PDB形式
PDB形式 4zxp.json.gz
4zxp.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 4zxp_validation.pdf.gz
4zxp_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 4zxp_full_validation.pdf.gz
4zxp_full_validation.pdf.gz 4zxp_validation.xml.gz
4zxp_validation.xml.gz 4zxp_validation.cif.gz
4zxp_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/zx/4zxp
https://data.pdbj.org/pub/pdb/validation_reports/zx/4zxp ftp://data.pdbj.org/pub/pdb/validation_reports/zx/4zxp
ftp://data.pdbj.org/pub/pdb/validation_reports/zx/4zxp リンク
リンク 集合体
集合体

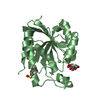
 要素
要素 Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌)
Vibrio cholerae O1 biovar El Tor str. N16961 (コレラ菌)
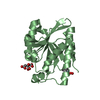
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: RIGAKU FR-E+ SUPERBRIGHT / 波長: 1.5418 Å
回転陽極 / タイプ: RIGAKU FR-E+ SUPERBRIGHT / 波長: 1.5418 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj