| 登録情報 | データベース: PDB / ID: 2w9v
|
|---|
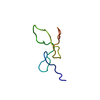
| タイトル | Solution structure of jerdostatin from Trimeresurus jerdonii with end C-terminal residues N45G46 deleted |
|---|
 要素 要素 | SHORT DISINTEGRIN JERDOSTATIN |
|---|
 キーワード キーワード | TOXIN / VENOM / CELL ADHESION / BLOOD COAGULATION |
|---|
| 機能・相同性 | Disintegrin domain / Echistatin / Disintegrin domain superfamily / Few Secondary Structures / Irregular / toxin activity / extracellular region / Disintegrin jerdostatin 機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |  TRIMERESURUS JERDONII (ヘビ) TRIMERESURUS JERDONII (ヘビ) |
|---|
| 手法 | 溶液NMR / CNS |
|---|
 データ登録者 データ登録者 | Carbajo, R.J. / Sanz, L. / Mosulen, S. / Calvete, J.J. / Pineda-Lucena, A. |
|---|
 引用 引用 |  ジャーナル: Proteins / 年: 2011 ジャーナル: Proteins / 年: 2011
タイトル: NMR Structure and Dynamics of Recombinant Wild-Type and Mutated Jerdostatin, a Selective Inhibitor of Integrin Alpha1 Beta1
著者: Carbajo, R.J. / Sanz, L. / Mosulen, S. / Perez, A. / Marcinkiewicz, C. / Pineda-Lucena, A. / Calvete, J.J. |
|---|
| 履歴 | | 登録 | 2009年1月29日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2010年3月31日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年11月9日 | Group: Database references / Version format compliance |
|---|
| 改定 1.2 | 2020年1月15日 | Group: Data collection / Other
カテゴリ: pdbx_database_status / pdbx_nmr_software / pdbx_nmr_spectrometer
Item: _pdbx_database_status.status_code_cs / _pdbx_database_status.status_code_mr ..._pdbx_database_status.status_code_cs / _pdbx_database_status.status_code_mr / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model |
|---|
| 改定 1.3 | 2023年6月14日 | Group: Database references / Other / カテゴリ: database_2 / pdbx_database_status
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data |
|---|
| 改定 1.4 | 2024年10月23日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature
Item: _database_2.pdbx_DOI / _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 TRIMERESURUS JERDONII (ヘビ)
TRIMERESURUS JERDONII (ヘビ) データ登録者
データ登録者 引用
引用 ジャーナル: Proteins / 年: 2011
ジャーナル: Proteins / 年: 2011 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2w9v.cif.gz
2w9v.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2w9v.ent.gz
pdb2w9v.ent.gz PDB形式
PDB形式 2w9v.json.gz
2w9v.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2w9v_validation.pdf.gz
2w9v_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2w9v_full_validation.pdf.gz
2w9v_full_validation.pdf.gz 2w9v_validation.xml.gz
2w9v_validation.xml.gz 2w9v_validation.cif.gz
2w9v_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/w9/2w9v
https://data.pdbj.org/pub/pdb/validation_reports/w9/2w9v ftp://data.pdbj.org/pub/pdb/validation_reports/w9/2w9v
ftp://data.pdbj.org/pub/pdb/validation_reports/w9/2w9v リンク
リンク 集合体
集合体
 要素
要素 TRIMERESURUS JERDONII (ヘビ) / 発現宿主:
TRIMERESURUS JERDONII (ヘビ) / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj HSQC
HSQC