| 登録情報 | データベース: PDB / ID: 2muq
|
|---|
| タイトル | Solution Structure of the Human FAAP20 UBZ |
|---|
 要素 要素 | Fanconi anemia-associated protein of 20 kDa |
|---|
 キーワード キーワード | Ubiquitin Binding Protein / UBZ / FAAP20 / zinc finger / ubiquitin-binding / Fanconi Anemia |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Fanconi anaemia nuclear complex / ubiquitin-modified protein reader activity / K63-linked polyubiquitin modification-dependent protein binding / polyubiquitin modification-dependent protein binding / translesion synthesis / interstrand cross-link repair / ubiquitin binding / Fanconi Anemia Pathway / PKR-mediated signaling / cell junction ...Fanconi anaemia nuclear complex / ubiquitin-modified protein reader activity / K63-linked polyubiquitin modification-dependent protein binding / polyubiquitin modification-dependent protein binding / translesion synthesis / interstrand cross-link repair / ubiquitin binding / Fanconi Anemia Pathway / PKR-mediated signaling / cell junction / chromosome / nuclear body / DNA damage response / chromatin / nucleoplasm / metal ion binding / cytosol類似検索 - 分子機能 FAAP20, zinc finger UBZ2-type / FAAP20, FANCA interaction domain / : / Ubiquitin-binding zinc-finger / FAAP20 FANCA interaction domain / Zinc finger UBZ2-type profile.類似検索 - ドメイン・相同性 Fanconi anemia core complex-associated protein 20類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / torsion angle dynamics |
|---|
| Model details | lowest energy, model1 |
|---|
 データ登録者 データ登録者 | Wojtaszek, J.L. / Wang, S. / Zhou, P. |
|---|
 引用 引用 |  ジャーナル: Nucleic Acids Res. / 年: 2014 ジャーナル: Nucleic Acids Res. / 年: 2014
タイトル: Ubiquitin recognition by FAAP20 expands the complex interface beyond the canonical UBZ domain.
著者: Wojtaszek, J.L. / Wang, S. / Kim, H. / Wu, Q. / D'Andrea, A.D. / Zhou, P. |
|---|
| 履歴 | | 登録 | 2014年9月16日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2014年12月3日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2015年2月11日 | Group: Database references |
|---|
| 改定 1.2 | 2023年6月14日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Other
カテゴリ: database_2 / pdbx_database_status ...database_2 / pdbx_database_status / pdbx_nmr_software / pdbx_struct_conn_angle / struct_conn / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data / _pdbx_nmr_software.name / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.3 | 2024年5月15日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2 / Item: _database_2.pdbx_DOI |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: Nucleic Acids Res. / 年: 2014
ジャーナル: Nucleic Acids Res. / 年: 2014 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2muq.cif.gz
2muq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2muq.ent.gz
pdb2muq.ent.gz PDB形式
PDB形式 2muq.json.gz
2muq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/mu/2muq
https://data.pdbj.org/pub/pdb/validation_reports/mu/2muq ftp://data.pdbj.org/pub/pdb/validation_reports/mu/2muq
ftp://data.pdbj.org/pub/pdb/validation_reports/mu/2muq リンク
リンク 集合体
集合体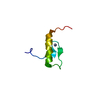
 要素
要素 Homo sapiens (ヒト) / 遺伝子: C1orf86, FAAP20, FP7162 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: C1orf86, FAAP20, FP7162 / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj


 HSQC
HSQC