| 登録情報 | データベース: PDB / ID: 2go0
|
|---|
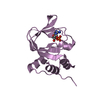
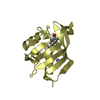
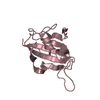
| タイトル | NMR solution structure of human pancreatitis-associated protein |
|---|
 要素 要素 | Regenerating islet-derived protein 3 alpha |
|---|
 キーワード キーワード | PROTEIN BINDING / C-type lectin / fibril |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
positive regulation of detection of glucose / response to symbiotic bacterium / positive regulation of keratinocyte proliferation / negative regulation of keratinocyte differentiation / negative regulation of inflammatory response to wounding / oligosaccharide binding / peptidoglycan binding / heterophilic cell-cell adhesion via plasma membrane cell adhesion molecules / Antimicrobial peptides / positive regulation of wound healing ...positive regulation of detection of glucose / response to symbiotic bacterium / positive regulation of keratinocyte proliferation / negative regulation of keratinocyte differentiation / negative regulation of inflammatory response to wounding / oligosaccharide binding / peptidoglycan binding / heterophilic cell-cell adhesion via plasma membrane cell adhesion molecules / Antimicrobial peptides / positive regulation of wound healing / acute-phase response / response to peptide hormone / hormone activity / response to wounding / antimicrobial humoral immune response mediated by antimicrobial peptide / signaling receptor activity / carbohydrate binding / positive regulation of cell population proliferation / extracellular space / extracellular region / identical protein binding / cytoplasm類似検索 - 分子機能 : / C-type lectin, conserved site / C-type lectin domain signature. / Mannose-Binding Protein A; Chain A / Mannose-Binding Protein A, subunit A / Lectin C-type domain / C-type lectin domain profile. / C-type lectin-like / C-type lectin (CTL) or carbohydrate-recognition domain (CRD) / C-type lectin-like/link domain superfamily ...: / C-type lectin, conserved site / C-type lectin domain signature. / Mannose-Binding Protein A; Chain A / Mannose-Binding Protein A, subunit A / Lectin C-type domain / C-type lectin domain profile. / C-type lectin-like / C-type lectin (CTL) or carbohydrate-recognition domain (CRD) / C-type lectin-like/link domain superfamily / C-type lectin fold / Roll / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / distance geometry, simulated annealing, torsion angle dynamics |
|---|
 データ登録者 データ登録者 | Chen, C.P. / Ho, M.R. / Lou, Y.C. |
|---|
 引用 引用 |  ジャーナル: To be Published ジャーナル: To be Published
タイトル: Human pancreatitis-associated protein forms fibrillar aggregate with native-like conformation.
著者: Ho, M.R. / Lou, Y.C. / Lin, W.C. / Lyu, P.C. / Chen, C.P. |
|---|
| 履歴 | | 登録 | 2006年4月12日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2006年9月12日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年5月1日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2020年2月26日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Other
カテゴリ: database_2 / pdbx_database_status ...database_2 / pdbx_database_status / pdbx_nmr_software / pdbx_nmr_spectrometer / pdbx_struct_assembly / pdbx_struct_oper_list
Item: _pdbx_database_status.status_code_cs / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model |
|---|
| 改定 1.4 | 2024年10月23日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: To be Published
ジャーナル: To be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2go0.cif.gz
2go0.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2go0.ent.gz
pdb2go0.ent.gz PDB形式
PDB形式 2go0.json.gz
2go0.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2go0_validation.pdf.gz
2go0_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2go0_full_validation.pdf.gz
2go0_full_validation.pdf.gz 2go0_validation.xml.gz
2go0_validation.xml.gz 2go0_validation.cif.gz
2go0_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/go/2go0
https://data.pdbj.org/pub/pdb/validation_reports/go/2go0 ftp://data.pdbj.org/pub/pdb/validation_reports/go/2go0
ftp://data.pdbj.org/pub/pdb/validation_reports/go/2go0 リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 発現宿主:
Homo sapiens (ヒト) / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj






 NMRPipe
NMRPipe