| 登録情報 | データベース: PDB / ID: 2frb
|
|---|
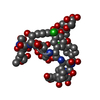
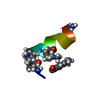
| タイトル | NMR structure of the alpha-conotoxin GI (ASN4)-benzoylphenylalanine derivative |
|---|
 要素 要素 | Alpha-conotoxin GIA |
|---|
 キーワード キーワード | TOXIN / ALPHA-CONOTOXIN GI / BENZOPHENONE ANALOGS / NICOTINIC ACETYLCHOLINE RECEPTOR ANTAGONIST |
|---|
| 機能・相同性 | Conotoxin, alpha-type / Alpha conotoxin precursor / Conotoxin, alpha-type, conserved site / Alpha-conotoxin family signature. / host cell postsynaptic membrane / acetylcholine receptor inhibitor activity / toxin activity / extracellular region / Alpha-conotoxin GI 機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |  Conus geographus (アンボイナ) Conus geographus (アンボイナ) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Pashkov, V.S. / Maslennikov, I. / Kasheverov, I.V. / Zhmak, M.N. / Utkin, Y.N. / Tsetlin, V.I. / Arseniev, A.S. |
|---|
 引用 引用 |  ジャーナル: Febs J. / 年: 2006 ジャーナル: Febs J. / 年: 2006
タイトル: Alpha-Conotoxin GI benzoylphenylalanine derivatives. (1)H-NMR structures and photoaffinity labeling of the Torpedo californica nicotinic acetylcholine receptor.
著者: Kasheverov, I.E. / Chiara, D.C. / Zhmak, M.N. / Maslennikov, I.V. / Pashkov, V.S. / Arseniev, A.S. / Utkin, Y.N. / Cohen, J.B. / Tsetlin, V.I. |
|---|
| 履歴 | | 登録 | 2006年1月19日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2006年5月30日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年5月1日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2021年11月3日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Experimental preparation / Source and taxonomy
カテゴリ: database_2 / diffrn ...database_2 / diffrn / diffrn_radiation / diffrn_radiation_wavelength / pdbx_entity_src_syn / pdbx_nmr_exptl_sample / pdbx_nmr_sample_details / pdbx_nmr_software / pdbx_nmr_spectrometer / pdbx_struct_assembly / pdbx_struct_oper_list / struct_conn / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_entity_src_syn.details / _pdbx_entity_src_syn.ncbi_taxonomy_id / _pdbx_entity_src_syn.organism_common_name / _pdbx_entity_src_syn.organism_scientific / _pdbx_nmr_sample_details.label / _pdbx_nmr_sample_details.type / _pdbx_nmr_software.authors / _pdbx_nmr_software.classification / _pdbx_nmr_spectrometer.model / _struct_conn.pdbx_leaving_atom_flag / _struct_ref_seq_dif.details |
|---|
| 改定 2.0 | 2023年11月15日 | Group: Atomic model / Data collection / カテゴリ: atom_site / chem_comp_atom / chem_comp_bond / Item: _atom_site.auth_atom_id / _atom_site.label_atom_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Conus geographus (アンボイナ)
Conus geographus (アンボイナ) データ登録者
データ登録者 引用
引用 ジャーナル: Febs J. / 年: 2006
ジャーナル: Febs J. / 年: 2006 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2frb.cif.gz
2frb.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2frb.ent.gz
pdb2frb.ent.gz PDB形式
PDB形式 2frb.json.gz
2frb.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/fr/2frb
https://data.pdbj.org/pub/pdb/validation_reports/fr/2frb ftp://data.pdbj.org/pub/pdb/validation_reports/fr/2frb
ftp://data.pdbj.org/pub/pdb/validation_reports/fr/2frb リンク
リンク 集合体
集合体
 要素
要素 Conus geographus (アンボイナ) / 参照: UniProt: P01519
Conus geographus (アンボイナ) / 参照: UniProt: P01519 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj