+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1z31 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | The structure of an enzyme-activating fragment of human telomerase RNA | ||||||
 要素 要素 | human telomerase PJ6 hairpin | ||||||
 キーワード キーワード | RNA / asymmetric internal bulge / residual dipolar couplings / telomerase protein binding site | ||||||
| 機能・相同性 | RNA / RNA (> 10) 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / torsion angle dynamics | ||||||
 データ登録者 データ登録者 | Leeper, T.C. / Varani, G. | ||||||
 引用 引用 |  ジャーナル: RNA / 年: 2005 ジャーナル: RNA / 年: 2005タイトル: The structure of an enzyme-activating fragment of human telomerase RNA. 著者: Leeper, T.C. / Varani, G. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1z31.cif.gz 1z31.cif.gz | 200.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1z31.ent.gz pdb1z31.ent.gz | 169.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1z31.json.gz 1z31.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1z31_validation.pdf.gz 1z31_validation.pdf.gz | 322.7 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1z31_full_validation.pdf.gz 1z31_full_validation.pdf.gz | 398.3 KB | 表示 | |
| XML形式データ |  1z31_validation.xml.gz 1z31_validation.xml.gz | 14 KB | 表示 | |
| CIF形式データ |  1z31_validation.cif.gz 1z31_validation.cif.gz | 22 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/z3/1z31 https://data.pdbj.org/pub/pdb/validation_reports/z3/1z31 ftp://data.pdbj.org/pub/pdb/validation_reports/z3/1z31 ftp://data.pdbj.org/pub/pdb/validation_reports/z3/1z31 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 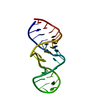
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 10183.078 Da / 分子数: 1 / 断片: human telomerase RNA / 由来タイプ: 合成 詳細: T7 RNA polymerase in vitro transcription from DNA oligonucleotide template |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 |
| ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 試料状態 |
|
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射波長 | 相対比: 1 | |||||||||||||||
| NMRスペクトロメーター |
|
- 解析
解析
| NMR software |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: torsion angle dynamics / ソフトェア番号: 1 詳細: 726 total restraints, 429 NOE-derived restraints, 159 dihedral restraints, 65 residual dipolar coupling restraints, 62 hydrogen bonds, and 11 weak planarity restraints. | ||||||||||||||||||||||||
| 代表構造 | 選択基準: closest to the average | ||||||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the least restraint violations 計算したコンフォーマーの数: 100 / 登録したコンフォーマーの数: 10 |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj





























 HSQC
HSQC