+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1ttj | ||||||
|---|---|---|---|---|---|---|---|
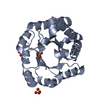
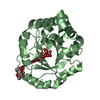
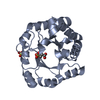
| タイトル | THREE NEW CRYSTAL STRUCTURES OF POINT MUTATION VARIANTS OF MONOTIM: CONFORMATIONAL FLEXIBILITY OF LOOP-1,LOOP-4 AND LOOP-8 | ||||||
 要素 要素 | TRIOSEPHOSPHATE ISOMERASE | ||||||
 キーワード キーワード | ISOMERASE(INTRAMOLECULAR OXIDOREDUCTASE) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報glycosome / triose-phosphate isomerase / triose-phosphate isomerase activity / glycerol catabolic process / glyceraldehyde-3-phosphate biosynthetic process / gluconeogenesis / glycolytic process / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / 解像度: 2.4 Å X線回折 / 解像度: 2.4 Å | ||||||
 データ登録者 データ登録者 | Radha Kishan, K.V. / Wierenga, R.K. | ||||||
 引用 引用 |  ジャーナル: Structure / 年: 1995 ジャーナル: Structure / 年: 1995タイトル: Three new crystal structures of point mutation variants of monoTIM: conformational flexibility of loop-1, loop-4 and loop-8. 著者: Borchert, T.V. / Kishan, K.V. / Zeelen, J.P. / Schliebs, W. / Thanki, N. / Abagyan, R. / Jaenicke, R. / Wierenga, R.K. #1:  ジャーナル: To be Published ジャーナル: To be Publishedタイトル: The 2.4 Angstrom Crystal Structure of the Complex of Monoss (A Monomeric Variant of Trypanosomal Triosephosphate Isomerase) and a Transition State Analogue, Phosphoglycolohydroxamate 著者: Radha Kishan, K.V. / Ph Zeelen, J. / Schliebs, W. / Wierenga, R.K. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1ttj.cif.gz 1ttj.cif.gz | 57.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1ttj.ent.gz pdb1ttj.ent.gz | 41 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1ttj.json.gz 1ttj.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1ttj_validation.pdf.gz 1ttj_validation.pdf.gz | 387.9 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1ttj_full_validation.pdf.gz 1ttj_full_validation.pdf.gz | 396.4 KB | 表示 | |
| XML形式データ |  1ttj_validation.xml.gz 1ttj_validation.xml.gz | 7.2 KB | 表示 | |
| CIF形式データ |  1ttj_validation.cif.gz 1ttj_validation.cif.gz | 10.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/tt/1ttj https://data.pdbj.org/pub/pdb/validation_reports/tt/1ttj ftp://data.pdbj.org/pub/pdb/validation_reports/tt/1ttj ftp://data.pdbj.org/pub/pdb/validation_reports/tt/1ttj | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 26020.688 Da / 分子数: 1 変異: VARIANT OF MONOTIM WITH PHE 45 REPLACED BY SER AND VAL 46 REPLACED BY SER (F45S, V46S) AND 73 - 79 DELETED 由来タイプ: 天然 由来: (天然)  生物種: Trypanosoma brucei / 株: brucei / 参照: UniProt: P04789, triose-phosphate isomerase |
|---|---|
| #2: 化合物 | ChemComp-PGH / |
| #3: 水 | ChemComp-HOH / |
| 配列の詳細 | THERE IS ONE BREAK IN THE SEQUENCE AT 73. RESIDUE NUMBERS 73 - 79 ARE MISSING DUE TO DELETION OF A ...THERE IS ONE BREAK IN THE SEQUENCE AT 73. RESIDUE NUMBERS 73 - 79 ARE MISSING DUE TO DELETION OF A LOOP FROM THE PARENT MODEL AND CONNECTING |
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.15 Å3/Da / 溶媒含有率: 42.92 % | ||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | *PLUS pH: 6.5 / 手法: 蒸気拡散法, ハンギングドロップ法 | ||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 反射 | 解像度: 2.4→32 Å / Num. obs: 8529 / % possible obs: 86 % / Observed criterion σ(I): 0 |
|---|---|
| 反射 | *PLUS Num. measured all: 20243 / Rmerge(I) obs: 0.053 |
| 反射 シェル | *PLUS 最高解像度: 2.4 Å / 最低解像度: 2.5 Å / % possible obs: 74 % |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 2.4→32 Å / σ(F): 0 /
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.4→32 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS Rfactor obs: 0.178 / Rfactor Rwork: 0.178 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj