+ データを開く
データを開く
- 基本情報
基本情報
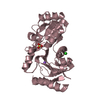
| 登録情報 | データベース: PDB / ID: 1lrp | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | COMPARISON OF THE STRUCTURES OF CRO AND LAMBDA REPRESSOR PROTEINS FROM BACTERIOPHAGE LAMBDA | |||||||||
 要素 要素 | LAMBDA REPRESSOR | |||||||||
 キーワード キーワード | DNA BINDING REGULATORY PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報maintenance of viral latency / latency-replication decision / positive regulation of viral transcription / negative regulation of transcription by competitive promoter binding / core promoter sequence-specific DNA binding / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Enterobacteria phage lambda (λファージ) Enterobacteria phage lambda (λファージ) | |||||||||
| 手法 |  X線回折 / 解像度: 3.2 Å X線回折 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Pabo, C. / Lewis, M. | |||||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 1983 ジャーナル: J.Mol.Biol. / 年: 1983タイトル: Comparison of the structures of cro and lambda repressor proteins from bacteriophage lambda. 著者: Ohlendorf, D.H. / Anderson, W.F. / Lewis, M. / Pabo, C.O. / Matthews, B.W. #1:  ジャーナル: Cold Spring Harbor Symp.Quant.Biol. / 年: 1983 ジャーナル: Cold Spring Harbor Symp.Quant.Biol. / 年: 1983タイトル: Structure of the Operator-Binding Domain of Bacteriophage Lambda Repressor. Implications for DNA Recognition and Gene Regulation 著者: Lewis, M. / Jeffrey, A. / Wang, J. / Ladner, R. / Ptashne, M. / Pabo, C.O. #2:  ジャーナル: Nature / 年: 1982 ジャーナル: Nature / 年: 1982タイトル: Homology Among DNA-Binding Proteins Suggests Use of a Conserved Super-Secondary Structure 著者: Sauer, R.T. / Yocum, R.R. / Doolittle, R.F. / Lewis, M. / Pabo, C.O. #3:  ジャーナル: Nature / 年: 1982 ジャーナル: Nature / 年: 1982タイトル: The Operator-Binding Domain of Lambda Repressor. Structure and DNA Recognition 著者: Pabo, C.O. / Lewis, M. #4:  ジャーナル: Nature / 年: 1982 ジャーナル: Nature / 年: 1982タイトル: The N-Terminal Arms of Lambda Repressor Wrap Around the Operator DNA 著者: Pabo, C.O. / Krovatin, W. / Jeffrey, A. / Sauer, R.T. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1lrp.cif.gz 1lrp.cif.gz | 18 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1lrp.ent.gz pdb1lrp.ent.gz | 9.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1lrp.json.gz 1lrp.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1lrp_validation.pdf.gz 1lrp_validation.pdf.gz | 315.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1lrp_full_validation.pdf.gz 1lrp_full_validation.pdf.gz | 315.1 KB | 表示 | |
| XML形式データ |  1lrp_validation.xml.gz 1lrp_validation.xml.gz | 722 B | 表示 | |
| CIF形式データ |  1lrp_validation.cif.gz 1lrp_validation.cif.gz | 3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/lr/1lrp https://data.pdbj.org/pub/pdb/validation_reports/lr/1lrp ftp://data.pdbj.org/pub/pdb/validation_reports/lr/1lrp ftp://data.pdbj.org/pub/pdb/validation_reports/lr/1lrp | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| 2 | 
| ||||||||||||
| 単位格子 |
| ||||||||||||
| 非結晶学的対称性 (NCS) | NCS oper:
| ||||||||||||
| 詳細 | THE REPRESSOR MOLECULE CONSISTS OF A DIMER, AND COORDINATES FOR THE SYMMETRY RELATED CHAIN CAN BE GENERATED FROM THE CHAIN PRESENTED IN THIS ENTRY BY 1.0 0.0 0.0 0.0 0.0 -1.0 0.0 0.0 0.0 0.0 -1.0 0.0 |
- 要素
要素
| #1: タンパク質 | 分子量: 10136.613 Da / 分子数: 3 / 由来タイプ: 組換発現 由来: (組換発現)  Enterobacteria phage lambda (λファージ) Enterobacteria phage lambda (λファージ)属: Lambda-like viruses / 参照: UniProt: P03034 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 3 Å3/Da / 溶媒含有率: 58.99 % |
|---|---|
| 結晶化 | *PLUS 手法: unknown |
-データ収集
| 放射 | 散乱光タイプ: x-ray |
|---|---|
| 放射波長 | 相対比: 1 |
- 解析
解析
| 精密化 | 最高解像度: 3.2 Å | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化ステップ | サイクル: LAST / 最高解像度: 3.2 Å
| ||||||||||||
| 精密化 | *PLUS 最高解像度: 3.2 Å | ||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||
| 原子変位パラメータ | *PLUS |
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj



