+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1i2u | ||||||
|---|---|---|---|---|---|---|---|
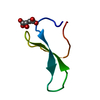
| タイトル | NMR SOLUTION STRUCTURES OF ANTIFUNGAL HELIOMICIN | ||||||
 要素 要素 | DEFENSIN HELIOMICIN | ||||||
 キーワード キーワード | ANTIFUNGAL PROTEIN / alpha-beta protein / CSab motif (cysteine stabilized alpha-helix beta-sheet motif) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報defense response to fungus / killing of cells of another organism / innate immune response / extracellular region 類似検索 - 分子機能 | ||||||
| 生物種 |  Heliothis virescens (蝶・蛾) Heliothis virescens (蝶・蛾) | ||||||
| 手法 | 溶液NMR / torsion angle dynamics (DYANA), energy minimisation (XPLOR) | ||||||
 データ登録者 データ登録者 | Lamberty, M. / Caille, A. / Landon, C. / Tassin-Moindrot, S. / Hetru, C. / Bulet, P. / Vovelle, F. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2001 ジャーナル: Biochemistry / 年: 2001タイトル: Solution structures of the antifungal heliomicin and a selected variant with both antibacterial and antifungal activities. 著者: Lamberty, M. / Caille, A. / Landon, C. / Tassin-Moindrot, S. / Hetru, C. / Bulet, P. / Vovelle, F. #1:  ジャーナル: J.Biol.Chem. / 年: 1999 ジャーナル: J.Biol.Chem. / 年: 1999タイトル: Insect Immunity. Isolation from the Lepidopteran Heliothis virescens of a Novel Insect Defensin with Potent Antifungal Activity 著者: LAMBERTY, M. / ADES, S. / UTTENWEILER-JOSEPH, S. / BROOKHART, G. / BUSHEY, D. / HOFFMANN, J.A. / BULET, P. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1i2u.cif.gz 1i2u.cif.gz | 230.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1i2u.ent.gz pdb1i2u.ent.gz | 189.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1i2u.json.gz 1i2u.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/i2/1i2u https://data.pdbj.org/pub/pdb/validation_reports/i2/1i2u ftp://data.pdbj.org/pub/pdb/validation_reports/i2/1i2u ftp://data.pdbj.org/pub/pdb/validation_reports/i2/1i2u | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 4796.368 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Heliothis virescens (蝶・蛾) / プラスミド: PSEA2 / 発現宿主: Heliothis virescens (蝶・蛾) / プラスミド: PSEA2 / 発現宿主:  |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 溶液NMR |
|---|---|
| NMR実験 | タイプ: 2D 1H DQF-COSY; TQF-COSY; TOCSY; NOESY |
| NMR実験の詳細 | Text: This structure was determined using standard 2D homonuclear techniques. |
- 試料調製
試料調製
| 詳細 | 内容: 4 mM heliomicin ; 40mM sodium acetate buffer / 溶媒系: 90% H2O/10% D2O |
|---|---|
| 試料状態 | イオン強度: 40mM sodium acetate buffer / pH: 4.3 / 圧: ambient / 温度: 293 K |
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M |
|---|---|
| 放射波長 | 相対比: 1 |
| NMRスペクトロメーター | タイプ: Bruker AMX / 製造業者: Bruker / モデル: AMX / 磁場強度: 500 MHz |
- 解析
解析
| NMR software |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: torsion angle dynamics (DYANA), energy minimisation (XPLOR) ソフトェア番号: 1 詳細: the structures are based on a total of 130 intra-residue, 163 sequential, 105 medium range, 198 long range NOE-derived distance restraints, 9 distances restraints corresponding to the 3 ...詳細: the structures are based on a total of 130 intra-residue, 163 sequential, 105 medium range, 198 long range NOE-derived distance restraints, 9 distances restraints corresponding to the 3 disulfide bridge, 85 dihedral angle restraints, and 14 distance restraints for hydrogen bonds | |||||||||||||||
| 代表構造 | 選択基準: lowest target function | |||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with acceptable covalent geometry, structures with favorable non-bond energy, structures with the least restraint violations, structures with the ...コンフォーマー選択の基準: structures with acceptable covalent geometry, structures with favorable non-bond energy, structures with the least restraint violations, structures with the lowest energy, target function 計算したコンフォーマーの数: 40 / 登録したコンフォーマーの数: 18 |
 ムービー
ムービー コントローラー
コントローラー







 PDBj
PDBj
 X-PLOR
X-PLOR