+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1ezn | ||||||
|---|---|---|---|---|---|---|---|
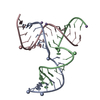
| タイトル | SOLUTION STRUCTURE OF A DNA THREE-WAY JUNCTION | ||||||
 要素 要素 | DNA THREE-WAY JUNCTION | ||||||
 キーワード キーワード | DNA / three-way junction / four-way junction / HMG-box protein / Holliday junction / hammerhead | ||||||
| 機能・相同性 | DNA / DNA (> 10) 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / torsion angle dynamics | ||||||
 データ登録者 データ登録者 | van Buuren, B.N.M. / Overmars, F.J. / Ippel, J.H. / Altona, C. / Wijmenga, S.S. | ||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2000 ジャーナル: J.Mol.Biol. / 年: 2000タイトル: Solution structure of a DNA three-way junction containing two unpaired thymidine bases. Identification of sequence features that decide conformer selection. 著者: van Buuren, B.N. / Overmars, F.J. / Ippel, J.H. / Altona, C. / Wijmenga, S.S. #1:  ジャーナル: J.Mol.Biol. / 年: 1996 ジャーナル: J.Mol.Biol. / 年: 1996タイトル: NMR studies of DNA three-way junctions containing two unpaired thymidine bases: the influence of the sequence at the junction on the stability of the stacking conformers. 著者: Overmars, F.J. / Pikkemaat, J.A. / van den Elst, H. / van Boom, J.H. / Altona, C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1ezn.cif.gz 1ezn.cif.gz | 591.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1ezn.ent.gz pdb1ezn.ent.gz | 490.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1ezn.json.gz 1ezn.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ez/1ezn https://data.pdbj.org/pub/pdb/validation_reports/ez/1ezn ftp://data.pdbj.org/pub/pdb/validation_reports/ez/1ezn ftp://data.pdbj.org/pub/pdb/validation_reports/ez/1ezn | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 11053.049 Da / 分子数: 1 / 由来タイプ: 合成 |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR |
|---|---|
| NMR実験 | タイプ: 2D NOESY |
- 試料調製
試料調製
| 詳細 | 内容: 1mM DNA 3H; 50mM NaCl; / 溶媒系: D2O/H2O and D2O |
|---|---|
| 試料状態 | イオン強度: 50mM / pH: 7 / 圧: 1 atm / 温度: 293 K |
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| NMRスペクトロメーター | タイプ: Bruker AMX / 製造業者: Bruker / モデル: AMX / 磁場強度: 600 MHz |
|---|
- 解析
解析
| NMR software | 名称:  X-PLOR / バージョン: 3.851 / 開発者: Brunger / 分類: 精密化 X-PLOR / バージョン: 3.851 / 開発者: Brunger / 分類: 精密化 |
|---|---|
| 精密化 | 手法: torsion angle dynamics / ソフトェア番号: 1 |
| 代表構造 | 選択基準: lowest energy |
| NMRアンサンブル | コンフォーマー選択の基準: back calculated data agree with experimental NOESY spectrum,structures with acceptable covalent geometry,structures with the least restraint ...コンフォーマー選択の基準: back calculated data agree with experimental NOESY spectrum,structures with acceptable covalent geometry,structures with the least restraint violations,structures with the lowest energy 計算したコンフォーマーの数: 100 / 登録したコンフォーマーの数: 26 |
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj






































