+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9947 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of ASC CARD filament | |||||||||
 マップデータ マップデータ | None | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | filament / SIGNALING PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報NLRP6 inflammasome complex / myosin I binding / Pyrin domain binding / myeloid dendritic cell activation involved in immune response / positive regulation of antigen processing and presentation of peptide antigen via MHC class II / negative regulation of protein serine/threonine kinase activity / regulation of intrinsic apoptotic signaling pathway / myeloid dendritic cell activation / IkappaB kinase complex / The AIM2 inflammasome ...NLRP6 inflammasome complex / myosin I binding / Pyrin domain binding / myeloid dendritic cell activation involved in immune response / positive regulation of antigen processing and presentation of peptide antigen via MHC class II / negative regulation of protein serine/threonine kinase activity / regulation of intrinsic apoptotic signaling pathway / myeloid dendritic cell activation / IkappaB kinase complex / The AIM2 inflammasome / AIM2 inflammasome complex / icosanoid biosynthetic process / NLRP1 inflammasome complex / macropinocytosis / canonical inflammasome complex / interleukin-6 receptor binding / BMP receptor binding / NLRP3 inflammasome complex assembly / positive regulation of adaptive immune response / NLRP3 inflammasome complex / cysteine-type endopeptidase activator activity / CLEC7A/inflammasome pathway / negative regulation of interferon-beta production / osmosensory signaling pathway / regulation of tumor necrosis factor-mediated signaling pathway / positive regulation of extrinsic apoptotic signaling pathway / pattern recognition receptor signaling pathway / positive regulation of macrophage cytokine production / : / pattern recognition receptor activity / tropomyosin binding / pyroptotic inflammatory response / positive regulation of actin filament polymerization / positive regulation of release of cytochrome c from mitochondria / positive regulation of activated T cell proliferation / intrinsic apoptotic signaling pathway by p53 class mediator / positive regulation of interleukin-10 production / The NLRP3 inflammasome / cellular response to interleukin-1 / intrinsic apoptotic signaling pathway in response to DNA damage by p53 class mediator / positive regulation of T cell migration / : / Purinergic signaling in leishmaniasis infection / positive regulation of chemokine production / positive regulation of defense response to virus by host / negative regulation of canonical NF-kappaB signal transduction / negative regulation of cytokine production involved in inflammatory response / activation of innate immune response / intrinsic apoptotic signaling pathway / positive regulation of phagocytosis / tumor necrosis factor-mediated signaling pathway / positive regulation of interleukin-1 beta production / positive regulation of interleukin-8 production / positive regulation of JNK cascade / apoptotic signaling pathway / positive regulation of non-canonical NF-kappaB signal transduction / : / protein homooligomerization / positive regulation of T cell activation / regulation of protein stability / positive regulation of interleukin-6 production / positive regulation of type II interferon production / positive regulation of inflammatory response / positive regulation of tumor necrosis factor production / SARS-CoV-1 activates/modulates innate immune responses / azurophil granule lumen / cellular response to tumor necrosis factor / cellular response to lipopolysaccharide / regulation of inflammatory response / protease binding / secretory granule lumen / defense response to Gram-negative bacterium / defense response to virus / microtubule / transmembrane transporter binding / positive regulation of ERK1 and ERK2 cascade / positive regulation of canonical NF-kappaB signal transduction / protein dimerization activity / defense response to Gram-positive bacterium / regulation of autophagy / positive regulation of apoptotic process / inflammatory response / Golgi membrane / innate immune response / neuronal cell body / apoptotic process / Neutrophil degranulation / nucleolus / enzyme binding / endoplasmic reticulum / signal transduction / protein homodimerization activity / protein-containing complex / mitochondrion / extracellular region / nucleoplasm / identical protein binding / nucleus / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 4.1 Å | |||||||||
 データ登録者 データ登録者 | Gong Q / Xu C | |||||||||
| 資金援助 |  シンガポール, 1件 シンガポール, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Structural basis for distinct inflammasome complex assembly by human NLRP1 and CARD8. 著者: Qin Gong / Kim Robinson / Chenrui Xu / Phuong Thao Huynh / Kelvin Han Chung Chong / Eddie Yong Jun Tan / Jiawen Zhang / Zhao Zhi Boo / Daniel Eng Thiam Teo / Kenneth Lay / Yaming Zhang / John ...著者: Qin Gong / Kim Robinson / Chenrui Xu / Phuong Thao Huynh / Kelvin Han Chung Chong / Eddie Yong Jun Tan / Jiawen Zhang / Zhao Zhi Boo / Daniel Eng Thiam Teo / Kenneth Lay / Yaming Zhang / John Soon Yew Lim / Wah Ing Goh / Graham Wright / Franklin L Zhong / Bruno Reversade / Bin Wu /   要旨: Nod-like receptor (NLR) proteins activate pyroptotic cell death and IL-1 driven inflammation by assembling and activating the inflammasome complex. Closely related sensor proteins NLRP1 and CARD8 ...Nod-like receptor (NLR) proteins activate pyroptotic cell death and IL-1 driven inflammation by assembling and activating the inflammasome complex. Closely related sensor proteins NLRP1 and CARD8 undergo unique auto-proteolysis-dependent activation and are implicated in auto-inflammatory diseases; however, their mechanisms of activation are not understood. Here we report the structural basis of how the activating domains (FIIND-CARD) of NLRP1 and CARD8 self-oligomerize to assemble distinct inflammasome complexes. Recombinant FIIND-CARD of NLRP1 forms a two-layered filament, with an inner core of oligomerized CARD surrounded by an outer ring of FIIND. Biochemically, self-assembled NLRP1-CARD filaments are sufficient to drive ASC speck formation in cultured human cells-a process that is greatly enhanced by NLRP1-FIIND which forms oligomers in vitro. The cryo-EM structures of NLRP1-CARD and CARD8-CARD filaments, solved here at 3.7 Å, uncover unique structural features that enable NLRP1 and CARD8 to discriminate between ASC and pro-caspase-1. In summary, our findings provide structural insight into the mechanisms of activation for human NLRP1 and CARD8 and reveal how highly specific signaling can be achieved by heterotypic CARD interactions within the inflammasome complexes. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9947.map.gz emd_9947.map.gz | 2.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9947-v30.xml emd-9947-v30.xml emd-9947.xml emd-9947.xml | 18.3 KB 18.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_9947_fsc.xml emd_9947_fsc.xml | 4.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_9947.png emd_9947.png | 84 KB | ||
| Filedesc metadata |  emd-9947.cif.gz emd-9947.cif.gz | 5.7 KB | ||
| その他 |  emd_9947_additional.map.gz emd_9947_additional.map.gz emd_9947_half_map_1.map.gz emd_9947_half_map_1.map.gz emd_9947_half_map_2.map.gz emd_9947_half_map_2.map.gz | 562.2 KB 2.5 MB 2.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9947 http://ftp.pdbj.org/pub/emdb/structures/EMD-9947 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9947 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9947 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_9947_validation.pdf.gz emd_9947_validation.pdf.gz | 720.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_9947_full_validation.pdf.gz emd_9947_full_validation.pdf.gz | 719.9 KB | 表示 | |
| XML形式データ |  emd_9947_validation.xml.gz emd_9947_validation.xml.gz | 8.7 KB | 表示 | |
| CIF形式データ |  emd_9947_validation.cif.gz emd_9947_validation.cif.gz | 11.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9947 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9947 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9947 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9947 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9947.map.gz / 形式: CCP4 / 大きさ: 4.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9947.map.gz / 形式: CCP4 / 大きさ: 4.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | None | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
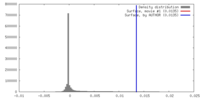
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
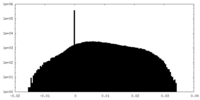
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: cropped 12mer from filament, used for model alignment...
| ファイル | emd_9947_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | cropped 12mer from filament, used for model alignment and refinement, not for publication | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_9947_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_9947_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : ASC CARD filament
| 全体 | 名称: ASC CARD filament |
|---|---|
| 要素 |
|
-超分子 #1: ASC CARD filament
| 超分子 | 名称: ASC CARD filament / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Apoptosis-associated speck-like protein containing a CARD
| 分子 | 名称: Apoptosis-associated speck-like protein containing a CARD タイプ: protein_or_peptide / ID: 1 / コピー数: 12 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 9.775143 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: LHFIDQHRAA LIARVTNVEW LLDALYGKVL TDEQYQAVRA EPTNPSKMRK LFSFTPAWNW TCKDLLLQAL RESQSYLVED LER UniProtKB: Apoptosis-associated speck-like protein containing a CARD |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 支持フィルム - Film thickness: 2 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK III |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 実像数: 3183 / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 最大 デフォーカス(補正後): 2.5 µm / 最小 デフォーカス(補正後): 1.5 µm / 照射モード: FLOOD BEAM / 撮影モード: DARK FIELD / Cs: 2.7 mm / 倍率(公称値): 115000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-6k99: |
 ムービー
ムービー コントローラー
コントローラー




























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)