+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Activated GluA4 homotetrameric AMPAR. | ||||||||||||
 マップデータ マップデータ | Full map of the GluA4 active state. | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | AMPAR / Ion Channel / Glutamate Receptor / Ligand-gated / MEMBRANE PROTEIN | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Presynaptic depolarization and calcium channel opening / LGI-ADAM interactions / Trafficking of AMPA receptors / eye blink reflex / positive regulation of protein localization to basolateral plasma membrane / cerebellar mossy fiber / postsynaptic neurotransmitter receptor diffusion trapping / regulation of AMPA receptor activity / Trafficking of AMPA receptors / kainate selective glutamate receptor complex ...Presynaptic depolarization and calcium channel opening / LGI-ADAM interactions / Trafficking of AMPA receptors / eye blink reflex / positive regulation of protein localization to basolateral plasma membrane / cerebellar mossy fiber / postsynaptic neurotransmitter receptor diffusion trapping / regulation of AMPA receptor activity / Trafficking of AMPA receptors / kainate selective glutamate receptor complex / channel regulator activity / membrane hyperpolarization / regulation of synapse structure or activity / nervous system process / Synaptic adhesion-like molecules / protein targeting to membrane / voltage-gated calcium channel complex / neurotransmitter receptor localization to postsynaptic specialization membrane / Activation of AMPA receptors / neuromuscular junction development / Trafficking of GluR2-containing AMPA receptors / AMPA glutamate receptor activity / negative regulation of smooth muscle cell apoptotic process / transmission of nerve impulse / AMPA glutamate receptor complex / ionotropic glutamate receptor complex / membrane depolarization / Unblocking of NMDA receptors, glutamate binding and activation / regulation of postsynaptic membrane neurotransmitter receptor levels / voltage-gated calcium channel activity / response to fungicide / positive regulation of synaptic transmission, glutamatergic / glutamate-gated receptor activity / somatodendritic compartment / presynaptic active zone membrane / ionotropic glutamate receptor binding / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / hippocampal mossy fiber to CA3 synapse / synaptic transmission, glutamatergic / regulation of membrane potential / transmitter-gated monoatomic ion channel activity involved in regulation of postsynaptic membrane potential / response to calcium ion / postsynaptic density membrane / modulation of chemical synaptic transmission / Schaffer collateral - CA1 synapse / terminal bouton / dendritic spine / chemical synaptic transmission / postsynaptic density / neuronal cell body / synapse / dendrite / glutamatergic synapse / cell surface / identical protein binding / plasma membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |   | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.31 Å | ||||||||||||
 データ登録者 データ登録者 | Hale WD / Huganir RL / Twomey EC | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Conformational Plasticity Tunes the GluA4 Channel Gate 著者: Hale WD / Huganir RL / Twomey EC | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_71405.map.gz emd_71405.map.gz | 230.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-71405-v30.xml emd-71405-v30.xml emd-71405.xml emd-71405.xml | 45.2 KB 45.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_71405.png emd_71405.png | 63.5 KB | ||
| Filedesc metadata |  emd-71405.cif.gz emd-71405.cif.gz | 7.2 KB | ||
| その他 |  emd_71405_additional_1.map.gz emd_71405_additional_1.map.gz emd_71405_additional_10.map.gz emd_71405_additional_10.map.gz emd_71405_additional_11.map.gz emd_71405_additional_11.map.gz emd_71405_additional_12.map.gz emd_71405_additional_12.map.gz emd_71405_additional_2.map.gz emd_71405_additional_2.map.gz emd_71405_additional_3.map.gz emd_71405_additional_3.map.gz emd_71405_additional_4.map.gz emd_71405_additional_4.map.gz emd_71405_additional_5.map.gz emd_71405_additional_5.map.gz emd_71405_additional_6.map.gz emd_71405_additional_6.map.gz emd_71405_additional_7.map.gz emd_71405_additional_7.map.gz emd_71405_additional_8.map.gz emd_71405_additional_8.map.gz emd_71405_additional_9.map.gz emd_71405_additional_9.map.gz emd_71405_half_map_1.map.gz emd_71405_half_map_1.map.gz emd_71405_half_map_2.map.gz emd_71405_half_map_2.map.gz | 230.3 MB 226.8 MB 120 MB 226.8 MB 226.3 MB 226.3 MB 120 MB 226.8 MB 120 MB 226.8 MB 226.8 MB 226.8 MB 226.5 MB 226.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-71405 http://ftp.pdbj.org/pub/emdb/structures/EMD-71405 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-71405 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-71405 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_71405.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_71405.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full map of the GluA4 active state. | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.93 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
+追加マップ: LBD/TMD map of the GluA4 active state used for model building.
+追加マップ: Half map A corresponding to NTD class 6.
+追加マップ: Map corresponding to NTD class 6.
+追加マップ: Map corresponding to NTD class 8.
+追加マップ: Half map A of the LBD/TMD map of...
+追加マップ: Half map B of the LBD/TMD map of...
+追加マップ: Half map A corresponding to NTD Class 9.
+追加マップ: Half map A corresponding to NTD class 8.
+追加マップ: Half map B corresponding to NTD class 8.
+追加マップ: Half map B corresponding to NTD Class 9.
+追加マップ: Half map B corresponding to NTD class 6.
+追加マップ: Map corresponding to NTD Class 9.
+ハーフマップ: Half map A of the full map of the GluA4 active state.
+ハーフマップ: Half map B of the full map of the GluA4 active state
- 試料の構成要素
試料の構成要素
-全体 : Octameric complex of four GluA4 subunits in complex with four TAR...
| 全体 | 名称: Octameric complex of four GluA4 subunits in complex with four TARP gamma 2 subunits. |
|---|---|
| 要素 |
|
-超分子 #1: Octameric complex of four GluA4 subunits in complex with four TAR...
| 超分子 | 名称: Octameric complex of four GluA4 subunits in complex with four TARP gamma 2 subunits. タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Isoform 2 of Glutamate receptor 4
| 分子 | 名称: Isoform 2 of Glutamate receptor 4 / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 95.140234 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MGKIMHISVL LSPVLWGLIF GVSSVQIGGL FIRNTDQEYT AFRLAIFLHN TSPNASEAPF NLVPHVDNIE TANSFAVTNA FCSQYSRGV FAIFGLYDKR SVHTLTSFCS ALHISLITPS FPTEGESQFV LQLRPSLRGA LLSLLDHYEW NCFVFLYDTD R GYSILQAI ...文字列: MGKIMHISVL LSPVLWGLIF GVSSVQIGGL FIRNTDQEYT AFRLAIFLHN TSPNASEAPF NLVPHVDNIE TANSFAVTNA FCSQYSRGV FAIFGLYDKR SVHTLTSFCS ALHISLITPS FPTEGESQFV LQLRPSLRGA LLSLLDHYEW NCFVFLYDTD R GYSILQAI MEKAGQNGWH VSAICVENFN DVSYRQLLEE LDRRQEKKFV IDCEIERLQN ILEQIVSVGK HVKGYHYIIA NL GFKDISL ERFIHGGANV TGFQLVDFNT PMVTKLMDRW KKLDQREYPG SETPPKYTSA LTYDGVLVMA ETFRSLRRQK IDI SRRGNA GDCLANPAAP WGQGIDMERT LKQVRIQGLT GNVQFDHYGR RVNYTMDVFE LKSTGPRKVG YWNDMDKLVL IQDM PTLGN DTAAIENRTV VVTTIMESPY VMYKKNHEMF EGNDKYEGYC VDLASEIAKH IGIKYKIAIV PDGKYGARDA DTKIW NGMV GELVYGKAEI AIAPLTITLV REEVIDFSKP FMSLGISIMI KKPQKSKPGV FSFLDPLAYE IWMCIVFAYI GVSVVL FLV SRFSPYEWHT EEPEDGKEGP SDQPPNEFGI FNSLWFSLGA FMQQGCDISP RSLSGRIVGG VWWFFTLIII SSYTANL AA FLTVERMVSP IESAEDLAKQ TEIAYGTLDS GSTKEFFRRS KIAVYEKMWT YMRSAEPSVF TRTTAEGVAR VRKSKGKF A FLLESTMNEY IEQRKPCDTM KVGGNLDSKG YGVATPKGSS LRTPVNLAVL KLSEAGVLDK LKNKWWYDKG ECGPKDSGS KDKTSALSLS NVAGVFYILV GGLGLAMLVA LIEFCYKSRA EAKRMK UniProtKB: Glutamate receptor 4 |
-分子 #2: Voltage-dependent calcium channel gamma-2 subunit
| 分子 | 名称: Voltage-dependent calcium channel gamma-2 subunit / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 23.066498 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GLFDRGVQML LTTVGAFAAF SLMTIAVGTD YWLYSRGVCK TKSVSEDETS KKNEEVMTHS GLWRTCCLEG NFKGLCKQID HFPEDADYE ADTAEYFLRA VRASSIFPIL SVILLFMGGL CIAASEFYKT RHNIILSAGI FFVSAGLSNI IGIIVYISAN A GDPSKSDS ...文字列: GLFDRGVQML LTTVGAFAAF SLMTIAVGTD YWLYSRGVCK TKSVSEDETS KKNEEVMTHS GLWRTCCLEG NFKGLCKQID HFPEDADYE ADTAEYFLRA VRASSIFPIL SVILLFMGGL CIAASEFYKT RHNIILSAGI FFVSAGLSNI IGIIVYISAN A GDPSKSDS KKNSYSYGWS FYFGALSFII AEMVGVLAVH MFIDRHKQLT G UniProtKB: Voltage-dependent calcium channel gamma-2 subunit |
-分子 #3: GLUTAMIC ACID
| 分子 | 名称: GLUTAMIC ACID / タイプ: ligand / ID: 3 / コピー数: 4 / 式: GLU |
|---|---|
| 分子量 | 理論値: 147.129 Da |
| Chemical component information |  ChemComp-GLU: |
-分子 #4: CYCLOTHIAZIDE
| 分子 | 名称: CYCLOTHIAZIDE / タイプ: ligand / ID: 4 / コピー数: 4 / 式: CYZ |
|---|---|
| 分子量 | 理論値: 389.878 Da |
| Chemical component information | 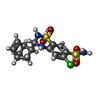 ChemComp-CYZ: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




































































































































