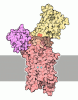
登録情報 データベース : EMDB / ID : EMD-65385タイトル cryo-EM structure of gastric proton pump bound to YK01 複合体 : pig gastric proton pump alpha-beta complexタンパク質・ペプチド : Sodium/potassium-transporting ATPase subunit alphaタンパク質・ペプチド : Potassium-transporting ATPase subunit betaリガンド : 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINEリガンド : MAGNESIUM IONリガンド : YK01-bリガンド : 2-acetamido-2-deoxy-beta-D-glucopyranoseリガンド : CHOLESTEROLリガンド : water / / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Sus scrofa (ブタ)手法 / / 解像度 : 2.66 Å Saito H / Abe K 資金援助 Organization Grant number 国 Japan Society for the Promotion of Science (JSPS) 24K01975
ジャーナル : Org Biomol Chem / 年 : 2026タイトル : Design, synthesis, and structural analysis of an inhibitor of the gastric proton pump with a diaza-tricyclic skeleton.著者 : Nariyoshi Umekubo / Airi Hashizume / Haruki Saito / Satoru Kato / Chisato Kanai / Chai C Gopalasingam / Christoph Gerle / Hideki Shigematsu / Atsushi Yoshimori / Kazuhiro Abe / Satoshi Yokoshima / 要旨 : The development of potent K-competitive acid blockers (P-CABs) as inhibitors of acid gastric secretion attracts much research attention. In this study, the structure-guided design and ... The development of potent K-competitive acid blockers (P-CABs) as inhibitors of acid gastric secretion attracts much research attention. In this study, the structure-guided design and enantioselective synthesis of P-CABs yielded a diaza-tricyclic compound with moderate inhibitory activity against the gastric proton pump. The eutomer was experimentally confirmed, consistent with pharmacophore predictions, and its binding mode to the gastric proton pump was elucidated cryo-electron microscopy. 履歴 登録 2025年7月16日 - ヘッダ(付随情報) 公開 2026年1月14日 - マップ公開 2026年1月14日 - 更新 2026年2月18日 - 現状 2026年2月18日 処理サイト : PDBj / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報
 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 日本, 1件
日本, 1件  引用
引用 ジャーナル: Org Biomol Chem / 年: 2026
ジャーナル: Org Biomol Chem / 年: 2026
 構造の表示
構造の表示 ダウンロードとリンク
ダウンロードとリンク emd_65385.map.gz
emd_65385.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-65385-v30.xml
emd-65385-v30.xml emd-65385.xml
emd-65385.xml EMDBヘッダ
EMDBヘッダ emd_65385_fsc.xml
emd_65385_fsc.xml FSCデータファイル
FSCデータファイル emd_65385.png
emd_65385.png emd_65385_msk_1.map
emd_65385_msk_1.map マスクマップ
マスクマップ emd-65385.cif.gz
emd-65385.cif.gz emd_65385_half_map_1.map.gz
emd_65385_half_map_1.map.gz emd_65385_half_map_2.map.gz
emd_65385_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-65385
http://ftp.pdbj.org/pub/emdb/structures/EMD-65385 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-65385
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-65385
 F&H 検索
F&H 検索 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_65385.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_65385.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_65385_msk_1.map
emd_65385_msk_1.map 試料の構成要素
試料の構成要素

 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Homo sapiens (ヒト)
Homo sapiens (ヒト)



 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X

























