+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | APLNR / JN241-9 / dimer / complex / STRUCTURAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報: / apelin receptor activity / apelin receptor signaling pathway / mechanoreceptor activity / regulation of gap junction assembly / vascular associated smooth muscle cell differentiation / atrioventricular valve development / positive regulation of G protein-coupled receptor internalization / regulation of body fluid levels / venous blood vessel development ...: / apelin receptor activity / apelin receptor signaling pathway / mechanoreceptor activity / regulation of gap junction assembly / vascular associated smooth muscle cell differentiation / atrioventricular valve development / positive regulation of G protein-coupled receptor internalization / regulation of body fluid levels / venous blood vessel development / positive regulation of cardiac muscle hypertrophy in response to stress / endocardial cushion formation / positive regulation of blood vessel endothelial cell proliferation involved in sprouting angiogenesis / coronary vasculature development / vasculature development / G protein-coupled peptide receptor activity / adult heart development / aorta development / negative regulation of cardiac muscle hypertrophy in response to stress / ventricular septum morphogenesis / blood vessel development / heart looping / vasculogenesis / gastrulation / Peptide ligand-binding receptors / positive regulation of release of sequestered calcium ion into cytosol / G protein-coupled receptor activity / adenylate cyclase-inhibiting G protein-coupled receptor signaling pathway / positive regulation of angiogenesis / heart development / signaling receptor activity / regulation of gene expression / angiogenesis / G alpha (i) signalling events / G protein-coupled receptor signaling pathway / negative regulation of gene expression / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.7 Å | |||||||||
 データ登録者 データ登録者 | Ji S / Wang W / Yang Y / Shen Q / Zhang Y | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer 著者: Ji S / Wang W / Yang Y / Shen Q / Zhang Y | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_63307.map.gz emd_63307.map.gz | 40.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-63307-v30.xml emd-63307-v30.xml emd-63307.xml emd-63307.xml | 16.8 KB 16.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_63307_fsc.xml emd_63307_fsc.xml | 10.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_63307.png emd_63307.png | 79.8 KB | ||
| マスクデータ |  emd_63307_msk_1.map emd_63307_msk_1.map | 42.9 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-63307.cif.gz emd-63307.cif.gz | 5.8 KB | ||
| その他 |  emd_63307_half_map_1.map.gz emd_63307_half_map_1.map.gz emd_63307_half_map_2.map.gz emd_63307_half_map_2.map.gz | 32.1 MB 32.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-63307 http://ftp.pdbj.org/pub/emdb/structures/EMD-63307 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-63307 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-63307 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9lqwMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_63307.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_63307.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.93 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_63307_msk_1.map emd_63307_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_63307_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_63307_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer
| 全体 | 名称: Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer
| 超分子 | 名称: Cryo-EM structure of the JN241-9-bound state 1b of APLNR homodimer タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Apelin receptor
| 分子 | 名称: Apelin receptor / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 42.696301 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MEEGGDFDNY YGADNQSECE YTDWKSSGAL IPAIYMLVFL LGTTGNGLVL WTVFRSSREK RRSADIFIAS LAVADLTFVV TLPLWATYT YRDYDWPFGT FFCKLSSYLI FVNMYASVFC LTGLSFDRYL AIVRPVANAR LRLRVSGAVA TAVLWVLAAL L AMPVMVLR ...文字列: MEEGGDFDNY YGADNQSECE YTDWKSSGAL IPAIYMLVFL LGTTGNGLVL WTVFRSSREK RRSADIFIAS LAVADLTFVV TLPLWATYT YRDYDWPFGT FFCKLSSYLI FVNMYASVFC LTGLSFDRYL AIVRPVANAR LRLRVSGAVA TAVLWVLAAL L AMPVMVLR TTGDLENTTK VQCYMDYSMV ATVSSEWAWE VGLGVSSTTV GFVVPFTIML TCYFFIAQTI AGHFRKERIE GL RKRRRLL SIIVVLVVTF ALCWMPYHLV KTLYMLGSLL HWPCDFDLFL MNIFPYCTCI SYVNSCLNPF LYAFFDPRFR QAC TSMLCC GQSRCAGTSH SSSGEKSASY SSGHSQGPGP NMGKGGEQMH EKSIPYSQET LVVD UniProtKB: Apelin receptor |
-分子 #2: JN241-9
| 分子 | 名称: JN241-9 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 13.929495 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: QVQLVESGGG SVQSGGSLTL SCAASGSTYS SHCMGWFRQA PGKEREGVAL MTRSRGTSYA DSVKGRFTIS QDNTKNILYL QMNSLKPED TAMYYCAAVP RAGIEYSGAY CKWNMKDSGS WGQGTQVTVS S |
-分子 #3: 1,2-DIACYL-SN-GLYCERO-3-PHOSHOCHOLINE
| 分子 | 名称: 1,2-DIACYL-SN-GLYCERO-3-PHOSHOCHOLINE / タイプ: ligand / ID: 3 / コピー数: 2 / 式: PCF |
|---|---|
| 分子量 | 理論値: 734.039 Da |
| Chemical component information | 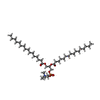 ChemComp-PCF: |
-分子 #4: CHOLESTEROL
| 分子 | 名称: CHOLESTEROL / タイプ: ligand / ID: 4 / コピー数: 16 / 式: CLR |
|---|---|
| 分子量 | 理論値: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 52.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)













































