+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of MPXV core protease in complex with aloxistatin(E64d) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ORTHOPOXVIRUSES / MONKEYPOX / PROTEASE / VIRAL REPLICATION / DRUG DISCOVERY / INHIBITOR / E64D / VIRAL PROTEIN | |||||||||
| 機能・相同性 | Peptidase C57, Vaccinia virus protein I7 / Vaccinia virus I7 processing peptidase / cysteine-type peptidase activity / Papain-like cysteine peptidase superfamily / virion component / proteolysis / MPXVgp068 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Monkeypox virus (サル痘ウイルス) Monkeypox virus (サル痘ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.93 Å | |||||||||
 データ登録者 データ登録者 | Lan W / You T / Li D / Dong X / Wang H / Xu J / Wang W / Gao Y / Yang H | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2025 ジャーナル: Nature / 年: 2025タイトル: Substrate recognition and cleavage mechanism of the monkeypox virus core protease. 著者: Yan Gao / Xiong Xie / Xiaoyu Zhang / Junyuan Cao / Weiqi Lan / Tian You / Dongxu Li / Xuxue Dong / Wenhao Dai / Yingchun Xiang / Shulei Hu / Weijuan Shang / Botao Wu / Yumin Zhang / Jin Xu / ...著者: Yan Gao / Xiong Xie / Xiaoyu Zhang / Junyuan Cao / Weiqi Lan / Tian You / Dongxu Li / Xuxue Dong / Wenhao Dai / Yingchun Xiang / Shulei Hu / Weijuan Shang / Botao Wu / Yumin Zhang / Jin Xu / Xiaoce Liu / Haofeng Wang / Wanlong Hu / Mingjing Zhang / Yinkai Duan / Wen Cui / Hao Zhou / Shengjiang Mao / Handi Jia / Zhanqi Sun / Menghan Jia / Yue Yin / Henry C Nguyen / Kailin Yang / Bei Yang / Xiuna Yang / Xiaoyun Ji / Gengfu Xiao / Wei Wang / Leike Zhang / Zihe Rao / Hong Liu / Haitao Yang /   要旨: Poxviruses cause severe diseases, including smallpox and mpox, that pose major threats to human health. The poxvirus core protease (Core) is essential for viral maturation and is highly conserved in ...Poxviruses cause severe diseases, including smallpox and mpox, that pose major threats to human health. The poxvirus core protease (Core) is essential for viral maturation and is highly conserved in poxviruses, making it an attractive antiviral target. However, the structure of Core remains unknown, hampering antiviral development. Here we determined the apo structure of monkeypox virus (MPXV) Core and the structure of Core in a complex with the inhibitor aloxistatin, a drug candidate for muscular dystrophy. These structures show that Core forms a homodimer that features a unique 'dancing couple' fold. The catalytic intermediate state of Core was characterized by an aldehyde derivative from a natural substrate (I-G18). This derivative binds covalently to the catalytic Cys328, shifting the active site of the viral protease from a closed conformation in the apo form to a favourable open conformation upon substrate binding. On the basis of the Core-I-G18 complex, we designed a series of peptidomimetic inhibitors with a nitrile warhead, which could covalently anchor with the catalytic Cys328. These compounds inhibit Core with half-maximal inhibitory concentrations of 44.9-100.3 nM, and exhibit potent and broad anti-poxvirus activity. Our studies provide a basis for designing wide-spectrum inhibitors against poxvirus infections. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_62516.map.gz emd_62516.map.gz | 78.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-62516-v30.xml emd-62516-v30.xml emd-62516.xml emd-62516.xml | 21.4 KB 21.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_62516.png emd_62516.png | 124.6 KB | ||
| Filedesc metadata |  emd-62516.cif.gz emd-62516.cif.gz | 6.7 KB | ||
| その他 |  emd_62516_half_map_1.map.gz emd_62516_half_map_1.map.gz emd_62516_half_map_2.map.gz emd_62516_half_map_2.map.gz | 77.5 MB 77.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-62516 http://ftp.pdbj.org/pub/emdb/structures/EMD-62516 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-62516 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-62516 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_62516_validation.pdf.gz emd_62516_validation.pdf.gz | 755.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_62516_full_validation.pdf.gz emd_62516_full_validation.pdf.gz | 755.3 KB | 表示 | |
| XML形式データ |  emd_62516_validation.xml.gz emd_62516_validation.xml.gz | 12.8 KB | 表示 | |
| CIF形式データ |  emd_62516_validation.cif.gz emd_62516_validation.cif.gz | 15.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-62516 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-62516 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-62516 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-62516 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9kqvMC  9jalC  9jamC  9janC  9jaqC  9kr6C  35539 M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_62516.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_62516.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.832 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_62516_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_62516_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : PROTEASE DIMER
| 全体 | 名称: PROTEASE DIMER |
|---|---|
| 要素 |
|
-超分子 #1: PROTEASE DIMER
| 超分子 | 名称: PROTEASE DIMER / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 / 詳細: MONKEYPOX I7 PORTEASE IS A DIMER |
|---|---|
| 由来(天然) | 生物種:  Monkeypox virus (サル痘ウイルス) Monkeypox virus (サル痘ウイルス) |
-分子 #1: Core protease I7
| 分子 | 名称: Core protease I7 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO EC番号: 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; システインプロテアーゼ |
|---|---|
| 由来(天然) | 生物種:  Monkeypox virus (サル痘ウイルス) Monkeypox virus (サル痘ウイルス) |
| 分子量 | 理論値: 49.088477 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MERYTDLVIS KIPELGFTNL LCHIYSLAGL CSNIDVSKFL TNCNGYVVEK YDKSTTAGKV SCIPIGMMLE LVESGHLSRP NSSDELDQK KELTDELTTR YHSIYDVFEL PTSIPLAYFF KPQLREKVSK AIDFSQMDLK IDDLSRKGIH TGENPKVVKM K IEPERGAW ...文字列: MERYTDLVIS KIPELGFTNL LCHIYSLAGL CSNIDVSKFL TNCNGYVVEK YDKSTTAGKV SCIPIGMMLE LVESGHLSRP NSSDELDQK KELTDELTTR YHSIYDVFEL PTSIPLAYFF KPQLREKVSK AIDFSQMDLK IDDLSRKGIH TGENPKVVKM K IEPERGAW MSNRSIKNLV SQFAYGSEVD YIGQFDMRFL NSLAIHEKFD AFMNKHILSY ILKDKIKSST SRFVMFGFCY LS HWKCVIY DKKQCLVSFY DSGGNIPTEF HHYNNFYFYS FSDGFNTNHR HSVLDNTNCD IDVLFRFFEC TFGAKIGCIN VEV NQLLES ECGMFISLFM ILCTRTPPKS FKSLKKVYTF FKFLADKKMT LFKSILFNLQ DLSLYITETD NAGLKEYKRM EKWT KKSIN VICDKLTTKL NRIVDDDE UniProtKB: MPXVgp068 |
-分子 #2: ethyl (3S)-3-hydroxy-4-({(2S)-4-methyl-1-[(3-methylbutyl)amino]-1...
| 分子 | 名称: ethyl (3S)-3-hydroxy-4-({(2S)-4-methyl-1-[(3-methylbutyl)amino]-1-oxopentan-2-yl}amino)-4-oxobutanoate タイプ: ligand / ID: 2 / コピー数: 2 / 式: E6D |
|---|---|
| 分子量 | 理論値: 344.446 Da |
| Chemical component information | 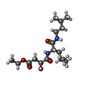 ChemComp-E6D: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析 #1
画像解析 #1
+ 画像解析 #2
画像解析 #2
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 162.1 |
|---|---|
| 得られたモデル |  PDB-9kqv: |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




































