+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-5370 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of full-length NSF in the ADP-AlFx state | |||||||||
 マップデータ マップデータ | NSF hexamer in the ADP-AlFx state | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | membrane fusion / AAA+ ATPase | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 9.2 Å | |||||||||
 データ登録者 データ登録者 | Chang LF / Chen S / Liu CC / Pan X / Jiang J / Bai XC / Xie X / Wang HW / Sui SF | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2012 ジャーナル: Nat Struct Mol Biol / 年: 2012タイトル: Structural characterization of full-length NSF and 20S particles. 著者: Lei-Fu Chang / Song Chen / Cui-Cui Liu / Xijiang Pan / Jiansen Jiang / Xiao-Chen Bai / Xin Xie / Hong-Wei Wang / Sen-Fang Sui /  要旨: The 20S particle, which is composed of the N-ethylmaleimide-sensitive factor (NSF), soluble NSF attachment proteins (SNAPs) and the SNAP receptor (SNARE) complex, has an essential role in ...The 20S particle, which is composed of the N-ethylmaleimide-sensitive factor (NSF), soluble NSF attachment proteins (SNAPs) and the SNAP receptor (SNARE) complex, has an essential role in intracellular vesicle fusion events. Using single-particle cryo-EM and negative stain EM, we reconstructed four related three-dimensional structures: Chinese hamster NSF hexamer in the ATPγS, ADP-AlFx and ADP states, and the 20S particle. These structures reveal a parallel arrangement between the D1 and D2 domains of the hexameric NSF and characterize the nucleotide-dependent conformational changes in NSF. The structure of the 20S particle shows that it holds the SNARE complex at two interaction interfaces around the C terminus and N-terminal half of the SNARE complex, respectively. These findings provide insight into the molecular mechanism underlying disassembly of the SNARE complex by NSF. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_5370.map.gz emd_5370.map.gz | 6.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-5370-v30.xml emd-5370-v30.xml emd-5370.xml emd-5370.xml | 7.3 KB 7.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_5370_1.jpg emd_5370_1.jpg | 181.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-5370 http://ftp.pdbj.org/pub/emdb/structures/EMD-5370 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5370 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5370 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_5370_validation.pdf.gz emd_5370_validation.pdf.gz | 77.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_5370_full_validation.pdf.gz emd_5370_full_validation.pdf.gz | 76.5 KB | 表示 | |
| XML形式データ |  emd_5370_validation.xml.gz emd_5370_validation.xml.gz | 492 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5370 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5370 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5370 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5370 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_5370.map.gz / 形式: CCP4 / 大きさ: 7.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_5370.map.gz / 形式: CCP4 / 大きさ: 7.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | NSF hexamer in the ADP-AlFx state | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
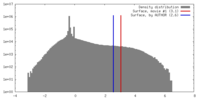
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : N-ethylmaleimide-sensitive factor (NSF)
| 全体 | 名称: N-ethylmaleimide-sensitive factor (NSF) |
|---|---|
| 要素 |
|
-超分子 #1000: N-ethylmaleimide-sensitive factor (NSF)
| 超分子 | 名称: N-ethylmaleimide-sensitive factor (NSF) / タイプ: sample / ID: 1000 / 詳細: The sample was freshly purified. / 集合状態: homohexamer / Number unique components: 1 |
|---|
-分子 #1: N-ethylmaleimide-sensitive factor
| 分子 | 名称: N-ethylmaleimide-sensitive factor / タイプ: protein_or_peptide / ID: 1 / Name.synonym: NSF / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  別称: Chinese hamster |
| 組換発現 | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 凍結 | 凍結剤: ETHANE / 装置: OTHER |
|---|
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 日付 | 2010年9月29日 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD |
| 試料ステージ | 試料ホルダー: CT3500 / 試料ホルダーモデル: OTHER |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 9.2 Å / 解像度の算出法: FSC 0.5 CUT-OFF |
|---|
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 精密化 | 空間: REAL |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)