+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-5227 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human 80S ribosomes in a cellular subtomogram | |||||||||
 マップデータ マップデータ | This is a tomographic subvolume containing ribosomes reconstructed from a peripheral cytosolic area of an untreated U87 MG cell, limited to 3s | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | human 80S ribosome / puromycin / in situ / cytosol / polysome / polyribosome / protein synthesis / translation / 3D cryoEM / tomography / cellular tomography | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 電子線トモグラフィー法 / クライオ電子顕微鏡法 / ネガティブ染色法 | |||||||||
 データ登録者 データ登録者 | Brandt F / Carlson L-A / Hartl FU / Baumeister W / Grunewald K | |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2010 ジャーナル: Mol Cell / 年: 2010タイトル: The three-dimensional organization of polyribosomes in intact human cells. 著者: Florian Brandt / Lars-Anders Carlson / F Ulrich Hartl / Wolfgang Baumeister / Kay Grünewald /  要旨: Structural studies have provided detailed insights into different functional states of the ribosome and its interaction with factors involved in nascent peptide folding, processing, and targeting. ...Structural studies have provided detailed insights into different functional states of the ribosome and its interaction with factors involved in nascent peptide folding, processing, and targeting. However, how the translational machinery is organized spatially in native cellular environments is not yet well understood. Here we have mapped individual ribosomes in electron tomograms of intact human cells by template matching and determined the average structure of the ribosome in situ. Characteristic features of active ribosomes in the cellular environment were assigned to the tRNA channel, elongation factors, and additional densities near the peptide tunnel. Importantly, the relative spatial configuration of neighboring ribosomes in the cell is clearly nonrandom. The preferred configurations are specific for active polysomes and were largely abrogated in puromycin-treated control cells. The distinct neighbor orientations found in situ resemble configurations of bacterial polysomes in vitro, indicating a conserved supramolecular organization with implications for nascent polypeptide folding. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_5227.map.gz emd_5227.map.gz | 19 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-5227-v30.xml emd-5227-v30.xml emd-5227.xml emd-5227.xml | 10.2 KB 10.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_5227_1.png emd_5227_1.png emd_5227_2.jpg emd_5227_2.jpg | 242.1 KB 235 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-5227 http://ftp.pdbj.org/pub/emdb/structures/EMD-5227 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5227 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5227 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_5227.map.gz / 形式: CCP4 / 大きさ: 20 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_5227.map.gz / 形式: CCP4 / 大きさ: 20 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | This is a tomographic subvolume containing ribosomes reconstructed from a peripheral cytosolic area of an untreated U87 MG cell, limited to 3s | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 16.4 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
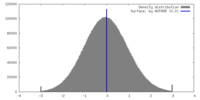
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Human 80S ribosomes, subtomogram of peripheral cytosol
| 全体 | 名称: Human 80S ribosomes, subtomogram of peripheral cytosol |
|---|---|
| 要素 |
|
-超分子 #1000: Human 80S ribosomes, subtomogram of peripheral cytosol
| 超分子 | 名称: Human 80S ribosomes, subtomogram of peripheral cytosol タイプ: sample / ID: 1000 / 詳細: Cellular ribosomes in situ / 集合状態: ca. 70-100 ribosomal particles / Number unique components: 1 |
|---|
-超分子 #1: Cytosol
| 超分子 | 名称: Cytosol / タイプ: organelle_or_cellular_component / ID: 1 / Name.synonym: Cytosolic ribosomes 詳細: Ca. 70-100 ribosomes within a subtomogram of the cytosol コピー数: 15 / 集合状態: polysome / 組換発現: No / データベース: NCBI |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 別称: Human / 細胞: U87MG / Organelle: Cytosol / 細胞中の位置: cytosolic Homo sapiens (ヒト) / 別称: Human / 細胞: U87MG / Organelle: Cytosol / 細胞中の位置: cytosolic |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線トモグラフィー法 |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 詳細: Cellular medium, DMEM (Gibco) supplemented with 10% foetal calf serum, 37C and 5% CO2 |
|---|---|
| 染色 | タイプ: NEGATIVE / 詳細: Cells grown on grids, vitrification |
| グリッド | 詳細: C-flat 2/1, holey carbon gold grid |
| 凍結 | 凍結剤: ETHANE / チャンバー内温度: 77 K / 装置: HOMEMADE PLUNGER 詳細: Vitrification instrument: plunger. Vitrification carried out in air 手法: Blot for 2 s before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI/PHILIPS CM300FEG/T |
|---|---|
| 温度 | 最低: 77 K / 最高: 77 K / 平均: 77 K |
| アライメント法 | Legacy - 非点収差: objective lens astigmatism was corrected at 50,000 times magnification |
| 特殊光学系 | エネルギーフィルター - 名称: GIF2002 エネルギーフィルター - エネルギー下限: 0.0 eV エネルギーフィルター - エネルギー上限: 20.0 eV |
| 日付 | 2008年7月3日 |
| 撮影 | カテゴリ: CCD / フィルム・検出器のモデル: GATAN MULTISCAN / 平均電子線量: 80 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 17500 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2 mm / 最大 デフォーカス(公称値): 6.0 µm / 最小 デフォーカス(公称値): 6.0 µm / 倍率(公称値): 17500 |
| 試料ステージ | 試料ホルダー: Side entry liquid nitrogen-cooled cryo specimen holder. 試料ホルダーモデル: GATAN LIQUID NITROGEN / Tilt series - Axis1 - Min angle: -65 ° / Tilt series - Axis1 - Max angle: 65 ° / Tilt series - Axis1 - Angle increment: 2 ° |
- 画像解析
画像解析
| 詳細 | Individual particle subvolumes were automatically selected by CCC threshold |
|---|---|
| 最終 再構成 | アルゴリズム: OTHER / ソフトウェア - 名称: EM / 詳細: exact weighting / 使用した粒子像数: 64 |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)