+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4703 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Thermus thermophilus V/A-type ATPase/synthase, rotational state 1R | |||||||||
 マップデータ マップデータ | A combined map from focused refinements of several domains of the intact complex as described in the paper. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ATP hydrolysis/synthesis / proton translocation / rotary catalysis / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報proton-transporting two-sector ATPase complex, catalytic domain / proton-transporting V-type ATPase, V0 domain / vacuolar proton-transporting V-type ATPase complex / vacuolar acidification / proton motive force-driven plasma membrane ATP synthesis / proton-transporting ATPase activity, rotational mechanism / H+-transporting two-sector ATPase / proton-transporting ATP synthase complex / proton-transporting ATP synthase activity, rotational mechanism / ATPase binding ...proton-transporting two-sector ATPase complex, catalytic domain / proton-transporting V-type ATPase, V0 domain / vacuolar proton-transporting V-type ATPase complex / vacuolar acidification / proton motive force-driven plasma membrane ATP synthesis / proton-transporting ATPase activity, rotational mechanism / H+-transporting two-sector ATPase / proton-transporting ATP synthase complex / proton-transporting ATP synthase activity, rotational mechanism / ATPase binding / ATP binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Thermus thermophilus HB8 (バクテリア) / Thermus thermophilus HB8 (バクテリア) /   Thermus thermophilus (strain HB8 / ATCC 27634 / DSM 579) (バクテリア) Thermus thermophilus (strain HB8 / ATCC 27634 / DSM 579) (バクテリア) | |||||||||
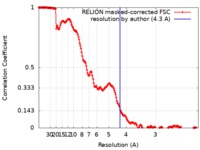
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.3 Å | |||||||||
 データ登録者 データ登録者 | Zhou L / Sazanov L | |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2019 ジャーナル: Science / 年: 2019タイトル: Structure and conformational plasticity of the intact V/A-type ATPase. 著者: Long Zhou / Leonid A Sazanov /  要旨: V (vacuolar)/A (archaeal)-type adenosine triphosphatases (ATPases), found in archaea and eubacteria, couple ATP hydrolysis or synthesis to proton translocation across the plasma membrane using the ...V (vacuolar)/A (archaeal)-type adenosine triphosphatases (ATPases), found in archaea and eubacteria, couple ATP hydrolysis or synthesis to proton translocation across the plasma membrane using the rotary-catalysis mechanism. They belong to the V-type ATPase family, which differs from the mitochondrial/chloroplast F-type ATP synthases in overall architecture. We solved cryo-electron microscopy structures of the intact V/A-ATPase, reconstituted into lipid nanodiscs, in three rotational states and two substates. These structures indicate substantial flexibility between V and V in a working enzyme, which results from mechanical competition between central shaft rotation and resistance from the peripheral stalks. We also describe details of adenosine diphosphate inhibition release, V-V torque transmission, and proton translocation, which are relevant for the entire V-type ATPase family. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4703.map.gz emd_4703.map.gz | 3.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4703-v30.xml emd-4703-v30.xml emd-4703.xml emd-4703.xml | 35.3 KB 35.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4703_fsc.xml emd_4703_fsc.xml | 17 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4703.png emd_4703.png | 158.9 KB | ||
| Filedesc metadata |  emd-4703.cif.gz emd-4703.cif.gz | 8.3 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4703 http://ftp.pdbj.org/pub/emdb/structures/EMD-4703 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4703 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4703 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4703_validation.pdf.gz emd_4703_validation.pdf.gz | 244.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4703_full_validation.pdf.gz emd_4703_full_validation.pdf.gz | 243.8 KB | 表示 | |
| XML形式データ |  emd_4703_validation.xml.gz emd_4703_validation.xml.gz | 12.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4703 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4703 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4703 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4703 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4703.map.gz / 形式: CCP4 / 大きさ: 15.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4703.map.gz / 形式: CCP4 / 大きさ: 15.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | A combined map from focused refinements of several domains of the intact complex as described in the paper. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.085 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
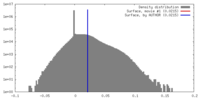
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Thermus thermophilus V/A-type ATPase/ATP synthase
+超分子 #1: Thermus thermophilus V/A-type ATPase/ATP synthase
+分子 #1: V-type ATP synthase alpha chain
+分子 #2: V-type ATP synthase beta chain
+分子 #3: V-type ATP synthase subunit D
+分子 #4: V-type ATP synthase subunit F
+分子 #5: V-type ATP synthase, subunit (VAPC-THERM)
+分子 #6: V-type ATP synthase subunit E
+分子 #7: V-type ATP synthase subunit C
+分子 #8: V-type ATP synthase subunit I
+分子 #9: V-type ATP synthase, subunit K
+分子 #10: MAGNESIUM ION
+分子 #11: ADENOSINE-5'-DIPHOSPHATE
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5.4 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| |||||||||||||||
| グリッド | モデル: Quantifoil R0.6/1 / 材質: COPPER / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 120 sec. | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 2700 / 平均露光時間: 63.0 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 最大 デフォーカス(補正後): 1.78 µm / 最小 デフォーカス(補正後): 0.5 µm / 倍率(補正後): 129032 / 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 空間: REAL / 温度因子: 167.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 得られたモデル |  PDB-6r10: |
 ムービー
ムービー コントローラー
コントローラー



















 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)