+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Vibrio cholerae FtsE Y20A mutant/FtsX/EnvC complex | |||||||||
 マップデータ マップデータ | full map_updated | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | membrane protein / enzyme / TRANSPORT PROTEIN | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.37 Å | |||||||||
 データ登録者 データ登録者 | Hao A / Lee S-Y | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2024 ジャーナル: Structure / 年: 2024タイトル: Structural insights into the FtsEX-EnvC complex regulation on septal peptidoglycan hydrolysis in Vibrio cholerae. 著者: Aili Hao / Yang Suo / Seok-Yong Lee /  要旨: During bacterial cell division, hydrolysis of septal peptidoglycan (sPG) is crucial for cell separation. This sPG hydrolysis is performed by the enzyme amidases whose activity is regulated by the ...During bacterial cell division, hydrolysis of septal peptidoglycan (sPG) is crucial for cell separation. This sPG hydrolysis is performed by the enzyme amidases whose activity is regulated by the integral membrane protein complex FtsEX-EnvC. FtsEX is an ATP-binding cassette transporter, and EnvC is a long coiled-coil protein that interacts with and activates the amidases. The molecular mechanism by which the FtsEX-EnvC complex activates amidases remains largely unclear. We present the cryo-electron microscopy structure of the FtsEX-EnvC complex from the pathogenic bacteria V. cholerae (FtsEX-EnvC). FtsEX-EnvC in the presence of ADP adopts a distinct conformation where EnvC is "horizontally extended" rather than "vertically extended". Subsequent structural studies suggest that EnvC can swing between these conformations in space in a nucleotide-dependent manner. Our structural analysis and functional studies suggest that FtsEX-EnvC employs spatial control of EnvC for amidase activation, providing mechanistic insights into the FtsEX-EnvC regulation on septal peptidoglycan hydrolysis. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41763.map.gz emd_41763.map.gz | 251.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41763-v30.xml emd-41763-v30.xml emd-41763.xml emd-41763.xml | 16.5 KB 16.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_41763.png emd_41763.png | 38.8 KB | ||
| マスクデータ |  emd_41763_msk_1.map emd_41763_msk_1.map | 512 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-41763.cif.gz emd-41763.cif.gz | 5.4 KB | ||
| その他 |  emd_41763_half_map_1.map.gz emd_41763_half_map_1.map.gz emd_41763_half_map_2.map.gz emd_41763_half_map_2.map.gz | 474.9 MB 475 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41763 http://ftp.pdbj.org/pub/emdb/structures/EMD-41763 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41763 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41763 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41763.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41763.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | full map_updated | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.08 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_41763_msk_1.map emd_41763_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
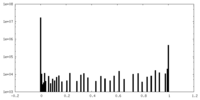
| 密度ヒストグラム |
-ハーフマップ: half map B updated
| ファイル | emd_41763_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map B_updated | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map A updated
| ファイル | emd_41763_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map A_updated | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : FtsEX
| 全体 | 名称: FtsEX |
|---|---|
| 要素 |
|
-超分子 #1: FtsEX
| 超分子 | 名称: FtsEX / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 200 KDa |
-分子 #1: FtsE
| 分子 | 名称: FtsE / タイプ: protein_or_peptide / ID: 1 / 光学異性体: DEXTRO |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
| 配列 | 文字列: PALSGGDGVI RFQQVSKAYR GGRQALQKVD FHLRRGEMAF LGGHSGAGKS TLLKLICAIE RPTDGKISFN GHDITRIPNK DIPFLRRNIG IVFQDHRLLM DRSIYDNVAL PMRIESISEN EIKRRVSAAL DKTGLLDKAR CLPSQLSGGE QQRVGIARAV VNRPTLLLAD ...文字列: PALSGGDGVI RFQQVSKAYR GGRQALQKVD FHLRRGEMAF LGGHSGAGKS TLLKLICAIE RPTDGKISFN GHDITRIPNK DIPFLRRNIG IVFQDHRLLM DRSIYDNVAL PMRIESISEN EIKRRVSAAL DKTGLLDKAR CLPSQLSGGE QQRVGIARAV VNRPTLLLAD EPTGNLDPEL SSRVLRLFEE FNRAGVTILL ATHDIHLVNS RPQYRHLELN QGFLSEVADY GR |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 8 mg/mL | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277 K / 装置: LEICA EM GP |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 1 / 平均露光時間: 2.4 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | Chain - Source name: AlphaFold / Chain - Initial model type: in silico model |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)