+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of Fab HC84.26-HCV E2 complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HCV / E2 / Fab / antiviral / complex / ANTIVIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報host cell lipid droplet / clathrin-dependent endocytosis of virus by host cell / host cell endoplasmic reticulum membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / virion membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  Hepacivirus C (ウイルス) Hepacivirus C (ウイルス) | |||||||||
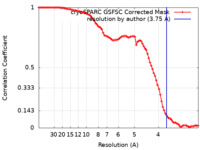
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.75 Å | |||||||||
 データ登録者 データ登録者 | Shahid S / Liqun J / LIu Y / Hasan SS / Mariuzza RA | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Commun Biol / 年: 2025 ジャーナル: Commun Biol / 年: 2025タイトル: Cryo-EM structures of HCV E2 glycoprotein bound to neutralizing and non-neutralizing antibodies determined using bivalent Fabs as fiducial markers. 著者: Salman Shahid / Sharanbasappa S Karade / S Saif Hasan / Rui Yin / Liqun Jiang / Yanxin Liu / Nathaniel Felbinger / Liudmila Kulakova / Eric A Toth / Zhen-Yong Keck / Steven K H Foung / Thomas ...著者: Salman Shahid / Sharanbasappa S Karade / S Saif Hasan / Rui Yin / Liqun Jiang / Yanxin Liu / Nathaniel Felbinger / Liudmila Kulakova / Eric A Toth / Zhen-Yong Keck / Steven K H Foung / Thomas R Fuerst / Brian G Pierce / Roy A Mariuzza /  要旨: Global elimination of hepatitis C virus (HCV) will require an effective cross-genotype vaccine. The HCV E2 envelope glycoprotein is the main target of neutralizing antibodies but also contains ...Global elimination of hepatitis C virus (HCV) will require an effective cross-genotype vaccine. The HCV E2 envelope glycoprotein is the main target of neutralizing antibodies but also contains epitopes that elicit non-neutralizing antibodies which may provide protection through Fc effector functions rather than direct neutralization. We determined cryo-EM structures of a broadly neutralizing antibody, a moderately neutralizing antibody, and a non-neutralizing antibody bound to E2 to resolutions of 3.8, 3.3, and 3.7 Å, respectively. Whereas the broadly neutralizing antibody targeted the front layer of E2 and the non-neutralizing antibody targeted the back layer, the moderately neutralizing antibody straddled both front and back layers, and thereby defined a new neutralizing epitope on E2. The small size of complexes between conventional (monovalent) Fabs and E2 (~110 kDa) presented a challenge for cryo-EM. Accordingly, we engineered bivalent versions of E2-specific Fabs that doubled the size of Fab-E2 complexes and conferred highly identifiable shapes to the complexes that facilitated particle selection and orientation for image processing. This study validates bivalent Fabs as new fiducial markers for cryo-EM analysis of small proteins such as HCV E2 and identifies a new target epitope for vaccine development. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41245.map.gz emd_41245.map.gz | 59.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41245-v30.xml emd-41245-v30.xml emd-41245.xml emd-41245.xml | 21.8 KB 21.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_41245_fsc.xml emd_41245_fsc.xml | 9.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_41245.png emd_41245.png | 164.5 KB | ||
| Filedesc metadata |  emd-41245.cif.gz emd-41245.cif.gz | 7 KB | ||
| その他 |  emd_41245_half_map_1.map.gz emd_41245_half_map_1.map.gz emd_41245_half_map_2.map.gz emd_41245_half_map_2.map.gz | 59.5 MB 59.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41245 http://ftp.pdbj.org/pub/emdb/structures/EMD-41245 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41245 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41245 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_41245_validation.pdf.gz emd_41245_validation.pdf.gz | 818.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_41245_full_validation.pdf.gz emd_41245_full_validation.pdf.gz | 817.9 KB | 表示 | |
| XML形式データ |  emd_41245_validation.xml.gz emd_41245_validation.xml.gz | 16.3 KB | 表示 | |
| CIF形式データ |  emd_41245_validation.cif.gz emd_41245_validation.cif.gz | 21.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41245 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41245 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41245 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41245 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8tgvMC  8tfeC  8tgzC  8thzC  8txqC  8tzyC  8u9yC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41245.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41245.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.4875 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_41245_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_41245_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : HCV E2-HC84.26 complex
| 全体 | 名称: HCV E2-HC84.26 complex |
|---|---|
| 要素 |
|
-超分子 #1: HCV E2-HC84.26 complex
| 超分子 | 名称: HCV E2-HC84.26 complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 340 KDa |
-分子 #1: envelope glycoprotein E2
| 分子 | 名称: envelope glycoprotein E2 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Hepacivirus C (ウイルス) Hepacivirus C (ウイルス) |
| 分子量 | 理論値: 32.28726 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: METDTLLLWV LLLWVPGSTG DSTHVTGGTA SHTTRHFASL FSSGASQRVQ LINTNGSWHI NRTALNCNDS LHTGFLAALF YTHKFNASG CPERMAHCRP IDEFAQGWGP ITYAEGHGSD QRPYCWHYAP RQCGTIPASQ VCGPVYCFTP SPVVVGTTDR F GAPTYTWG ...文字列: METDTLLLWV LLLWVPGSTG DSTHVTGGTA SHTTRHFASL FSSGASQRVQ LINTNGSWHI NRTALNCNDS LHTGFLAALF YTHKFNASG CPERMAHCRP IDEFAQGWGP ITYAEGHGSD QRPYCWHYAP RQCGTIPASQ VCGPVYCFTP SPVVVGTTDR F GAPTYTWG ENETDVLILN NTRPPQGNWF GCTWMNSTGF TKTCGGPPCN IGGVGNNTLT CPTDCFRKHP EATYTKCGSG PW LTPRCLV DYPYRLWHYP CTVNFTIFKV RMYVGGVEHR LNAACNIGHH HHHH UniProtKB: Genome polyprotein |
-分子 #2: HC84.26 Heavy chain
| 分子 | 名称: HC84.26 Heavy chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 27.304617 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: METDTLLLWV LLLWVPGSTG DQVQPVQSGA EVKKPGSSVK VSCEASGGTH SNYVITWVRQ APGQGLEWMG GFIPDFRTAM YAQGFQGRV TITADESTSL AYMELTNLRS EDTAVYYCAR GPLSRGYYDY WGPGTLVTVS ASTKGPSVFP LAPSSKSTSG G TAALGCLV ...文字列: METDTLLLWV LLLWVPGSTG DQVQPVQSGA EVKKPGSSVK VSCEASGGTH SNYVITWVRQ APGQGLEWMG GFIPDFRTAM YAQGFQGRV TITADESTSL AYMELTNLRS EDTAVYYCAR GPLSRGYYDY WGPGTLVTVS ASTKGPSVFP LAPSSKSTSG G TAALGCLV KDYFPEPVTV SWNSGALTSG VHTFPAVLQS SGLYSLSSVV TVPSSSLGTQ TYICNVNHKP SNTKVDKRVE PK SCDKTAG WSHPQFEK |
-分子 #3: HC84.26 Light chain
| 分子 | 名称: HC84.26 Light chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25.35215 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: METDTLLLWV LLLWVPGSTG DSYVLTQPPS VSVAPGQTAS ITCSGDKLGD KYVSWYQQRP GQSPVLVLYQ DSKRPSGIPE RFSGSNSGN TATLTISGTQ AMDEADYYCQ AWDSSALVFG GGTKLTVLRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF Y PREAKVQW ...文字列: METDTLLLWV LLLWVPGSTG DSYVLTQPPS VSVAPGQTAS ITCSGDKLGD KYVSWYQQRP GQSPVLVLYQ DSKRPSGIPE RFSGSNSGN TATLTISGTQ AMDEADYYCQ AWDSSALVFG GGTKLTVLRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF Y PREAKVQW KVDNALQSGN SQESVTEQDS KDSTYSLSST LTLSKADYEK HKVYACEVTH QGLSSPVTKS FNRGEC |
-分子 #6: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 6 / コピー数: 1 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL |
|---|---|
| 緩衝液 | pH: 8 / 詳細: 20 mM Tris-HCl pH 8.0, 100 mM NaCl |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 9653 / 平均露光時間: 3.8 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 81000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)