+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of BtKY72 spike receptor-binding domain (RBD) complexed with bat ACE2 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | BtKY72 RBD ACE2 bat / VIRAL PROTEIN | |||||||||
| 生物種 |   Rhinolophus landeri (ランダーキクガシラコウモリ) Rhinolophus landeri (ランダーキクガシラコウモリ) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Su C / Qi JX / Gao GF | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: mBio / 年: 2024 ジャーナル: mBio / 年: 2024タイトル: Structural characteristics of BtKY72 RBD bound to bat ACE2 reveal multiple key residues affecting ACE2 usage of sarbecoviruses. 著者: Chao Su / Juanhua He / Liang Wang / Yu Hu / Jian Cao / Bin Bai / Jianxun Qi / George Fu Gao / Mengsu Yang / Qihui Wang /  要旨: Two different sarbecoviruses, severe acute respiratory syndrome coronavirus (SARS-CoV) and SARS-CoV-2, have caused serious challenges to public health. Certain sarbecoviruses utilize angiotensin- ...Two different sarbecoviruses, severe acute respiratory syndrome coronavirus (SARS-CoV) and SARS-CoV-2, have caused serious challenges to public health. Certain sarbecoviruses utilize angiotensin-converting enzyme 2 (ACE2) as their cellular receptor, whereas some do not, speculatively due to the two deletions in their receptor-binding domain (RBD). However, it remains unclear whether sarbecoviruses with one deletion in the RBD can still bind to ACE2. Here, we showed that two phylogenetically related sarbecoviruses with one deletion, BtKY72 and BM48-31, displayed a different ACE2-usage range. The cryo-electron microscopy structure of BtKY72 RBD bound to bat ACE2 identified a key residue important for the interaction between RBD and ACE2. In addition, we demonstrated that the mutations involving four types of core residues enabled the sarbecoviruses with deletion(s) to bind to human ACE2 (hACE2) and broadened the ACE2 usage of SARS-CoV-2. Our findings help predict the potential hACE2-binding ability to emerge sarbecoviruses and develop pan-sarbecovirus therapeutic agents. IMPORTANCE: Many sarbecoviruses, including severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2), possess the ability to bind to receptor angiotensin-converting enzyme 2 (ACE2) through their ...IMPORTANCE: Many sarbecoviruses, including severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2), possess the ability to bind to receptor angiotensin-converting enzyme 2 (ACE2) through their receptor-binding domain (RBD). However, certain sarbecoviruses with deletion(s) in the RBD lack this capability. In this study, we investigated two closely related short-deletion sarbecoviruses, BtKY72 and BM48-31, and revealed that BtKY72 exhibited a broader ACE2-binding spectrum compared to BM48-31. Structural analysis of the BtKY72 RBD-bat ACE2 complex identifies a critical residue at position 493 contributing to these differences. Furthermore, we demonstrated that the mutations involving four core residues in the RBD enabled the sarbecoviruses with deletion(s) to bind to human ACE2 and expanded the ACE2 usage spectra of SARS-CoV-2. These findings offer crucial insights for accurately predicting the potential threat of newly emerging sarbecoviruses to human health. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_36892.map.gz emd_36892.map.gz | 167.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-36892-v30.xml emd-36892-v30.xml emd-36892.xml emd-36892.xml | 19.2 KB 19.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_36892.png emd_36892.png | 31 KB | ||
| Filedesc metadata |  emd-36892.cif.gz emd-36892.cif.gz | 6.4 KB | ||
| その他 |  emd_36892_half_map_1.map.gz emd_36892_half_map_1.map.gz emd_36892_half_map_2.map.gz emd_36892_half_map_2.map.gz | 165.4 MB 165.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-36892 http://ftp.pdbj.org/pub/emdb/structures/EMD-36892 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36892 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36892 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_36892.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_36892.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.669 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_36892_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
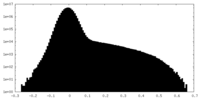
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_36892_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Structure of BtKY72 spike receptor-binding domain (RBD) complexed...
| 全体 | 名称: Structure of BtKY72 spike receptor-binding domain (RBD) complexed with bat ACE2 |
|---|---|
| 要素 |
|
-超分子 #1: Structure of BtKY72 spike receptor-binding domain (RBD) complexed...
| 超分子 | 名称: Structure of BtKY72 spike receptor-binding domain (RBD) complexed with bat ACE2 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #2: BtKY72 RBD
| 超分子 | 名称: BtKY72 RBD / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Rhinolophus landeri (ランダーキクガシラコウモリ) Rhinolophus landeri (ランダーキクガシラコウモリ) |
-超分子 #3: Bat ACE2
| 超分子 | 名称: Bat ACE2 / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|
-分子 #1: BtKY72
| 分子 | 名称: BtKY72 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 25.514703 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: RVSPSTEVVR FPNITNLCPF GQVFNASNFP SVYAWERLRI SDCVADYAVL YNSSSSFSTF KCYGVSPTKL NDLCFSSVYA DYFVVKGDD VRQIAPAQTG VIADYNYKLP DDFTGCVLAW NTNSVDSKSG NNFYYRLFRH GKIKPYERDI SNVLYNSAGG T CSSISQLG ...文字列: RVSPSTEVVR FPNITNLCPF GQVFNASNFP SVYAWERLRI SDCVADYAVL YNSSSSFSTF KCYGVSPTKL NDLCFSSVYA DYFVVKGDD VRQIAPAQTG VIADYNYKLP DDFTGCVLAW NTNSVDSKSG NNFYYRLFRH GKIKPYERDI SNVLYNSAGG T CSSISQLG CYEPLKSYGF TPTVGVGYQP YRVVVLSFEL LNAPATVCGP KKSTELVKNK CVNFHHHHHH |
-分子 #2: ACE2
| 分子 | 名称: ACE2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Rhinolophus landeri (ランダーキクガシラコウモリ) Rhinolophus landeri (ランダーキクガシラコウモリ) |
| 分子量 | 理論値: 69.443156 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: STPEDLAKTF LDDFNSAAEN LSYQSSLASW EYNTNISDEN IQKMDEAGAK WSDFYETQSK HAKNFSLEEI HNDTVKLQLQ ILQQSGSPV LSEDKSKRLN SILNAMSTIY STGKVCRPNN PQECLLLEPG LDNIMGTSKD YNERLWAWEG WRAEVGKQLR P LYEEYVVL ...文字列: STPEDLAKTF LDDFNSAAEN LSYQSSLASW EYNTNISDEN IQKMDEAGAK WSDFYETQSK HAKNFSLEEI HNDTVKLQLQ ILQQSGSPV LSEDKSKRLN SILNAMSTIY STGKVCRPNN PQECLLLEPG LDNIMGTSKD YNERLWAWEG WRAEVGKQLR P LYEEYVVL KNEMARGYHY EDYGDYWRRD YETEGSPDLE YSRDQLTKDV ERIFAEIKPL YEQLHAYVRA KLMDTYPFHI SP TGCLPAH LLGDMWGRFW TNLYPLTVPF GQKPNIDVTD AMLNQTWDAK RIFKEAEKFF VSIGLPHMTE GFWNNSMLTD PGD GRKVVC HPTAWDLGKG DFRIKMCTKV TMEDFLTAHH EMGHIQYDMA YASQPYLLRN GANEGFHEAV GEVMSLSVAT PKHL KTMGL LSPDFLEDNE TEINFLFKQA LTIVGTLPFT YMLEKWRWMV FKGEIPKEEW MTKWWEMKRK IVGVVEPVPH DETYC DPAS LFHVANDYSF IRYYTRTIFE FQFHEALCRI AKHDGPLHKC DISNSTDAGK KLHQMLSVGK SQPWTSVLKD FVDSKD MDV GPLLRYFEPL YTWLKEQNRN SFVGWNTDWS PHAD |
-分子 #3: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 3 / コピー数: 1 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)