+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of mTIP60-Ba (metal-ion induced TIP60 (K67E) complex with barium ions | |||||||||||||||
 マップデータ マップデータ | Sharpened map by post-processing | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | Artificial designed protein complex / Protein cage / Protein nanoparticle / Metal-induced protein assembly / Protein metal complex / DE NOVO PROTEIN | |||||||||||||||
| 生物種 | synthetic construct (人工物) | |||||||||||||||
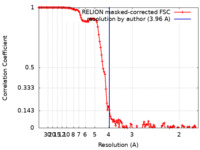
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.96 Å | |||||||||||||||
 データ登録者 データ登録者 | Ohara N / Kawakami N / Arai R / Adachi N / Moriya T / Kawasaki M / Miyamoto K | |||||||||||||||
| 資金援助 |  日本, 4件 日本, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Chem Commun (Camb) / 年: 2021 ジャーナル: Chem Commun (Camb) / 年: 2021タイトル: Icosahedral 60-meric porous structure of designed supramolecular protein nanoparticle TIP60. 著者: Junya Obata / Norifumi Kawakami / Akihisa Tsutsumi / Erika Nasu / Kenji Miyamoto / Masahide Kikkawa / Ryoichi Arai /  要旨: Supramolecular protein nanoparticles and nanocages have potential in a broad range of applications. Recently, we developed a uniform supramolecular protein nanoparticle, TIP60, symmmetrically self- ...Supramolecular protein nanoparticles and nanocages have potential in a broad range of applications. Recently, we developed a uniform supramolecular protein nanoparticle, TIP60, symmmetrically self-assembled from fusion proteins of a pentameric Sm-like protein and a dimeric MyoX-coil domain. Herein, we report the icosahedral 60-meric structure of TIP60 solved using single-particle cryo-electron microscopy. Interestingly, the structure revealed 20 regular-triangle-like pores on the surface. TIP60 and its mutants have many modifiable sites on their exterior and interior surfaces. The TIP60 architecture will be useful in the development of biomedical and biochemical nanoparticles/nanocages for future applications. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_33289.map.gz emd_33289.map.gz | 165.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-33289-v30.xml emd-33289-v30.xml emd-33289.xml emd-33289.xml | 25.4 KB 25.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_33289_fsc.xml emd_33289_fsc.xml | 12.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_33289.png emd_33289.png | 102.3 KB | ||
| マスクデータ |  emd_33289_msk_1.map emd_33289_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-33289.cif.gz emd-33289.cif.gz | 6.9 KB | ||
| その他 |  emd_33289_additional_1.map.gz emd_33289_additional_1.map.gz emd_33289_half_map_1.map.gz emd_33289_half_map_1.map.gz emd_33289_half_map_2.map.gz emd_33289_half_map_2.map.gz | 137.4 MB 139.4 MB 139.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-33289 http://ftp.pdbj.org/pub/emdb/structures/EMD-33289 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33289 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33289 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_33289_validation.pdf.gz emd_33289_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_33289_full_validation.pdf.gz emd_33289_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_33289_validation.xml.gz emd_33289_validation.xml.gz | 20 KB | 表示 | |
| CIF形式データ |  emd_33289_validation.cif.gz emd_33289_validation.cif.gz | 26.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33289 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33289 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33289 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33289 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_33289.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_33289.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map by post-processing | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.88 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_33289_msk_1.map emd_33289_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Raw full map
| ファイル | emd_33289_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Raw full map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_33289_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_33289_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : mTIP60-Ba
| 全体 | 名称: mTIP60-Ba |
|---|---|
| 要素 |
|
-超分子 #1: mTIP60-Ba
| 超分子 | 名称: mTIP60-Ba / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 詳細: metal-ion induced TIP60 (truncated icosahedral protein composed of 60-mer fusion proteins) complexed with barium ions |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 1.074 MDa |
-分子 #1: TIP60 K67E mutant
| 分子 | 名称: TIP60 K67E mutant / タイプ: protein_or_peptide / ID: 1 / コピー数: 60 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 17.79416 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGSSHHHHHH SQDPKNIKIM RLVTGEDIIG NISESQGLIT IKKAFVIIPM QATPGKPVQL VLSPWQPYTD DKEIVIDDSE VITITSPKD DIIKSYESHT RVLENKQVEE ILRLEKEIED LQRMKEQQEL SLTEASLQKL QERRDQELRR LEEE |
-分子 #2: BARIUM ION
| 分子 | 名称: BARIUM ION / タイプ: ligand / ID: 2 / コピー数: 60 / 式: BA |
|---|---|
| 分子量 | 理論値: 137.327 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR / 詳細: The grid was washed by acetone prior to use. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 291 K / 装置: FEI VITROBOT MARK IV / 詳細: Blotting time was 15 seconds (blot force 5). |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 2206 / 平均露光時間: 66.42 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 120000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A / Chain - Residue range: 2-136 / Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 精密化 | 空間: REAL / プロトコル: OTHER / 温度因子: 22.77 / 当てはまり具合の基準: Correlation coefficient |
| 得られたモデル |  PDB-7xm1: |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)