+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Streptomyces coelicolor zinc uptake regulator complexed with zinc and DNA (trimer of dimers) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | DNA BINDING PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of secondary metabolite biosynthetic process / DNA-binding transcription repressor activity / protein-DNA complex / transcription cis-regulatory region binding / DNA-binding transcription factor activity / negative regulation of DNA-templated transcription / zinc ion binding / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Streptomyces coelicolor A3(2) (バクテリア) / Streptomyces coelicolor A3(2) (バクテリア) /  Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) (バクテリア) Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Yang X / Zheng J | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2022 ジャーナル: Nucleic Acids Res / 年: 2022タイトル: Structural basis of Streptomyces transcription activation by zinc uptake regulator. 著者: Xu Yang / Yiqun Wang / Guiyang Liu / Zixin Deng / Shuangjun Lin / Jianting Zheng /  要旨: Streptomyces coelicolor (Sc) is a model organism of actinobacteria to study morphological differentiation and production of bioactive metabolites. Sc zinc uptake regulator (Zur) affects both ...Streptomyces coelicolor (Sc) is a model organism of actinobacteria to study morphological differentiation and production of bioactive metabolites. Sc zinc uptake regulator (Zur) affects both processes by controlling zinc homeostasis. It activates transcription by binding to palindromic Zur-box sequences upstream of -35 elements. Here we deciphered the molecular mechanism by which ScZur interacts with promoter DNA and Sc RNA polymerase (RNAP) by cryo-EM structures and biochemical assays. The ScZur-DNA structures reveal a sequential and cooperative binding of three ScZur dimers surrounding a Zur-box spaced 8 nt upstream from a -35 element. The ScRNAPσHrdB-Zur-DNA structures define protein-protein and protein-DNA interactions involved in the principal housekeeping σHrdB-dependent transcription initiation from a noncanonical promoter with a -10 element lacking the critical adenine residue at position -11 and a TTGCCC -35 element deviating from the canonical TTGACA motif. ScZur interacts with the C-terminal domain of ScRNAP α subunit (αCTD) in a complex structure trapped in an active conformation. Key ScZur-αCTD interfacial residues accounting for ScZur-dependent transcription activation were confirmed by mutational studies. Together, our structural and biochemical results provide a comprehensive model for transcription activation of Zur family regulators. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
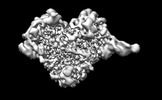
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32048.map.gz emd_32048.map.gz | 1.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32048-v30.xml emd-32048-v30.xml emd-32048.xml emd-32048.xml | 18.1 KB 18.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32048_fsc.xml emd_32048_fsc.xml | 13.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32048.png emd_32048.png | 57.3 KB | ||
| マスクデータ |  emd_32048_msk_1.map emd_32048_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-32048.cif.gz emd-32048.cif.gz | 5.8 KB | ||
| その他 |  emd_32048_half_map_1.map.gz emd_32048_half_map_1.map.gz emd_32048_half_map_2.map.gz emd_32048_half_map_2.map.gz | 95.7 MB 95.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32048 http://ftp.pdbj.org/pub/emdb/structures/EMD-32048 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32048 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32048 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_32048_validation.pdf.gz emd_32048_validation.pdf.gz | 620.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_32048_full_validation.pdf.gz emd_32048_full_validation.pdf.gz | 619.8 KB | 表示 | |
| XML形式データ |  emd_32048_validation.xml.gz emd_32048_validation.xml.gz | 17.2 KB | 表示 | |
| CIF形式データ |  emd_32048_validation.cif.gz emd_32048_validation.cif.gz | 22.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32048 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32048 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32048 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32048 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7vo0MC  7vo9C  7vpdC  7vpzC  7x74C  7x75C  7x76C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32048.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32048.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_32048_msk_1.map emd_32048_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_32048_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_32048_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Zur-DNA
| 全体 | 名称: Zur-DNA |
|---|---|
| 要素 |
|
-超分子 #1: Zur-DNA
| 超分子 | 名称: Zur-DNA / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Streptomyces coelicolor A3(2) (バクテリア) Streptomyces coelicolor A3(2) (バクテリア) |
| 分子量 | 理論値: 250 kDa/nm |
-分子 #1: DNA_NT (84-MER)
| 分子 | 名称: DNA_NT (84-MER) / タイプ: dna / ID: 1 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  Streptomyces coelicolor A3(2) (バクテリア) Streptomyces coelicolor A3(2) (バクテリア) |
| 分子量 | 理論値: 25.808424 KDa |
| 配列 | 文字列: (DC)(DA)(DA)(DG)(DG)(DC)(DA)(DC)(DA)(DT) (DG)(DA)(DC)(DA)(DA)(DC)(DG)(DG)(DT)(DG) (DT)(DT)(DC)(DA)(DG)(DT)(DG)(DC)(DC) (DG)(DC)(DG)(DT)(DT)(DG)(DC)(DC)(DC)(DG) (DA) (DT)(DA)(DC)(DC)(DC) ...文字列: (DC)(DA)(DA)(DG)(DG)(DC)(DA)(DC)(DA)(DT) (DG)(DA)(DC)(DA)(DA)(DC)(DG)(DG)(DT)(DG) (DT)(DT)(DC)(DA)(DG)(DT)(DG)(DC)(DC) (DG)(DC)(DG)(DT)(DT)(DG)(DC)(DC)(DC)(DG) (DA) (DT)(DA)(DC)(DC)(DC)(DC)(DC)(DT) (DA)(DC)(DC)(DC)(DG)(DT)(DA)(DG)(DT)(DT) (DG)(DA) (DC)(DT)(DG)(DG)(DC)(DA)(DT) (DC)(DC)(DG)(DG)(DG)(DC)(DG)(DC)(DC)(DG) (DG)(DG)(DT) (DC)(DG)(DC)(DC) GENBANK: GENBANK: AL939129.1 |
-分子 #2: DNA_T (84-MER)
| 分子 | 名称: DNA_T (84-MER) / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  Streptomyces coelicolor A3(2) (バクテリア) Streptomyces coelicolor A3(2) (バクテリア) |
| 分子量 | 理論値: 26.008541 KDa |
| 配列 | 文字列: (DG)(DG)(DC)(DG)(DA)(DC)(DC)(DC)(DG)(DG) (DC)(DG)(DC)(DC)(DG)(DC)(DC)(DT)(DA)(DC) (DG)(DG)(DT)(DC)(DA)(DG)(DT)(DA)(DC) (DT)(DA)(DC)(DG)(DG)(DG)(DT)(DA)(DG)(DG) (DG) (DG)(DG)(DT)(DA)(DT) ...文字列: (DG)(DG)(DC)(DG)(DA)(DC)(DC)(DC)(DG)(DG) (DC)(DG)(DC)(DC)(DG)(DC)(DC)(DT)(DA)(DC) (DG)(DG)(DT)(DC)(DA)(DG)(DT)(DA)(DC) (DT)(DA)(DC)(DG)(DG)(DG)(DT)(DA)(DG)(DG) (DG) (DG)(DG)(DT)(DA)(DT)(DC)(DG)(DG) (DG)(DC)(DA)(DA)(DC)(DG)(DC)(DG)(DG)(DC) (DA)(DC) (DT)(DG)(DA)(DA)(DC)(DA)(DC) (DC)(DG)(DT)(DT)(DG)(DT)(DC)(DA)(DT)(DG) (DT)(DG)(DC) (DC)(DT)(DT)(DG) |
-分子 #3: Putative metal uptake regulation protein
| 分子 | 名称: Putative metal uptake regulation protein / タイプ: protein_or_peptide / ID: 3 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) (バクテリア) Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) (バクテリア)株: ATCC BAA-471 / A3(2) / M145 |
| 分子量 | 理論値: 16.90484 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGSSHHHHHH SSGLVPRGSH MTTAGPPVKG RATRQRAAVS AALQEVEEFR SAQELHDMLK HKGDAVGLTT VYRTLQSLAD AGEVDVLRT AEGESVYRRC STGDHHHHLV CRACGKAVEV EGPAVEKWAE AIAAEHGYVN VAHTVEIFGT CADCAGASGG UniProtKB: Zinc uptake regulation protein |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 18 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.8 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 289 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法 #1
電子顕微鏡法 #1
| Microscopy ID | 1 |
|---|---|
| 顕微鏡 | FEI TITAN KRIOS |
| 撮影 | Image recording ID: 1 フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 平均電子線量: 1.25 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 電子顕微鏡法 #1~
電子顕微鏡法 #1~
| Microscopy ID | 1 |
|---|---|
| 顕微鏡 | FEI TITAN KRIOS |
| 撮影 | Image recording ID: 2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 1.25 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)