+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of iSAT large ribosomal subunit assembly intermediate - Class B2 | ||||||||||||
 マップデータ マップデータ | Class B2 iSAT 50S Ribosomal Intermediate | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | 50S subunit / assembly intermediate / in vitro / RIBOSOME | ||||||||||||
| 生物種 |  | ||||||||||||
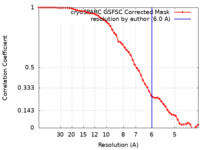
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.0 Å | ||||||||||||
 データ登録者 データ登録者 | Dong X / Doerfel LK / Sheng K / Rabuck-Gibbons JN / Popova AM / Lyumkis D / Williamson JR | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2023 ジャーナル: Nucleic Acids Res / 年: 2023タイトル: Near-physiological in vitro assembly of 50S ribosomes involves parallel pathways. 著者: Xiyu Dong / Lili K Doerfel / Kai Sheng / Jessica N Rabuck-Gibbons / Anna M Popova / Dmitry Lyumkis / James R Williamson /  要旨: Understanding the assembly principles of biological macromolecular complexes remains a significant challenge, due to the complexity of the systems and the difficulties in developing experimental ...Understanding the assembly principles of biological macromolecular complexes remains a significant challenge, due to the complexity of the systems and the difficulties in developing experimental approaches. As a ribonucleoprotein complex, the ribosome serves as a model system for the profiling of macromolecular complex assembly. In this work, we report an ensemble of large ribosomal subunit intermediate structures that accumulate during synthesis in a near-physiological and co-transcriptional in vitro reconstitution system. Thirteen pre-50S intermediate maps covering the entire assembly process were resolved using cryo-EM single-particle analysis and heterogeneous subclassification. Segmentation of the set of density maps reveals that the 50S ribosome intermediates assemble based on fourteen cooperative assembly blocks, including the smallest assembly core reported to date, which is composed of a 600-nucleotide-long folded rRNA and three ribosomal proteins. The cooperative blocks assemble onto the assembly core following defined dependencies, revealing the parallel pathways at both early and late assembly stages of the 50S subunit. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29042.map.gz emd_29042.map.gz | 8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29042-v30.xml emd-29042-v30.xml emd-29042.xml emd-29042.xml | 19.8 KB 19.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_29042_fsc.xml emd_29042_fsc.xml | 5.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_29042.png emd_29042.png | 79 KB | ||
| Filedesc metadata |  emd-29042.cif.gz emd-29042.cif.gz | 4.7 KB | ||
| その他 |  emd_29042_half_map_1.map.gz emd_29042_half_map_1.map.gz emd_29042_half_map_2.map.gz emd_29042_half_map_2.map.gz | 14.5 MB 14.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29042 http://ftp.pdbj.org/pub/emdb/structures/EMD-29042 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29042 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29042 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29042_validation.pdf.gz emd_29042_validation.pdf.gz | 905.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29042_full_validation.pdf.gz emd_29042_full_validation.pdf.gz | 905.1 KB | 表示 | |
| XML形式データ |  emd_29042_validation.xml.gz emd_29042_validation.xml.gz | 12.5 KB | 表示 | |
| CIF形式データ |  emd_29042_validation.cif.gz emd_29042_validation.cif.gz | 15.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29042 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29042 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29042 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29042 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29042.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29042.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Class B2 iSAT 50S Ribosomal Intermediate | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.096 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: Class B2 iSAT 50S Ribosomal Intermediate - Half Map 1
| ファイル | emd_29042_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Class B2 iSAT 50S Ribosomal Intermediate - Half Map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
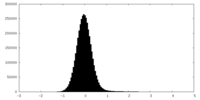
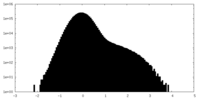
| 密度ヒストグラム |
-ハーフマップ: Class B2 iSAT 50S Ribosomal Intermediate - Half Map 2
| ファイル | emd_29042_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Class B2 iSAT 50S Ribosomal Intermediate - Half Map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
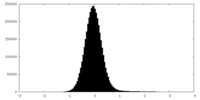
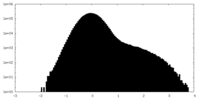
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : iSAT large ribosomal subunit assembly intermediate (Class B2)
| 全体 | 名称: iSAT large ribosomal subunit assembly intermediate (Class B2) |
|---|---|
| 要素 |
|
-超分子 #1: iSAT large ribosomal subunit assembly intermediate (Class B2)
| 超分子 | 名称: iSAT large ribosomal subunit assembly intermediate (Class B2) タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
詳細: Most of the sucrose was removed by spin concentration. | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 80 % / チャンバー内温度: 298 K / 装置: GATAN CRYOPLUNGE 3 / 詳細: 3 microliter of the sample was added.. | ||||||||||||||||||
| 詳細 | The in vitro assembled large ribosomal subunit was purified by sucrose gradient and was spin-concentrated in a 100 kDa MW-cutoff filter. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 詳細 | In order to account for highly preferred orientation of the specimen, data were acquired using tilts ranging from 10-60 degrees, in addition to untilted images at 0 degrees. The CTF was estimated on a per-particle basis to account for the gradient of CTF values across individual micrographs |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3710 pixel / デジタル化 - サイズ - 縦: 3838 pixel / デジタル化 - 画像ごとのフレーム数: 1-50 / 実像数: 4607 / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 22500 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)