+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Chikungunya virus asymmetric unit | |||||||||
 マップデータ マップデータ | chikv_asu_165.mrc | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | CHIKV asymmetric unit / VIRUS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報T=4 icosahedral viral capsid / host cell cytoplasm / serine-type endopeptidase activity / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / host cell plasma membrane / virion membrane / structural molecule activity / proteolysis / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Chikungunya virus (チクングニヤウイルス) Chikungunya virus (チクングニヤウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.09 Å | |||||||||
 データ登録者 データ登録者 | Su GC / Chmielewsk D / Kaelber J / Pintilie G / Chen M / Jin J / Auguste A / Chiu W | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: PNAS Nexus / 年: 2024 ジャーナル: PNAS Nexus / 年: 2024タイトル: Cryogenic electron microscopy and tomography reveal imperfect icosahedral symmetry in alphaviruses. 著者: David Chmielewski / Guan-Chin Su / Jason T Kaelber / Grigore D Pintilie / Muyuan Chen / Jing Jin / Albert J Auguste / Wah Chiu /  要旨: Alphaviruses are spherical, enveloped RNA viruses with two-layered icosahedral architecture. The structures of many alphaviruses have been studied using cryogenic electron microscopy (cryo-EM) ...Alphaviruses are spherical, enveloped RNA viruses with two-layered icosahedral architecture. The structures of many alphaviruses have been studied using cryogenic electron microscopy (cryo-EM) reconstructions, which impose icosahedral symmetry on the viral particles. Using cryogenic electron tomography (cryo-ET), we revealed a polarized symmetry defect in the icosahedral lattice of Chikungunya virus (CHIKV) in situ, similar to the late budding particles, suggesting the inherent imperfect symmetry originates from the final pinch-off of assembled virions. We further demonstrated this imperfect symmetry is also present in in vitro purified CHIKV and Mayaro virus, another arthritogenic alphavirus. We employed a subparticle-based single-particle analysis protocol to circumvent the icosahedral imperfection and boosted the resolution of the structure of the CHIKV to ∼3 Å resolution, which revealed detailed molecular interactions between glycoprotein E1-E2 heterodimers in the transmembrane region and multiple lipid-like pocket factors located in a highly conserved hydrophobic pocket. This complementary use of in situ cryo-ET and single-particle cryo-EM approaches provides a more precise structural description of near-icosahedral viruses and valuable insights to guide the development of structure-based antiviral therapies against alphaviruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28979.map.gz emd_28979.map.gz | 2.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28979-v30.xml emd-28979-v30.xml emd-28979.xml emd-28979.xml | 21.6 KB 21.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_28979_fsc.xml emd_28979_fsc.xml | 24.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_28979.png emd_28979.png | 146 KB | ||
| Filedesc metadata |  emd-28979.cif.gz emd-28979.cif.gz | 7.1 KB | ||
| その他 |  emd_28979_half_map_1.map.gz emd_28979_half_map_1.map.gz emd_28979_half_map_2.map.gz emd_28979_half_map_2.map.gz | 146.4 MB 146.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28979 http://ftp.pdbj.org/pub/emdb/structures/EMD-28979 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28979 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28979 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_28979_validation.pdf.gz emd_28979_validation.pdf.gz | 884.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_28979_full_validation.pdf.gz emd_28979_full_validation.pdf.gz | 883.9 KB | 表示 | |
| XML形式データ |  emd_28979_validation.xml.gz emd_28979_validation.xml.gz | 23.6 KB | 表示 | |
| CIF形式データ |  emd_28979_validation.cif.gz emd_28979_validation.cif.gz | 31.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28979 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28979 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28979 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28979 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28979.map.gz / 形式: CCP4 / 大きさ: 17.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28979.map.gz / 形式: CCP4 / 大きさ: 17.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | chikv_asu_165.mrc | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.352 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: run half2 class001 unfil.mrc
| ファイル | emd_28979_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | run_half2_class001_unfil.mrc | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
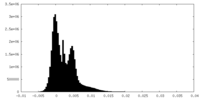
| 密度ヒストグラム |
-ハーフマップ: run half2 class001 unfil.mrc
| ファイル | emd_28979_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | run_half2_class001_unfil.mrc | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
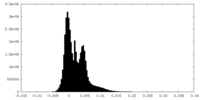
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Chikungunya virus
| 全体 | 名称:   Chikungunya virus (チクングニヤウイルス) Chikungunya virus (チクングニヤウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Chikungunya virus
| 超分子 | 名称: Chikungunya virus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 / NCBI-ID: 37124 / 生物種: Chikungunya virus / Sci species strain: vaccine strain 181/clone 25 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|---|
| 分子量 | 理論値: 500 KDa |
| ウイルス殻 | Shell ID: 1 / 直径: 700.0 Å / T番号(三角分割数): 4 |
-分子 #1: E1 glycoprotein
| 分子 | 名称: E1 glycoprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO / EC番号: togavirin |
|---|---|
| 由来(天然) | 生物種:   Chikungunya virus (チクングニヤウイルス) Chikungunya virus (チクングニヤウイルス)株: vaccine strain 181/clone 25 |
| 分子量 | 理論値: 47.497906 KDa |
| 配列 | 文字列: YEHVTVIPNT VGVPYKTLVN RPGYSPMVLE MELLSVTLEP TLSLDYITCE YKTVIPSPYV KCCGTAECKD KSLPDYSCKV FTGVYPFMW GGAYCFCDTE NTQLSEAHVE KSESCKTEFA SAYRAHTASA SAKLRVLYQG NNVTVSAYAN GDHAVTVKDA K FIVGPMSS ...文字列: YEHVTVIPNT VGVPYKTLVN RPGYSPMVLE MELLSVTLEP TLSLDYITCE YKTVIPSPYV KCCGTAECKD KSLPDYSCKV FTGVYPFMW GGAYCFCDTE NTQLSEAHVE KSESCKTEFA SAYRAHTASA SAKLRVLYQG NNVTVSAYAN GDHAVTVKDA K FIVGPMSS AWTPFDNKIV VYKGDVYNMD YPPFGAGRPG QFGDIQSRTP ESEDVYANTQ LVLQRPSAGT VHVPYSQAPS GF KYWLKER GASLQHTAPF GCQIATNPVR AMNCAVGNMP ISIDIPDAAF TRVVDAPSLT DMSCEVPACT HSSDFGGVAI IKY AASKKG KCAVHSMTNA VTIREAEIEV EGNSQLQISF STALASAEFR VQVCSTQVHC AAECHPPKDH IVNYPASHTT LGVQ DISVT AMSWVQKITG GVGLVVAVAA LILIVVLCVS FSRH UniProtKB: Structural polyprotein |
-分子 #2: E2 glycoprotein
| 分子 | 名称: E2 glycoprotein / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO / EC番号: togavirin |
|---|---|
| 由来(天然) | 生物種:   Chikungunya virus (チクングニヤウイルス) Chikungunya virus (チクングニヤウイルス)株: vaccine strain 181/clone 25 |
| 分子量 | 理論値: 47.077719 KDa |
| 配列 | 文字列: NFNVYKAIRP YLAHCPDCGE GHSCHSPVAL ERIRNEATDG TLKIQVSLQI GIKTDDSHDW TKLRYMDNHM PADAERARLF VRTSAPCTI TGTMGHFILA RCPKGETLTV GFTDGRKISH SCTHPFHHDP PVIGREKFHS RPQHGRELPC STYAQSTAAT A EEIEVHMP ...文字列: NFNVYKAIRP YLAHCPDCGE GHSCHSPVAL ERIRNEATDG TLKIQVSLQI GIKTDDSHDW TKLRYMDNHM PADAERARLF VRTSAPCTI TGTMGHFILA RCPKGETLTV GFTDGRKISH SCTHPFHHDP PVIGREKFHS RPQHGRELPC STYAQSTAAT A EEIEVHMP PDTPDRTLMS QQSGNVKITV NSQTVRYKCN CGDSNEGLTT TDKVINNCKV DQCHAAVTNH KKWQYNSPLV PR NAELGDR KGKVHIPFPL ANVTCRVPKA RNPTVTYGKN QVIMLLYPDH PTLLSYRNMG EEPNYQEEWV THKKEIRLTV PTE GLEVTW GNNEPYKYWP QLSTNGTAHG HPHEIILYYY ELYPTMTVVV VSVASFVLLS MVGVAVGMCM CARRRCITPY ELTP GATVP FLLSLICCIR TAKA UniProtKB: Structural polyprotein |
-分子 #3: Capsid protein
| 分子 | 名称: Capsid protein / タイプ: protein_or_peptide / ID: 3 / コピー数: 4 / 光学異性体: LEVO / EC番号: togavirin |
|---|---|
| 由来(天然) | 生物種:   Chikungunya virus (チクングニヤウイルス) Chikungunya virus (チクングニヤウイルス)株: vaccine strain 181/clone 25 |
| 分子量 | 理論値: 16.428607 KDa |
| 配列 | 文字列: NDCIFEVKHE GKVTGYACLV GDKVMKPAHV KGTIDNADLA KLAFKRSSKY DLECAQIPVH MKSDASKFTH EKPEGYYNWH HGAVQYSGG RFTIPTGAGK PGDSGRPIFD NKGRVVAIVL GGANEGARTA LSVVTWNKDI VTKITPEGAE EW UniProtKB: Structural polyprotein |
-分子 #4: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 4 / コピー数: 5 / 式: PCW |
|---|---|
| 分子量 | 理論値: 787.121 Da |
| Chemical component information |  ChemComp-PCW: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 構成要素:
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 支持フィルム - Film thickness: 2 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 25 sec. | ||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 293.15 K / 装置: LEICA EM GP |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 47.25 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 106000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)