+ Open data
Open data
- Basic information
Basic information
| Entry |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Type I-C Cas4-Cas1-Cas2 complex bound to a PAM/NoPAM prespacer | |||||||||
 Map data Map data | ||||||||||
 Sample Sample |
| |||||||||
 Keywords Keywords | CRISPR Cas adaptation type I-C / HYDROLASE-DNA complex | |||||||||
| Function / homology |  Function and homology information Function and homology information5' to 3' exodeoxyribonuclease (nucleoside 3'-phosphate-forming) / exonuclease activity / maintenance of CRISPR repeat elements / iron-sulfur cluster binding / RNA endonuclease activity / DNA endonuclease activity / defense response to virus / Hydrolases; Acting on ester bonds / hydrolase activity / magnesium ion binding ...5' to 3' exodeoxyribonuclease (nucleoside 3'-phosphate-forming) / exonuclease activity / maintenance of CRISPR repeat elements / iron-sulfur cluster binding / RNA endonuclease activity / DNA endonuclease activity / defense response to virus / Hydrolases; Acting on ester bonds / hydrolase activity / magnesium ion binding / protein homodimerization activity / DNA binding / metal ion binding Similarity search - Function | |||||||||
| Biological species |  Alkalihalobacillus halodurans C-125 (bacteria) / synthetic construct (others) Alkalihalobacillus halodurans C-125 (bacteria) / synthetic construct (others) | |||||||||
| Method | single particle reconstruction / cryo EM / Resolution: 3.9 Å | |||||||||
 Authors Authors | Dhingra Y / Suresh SK / Juneja P / Sashital DG | |||||||||
| Funding support |  United States, 2 items United States, 2 items
| |||||||||
 Citation Citation |  Journal: Mol Cell / Year: 2022 Journal: Mol Cell / Year: 2022Title: PAM binding ensures orientational integration during Cas4-Cas1-Cas2-mediated CRISPR adaptation. Authors: Yukti Dhingra / Shravanti K Suresh / Puneet Juneja / Dipali G Sashital /  Abstract: Adaptation in CRISPR-Cas systems immunizes bacteria and archaea against mobile genetic elements. In many DNA-targeting systems, the Cas4-Cas1-Cas2 complex is required for selection and processing of ...Adaptation in CRISPR-Cas systems immunizes bacteria and archaea against mobile genetic elements. In many DNA-targeting systems, the Cas4-Cas1-Cas2 complex is required for selection and processing of DNA segments containing PAM sequences prior to integration of these "prespacer" substrates as spacers in the CRISPR array. We determined cryo-EM structures of the Cas4-Cas1-Cas2 adaptation complex from the type I-C system that encodes standalone Cas1 and Cas4 proteins. The structures reveal how Cas4 specifically reads out bases within the PAM sequence and how interactions with both Cas1 and Cas2 activate Cas4 endonuclease activity. The Cas4-PAM interaction ensures tight binding between the adaptation complex and the prespacer, significantly enhancing integration of the non-PAM end into the CRISPR array and ensuring correct spacer orientation. Corroborated with our biochemical results, Cas4-Cas1-Cas2 structures with substrates representing various stages of CRISPR adaptation reveal a temporally resolved mechanism for maturation and integration of functional spacers into the CRISPR array. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Supplemental images |
|---|
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_27162.map.gz emd_27162.map.gz | 128.4 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-27162-v30.xml emd-27162-v30.xml emd-27162.xml emd-27162.xml | 22.7 KB 22.7 KB | Display Display |  EMDB header EMDB header |
| Images |  emd_27162.png emd_27162.png | 81 KB | ||
| Filedesc metadata |  emd-27162.cif.gz emd-27162.cif.gz | 6.8 KB | ||
| Others |  emd_27162_half_map_1.map.gz emd_27162_half_map_1.map.gz emd_27162_half_map_2.map.gz emd_27162_half_map_2.map.gz | 200.7 MB 200.7 MB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27162 http://ftp.pdbj.org/pub/emdb/structures/EMD-27162 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27162 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27162 | HTTPS FTP |
-Related structure data
| Related structure data |  8d3qMC  8d3lC  8d3mC  8d3pC C: citing same article ( M: atomic model generated by this map |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| Related items in Molecule of the Month |
- Map
Map
| File |  Download / File: emd_27162.map.gz / Format: CCP4 / Size: 149.9 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_27162.map.gz / Format: CCP4 / Size: 149.9 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 0.9063 Å | ||||||||||||||||||||||||||||||||||||
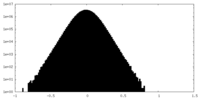
| Density |
| ||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
|
-Supplemental data
-Half map: #2
| File | emd_27162_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
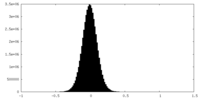
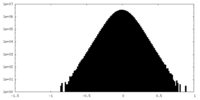
| Density Histograms |
-Half map: #1
| File | emd_27162_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
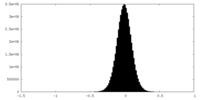
| Density Histograms |
- Sample components
Sample components
-Entire : Type I-C Cas4-Cas1-Cas2 complex with a PAM/Processed substrate
| Entire | Name: Type I-C Cas4-Cas1-Cas2 complex with a PAM/Processed substrate |
|---|---|
| Components |
|
-Supramolecule #1: Type I-C Cas4-Cas1-Cas2 complex with a PAM/Processed substrate
| Supramolecule | Name: Type I-C Cas4-Cas1-Cas2 complex with a PAM/Processed substrate type: complex / ID: 1 / Parent: 0 / Macromolecule list: #1-#5 |
|---|---|
| Source (natural) | Organism:  Alkalihalobacillus halodurans C-125 (bacteria) Alkalihalobacillus halodurans C-125 (bacteria) |
-Macromolecule #1: CRISPR-associated endonuclease Cas1
| Macromolecule | Name: CRISPR-associated endonuclease Cas1 / type: protein_or_peptide / ID: 1 / Number of copies: 4 / Enantiomer: LEVO / EC number: Hydrolases; Acting on ester bonds |
|---|---|
| Source (natural) | Organism:  Alkalihalobacillus halodurans C-125 (bacteria) Alkalihalobacillus halodurans C-125 (bacteria)Strain: ATCC BAA-125 / DSM 18197 / FERM 7344 / JCM 9153 / C-125 |
| Molecular weight | Theoretical: 39.39334 KDa |
| Recombinant expression | Organism:  |
| Sequence | String: MKKLLNTLYV TQPDTYLSLD GDNVVLLKEQ EKLGRLPLHN LEAIVGFGYT GASPALMGYC AERNISITFL TKNGRFLARV VGESRGNVV LRKTQYRISE NDQESTKIAR NFITGKVYNS KWMLERMTRE HPLRVNVEQF KATSQLLSVM MQEIRNCDSL E SLRGWEGQ ...String: MKKLLNTLYV TQPDTYLSLD GDNVVLLKEQ EKLGRLPLHN LEAIVGFGYT GASPALMGYC AERNISITFL TKNGRFLARV VGESRGNVV LRKTQYRISE NDQESTKIAR NFITGKVYNS KWMLERMTRE HPLRVNVEQF KATSQLLSVM MQEIRNCDSL E SLRGWEGQ AAINYNKVFD QMILQQKEEF AFHGRSRRPP KDNVNAMLSF AYTLLANDVA AALETVGLDA YVGFMHQDRP GR ASLALDL MEELRGLYAD RFVLSLINRK EMTADGFYKK ENGAVLMTDE ARKTFLKAWQ TKKQEKITHP YLGEKMSWGL VPY VQALLL ARFLRGDLDE YPPFLWK UniProtKB: CRISPR-associated endonuclease Cas1 |
-Macromolecule #2: CRISPR-associated endonuclease Cas2
| Macromolecule | Name: CRISPR-associated endonuclease Cas2 / type: protein_or_peptide / ID: 2 / Number of copies: 2 / Enantiomer: LEVO / EC number: Hydrolases; Acting on ester bonds |
|---|---|
| Source (natural) | Organism:  Alkalihalobacillus halodurans C-125 (bacteria) Alkalihalobacillus halodurans C-125 (bacteria)Strain: ATCC BAA-125 / DSM 18197 / FERM 7344 / JCM 9153 / C-125 |
| Molecular weight | Theoretical: 11.038668 KDa |
| Recombinant expression | Organism:  |
| Sequence | String: GSMLVLITYD VQTSSMGGTK RLRKVAKACQ NYGQRVQNSV FECIVDSTQL TSLKLELTSL IDEEKDSLRI YRLGNNYKTK VEHIGAKPS IDLEDPLIF UniProtKB: CRISPR-associated endonuclease Cas2 |
-Macromolecule #5: CRISPR-associated exonuclease Cas4
| Macromolecule | Name: CRISPR-associated exonuclease Cas4 / type: protein_or_peptide / ID: 5 / Number of copies: 2 / Enantiomer: LEVO EC number: 5' to 3' exodeoxyribonuclease (nucleoside 3'-phosphate-forming) |
|---|---|
| Source (natural) | Organism:  Alkalihalobacillus halodurans C-125 (bacteria) Alkalihalobacillus halodurans C-125 (bacteria) |
| Molecular weight | Theoretical: 25.403396 KDa |
| Recombinant expression | Organism:  |
| Sequence | String: ASNEEDRYLM LSGLQHFQFC KRQWALIHIE QQWEENVRTI EGQHLHKKAD QPFMKEKRGS KLTVRAMPIQ SKNLQISGIC DVVEFVQDS EGIELSGVSG SYKAFPVEYK RGKPKKGDED IVQLVAQAMC LEEMLVCRID KGYLFYNEIK HRVEVPITDA L RDKVVQMA ...String: ASNEEDRYLM LSGLQHFQFC KRQWALIHIE QQWEENVRTI EGQHLHKKAD QPFMKEKRGS KLTVRAMPIQ SKNLQISGIC DVVEFVQDS EGIELSGVSG SYKAFPVEYK RGKPKKGDED IVQLVAQAMC LEEMLVCRID KGYLFYNEIK HRVEVPITDA L RDKVVQMA KEMHHYYENR HTPKVKTGPF CNNCSLQSIC LPKLMNKRSV KRYIEGRLSE UniProtKB: CRISPR-associated exonuclease Cas4 |
-Macromolecule #3: PAM/NoPAM strand 2
| Macromolecule | Name: PAM/NoPAM strand 2 / type: dna / ID: 3 / Number of copies: 1 / Classification: DNA |
|---|---|
| Source (natural) | Organism: synthetic construct (others) |
| Molecular weight | Theoretical: 8.575494 KDa |
| Sequence | String: (DG)(DT)(DT)(DC)(DT)(DG)(DG)(DT)(DG)(DG) (DT)(DC)(DC)(DT)(DC)(DA)(DG)(DC)(DT)(DA) (DC)(DG)(DT)(DT)(DT)(DT)(DT)(DT) |
-Macromolecule #4: PAM/NoPAM strand 1
| Macromolecule | Name: PAM/NoPAM strand 1 / type: dna / ID: 4 / Number of copies: 1 / Classification: DNA |
|---|---|
| Source (natural) | Organism: synthetic construct (others) |
| Molecular weight | Theoretical: 9.840351 KDa |
| Sequence | String: (DC)(DG)(DT)(DA)(DG)(DC)(DT)(DG)(DA)(DG) (DG)(DA)(DC)(DC)(DA)(DC)(DC)(DA)(DG)(DA) (DA)(DC)(DT)(DT)(DT)(DT)(DT)(DT)(DG) (DA)(DA)(DT) |
-Macromolecule #6: IRON/SULFUR CLUSTER
| Macromolecule | Name: IRON/SULFUR CLUSTER / type: ligand / ID: 6 / Number of copies: 2 / Formula: SF4 |
|---|---|
| Molecular weight | Theoretical: 351.64 Da |
| Chemical component information | 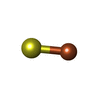 ChemComp-FS1: |
-Macromolecule #7: MANGANESE (II) ION
| Macromolecule | Name: MANGANESE (II) ION / type: ligand / ID: 7 / Number of copies: 1 / Formula: MN |
|---|---|
| Molecular weight | Theoretical: 54.938 Da |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Concentration | 0.75 mg/mL |
|---|---|
| Buffer | pH: 7.5 Details: 20 mM HEPES (pH 7.5), 100 mM KCl, 5% glycerol, 2 mM DTT, and 2 mM MnCl2 |
| Vitrification | Cryogen name: ETHANE / Chamber humidity: 100 % / Instrument: FEI VITROBOT MARK IV |
- Electron microscopy
Electron microscopy
| Microscope | TFS GLACIOS |
|---|---|
| Image recording | Film or detector model: GATAN K3 (6k x 4k) / Average electron dose: 50.0 e/Å2 |
| Electron beam | Acceleration voltage: 200 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | Illumination mode: OTHER / Imaging mode: BRIGHT FIELD / Nominal defocus max: 3.5 µm / Nominal defocus min: 1.5 µm |
| Sample stage | Cooling holder cryogen: NITROGEN |
 Movie
Movie Controller
Controller










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)