+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SARS-CoV-2 spike trimer in complex with Fab NA8, ensemble map | |||||||||
 マップデータ マップデータ | Map after post-processing | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
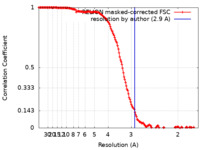
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | |||||||||
 データ登録者 データ登録者 | Tsybovsky Y / Kwong PD / Farci P | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2022 ジャーナル: Cell Rep / 年: 2022タイトル: Potent monoclonal antibodies neutralize Omicron sublineages and other SARS-CoV-2 variants. 著者: Zhaochun Chen / Peng Zhang / Yumiko Matsuoka / Yaroslav Tsybovsky / Kamille West / Celia Santos / Lisa F Boyd / Hanh Nguyen / Anna Pomerenke / Tyler Stephens / Adam S Olia / Baoshan Zhang / ...著者: Zhaochun Chen / Peng Zhang / Yumiko Matsuoka / Yaroslav Tsybovsky / Kamille West / Celia Santos / Lisa F Boyd / Hanh Nguyen / Anna Pomerenke / Tyler Stephens / Adam S Olia / Baoshan Zhang / Valeria De Giorgi / Michael R Holbrook / Robin Gross / Elena Postnikova / Nicole L Garza / Reed F Johnson / David H Margulies / Peter D Kwong / Harvey J Alter / Ursula J Buchholz / Paolo Lusso / Patrizia Farci /  要旨: The emergence and global spread of the SARS-CoV-2 Omicron variants, which carry an unprecedented number of mutations, raise serious concerns due to the reduced efficacy of current vaccines and ...The emergence and global spread of the SARS-CoV-2 Omicron variants, which carry an unprecedented number of mutations, raise serious concerns due to the reduced efficacy of current vaccines and resistance to therapeutic antibodies. Here, we report the generation and characterization of two potent human monoclonal antibodies, NA8 and NE12, against the receptor-binding domain of the SARS-CoV-2 spike protein. NA8 interacts with a highly conserved region and has a breadth of neutralization with picomolar potency against the Beta variant and the Omicron BA.1 and BA.2 sublineages and nanomolar potency against BA.2.12.1 and BA.4. Combination of NA8 and NE12 retains potent neutralizing activity against the major SARS-CoV-2 variants of concern. Cryo-EM analysis provides the structural basis for the broad and complementary neutralizing activity of these two antibodies. We confirm the in vivo protective and therapeutic efficacies of NA8 and NE12 in the hamster model. These results show that broad and potent human antibodies can overcome the continuous immune escape of evolving SARS-CoV-2 variants. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26403.map.gz emd_26403.map.gz | 24.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26403-v30.xml emd-26403-v30.xml emd-26403.xml emd-26403.xml | 21.6 KB 21.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_26403_fsc.xml emd_26403_fsc.xml | 15.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_26403.png emd_26403.png | 60.4 KB | ||
| マスクデータ |  emd_26403_msk_1.map emd_26403_msk_1.map | 325 MB |  マスクマップ マスクマップ | |
| その他 |  emd_26403_additional_1.map.gz emd_26403_additional_1.map.gz emd_26403_half_map_1.map.gz emd_26403_half_map_1.map.gz emd_26403_half_map_2.map.gz emd_26403_half_map_2.map.gz | 260.2 MB 261.4 MB 261.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26403 http://ftp.pdbj.org/pub/emdb/structures/EMD-26403 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26403 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26403 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26403.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26403.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map after post-processing | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.873 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_26403_msk_1.map emd_26403_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
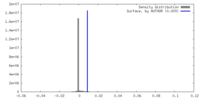
| 密度ヒストグラム |
-追加マップ: Map before post-processing
| ファイル | emd_26403_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map before post-processing | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
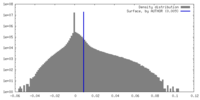
| 密度ヒストグラム |
-ハーフマップ: Half-map 1
| ファイル | emd_26403_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
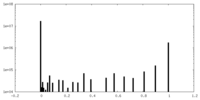
| 密度ヒストグラム |
-ハーフマップ: Half-map 2
| ファイル | emd_26403_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
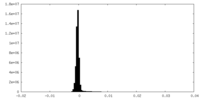
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SARS-CoV-2 S6P spike trimer in complex with Fab NA8
| 全体 | 名称: SARS-CoV-2 S6P spike trimer in complex with Fab NA8 |
|---|---|
| 要素 |
|
-超分子 #1: SARS-CoV-2 S6P spike trimer in complex with Fab NA8
| 超分子 | 名称: SARS-CoV-2 S6P spike trimer in complex with Fab NA8 / タイプ: complex / キメラ: Yes / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 580 KDa |
-分子 #1: SARS-CoV-2 S6P spike trimer
| 分子 | 名称: SARS-CoV-2 S6P spike trimer / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QCVNLTTRTQ LPPAYTNSFT RGVYYPDKVF RSSVLHSTQD LFLPF FSNV TWFHAIHVSG TNGTKRFDNP VLPFNDGVYF ASTEKSNIIR GWIFGT TLD SKTQSLLIVN NATNVVIKVC EFQFCNDPFL GVYYHKNNKS WMESEFR VY SSANNCTFEY VSQPFLMDLE ...文字列: QCVNLTTRTQ LPPAYTNSFT RGVYYPDKVF RSSVLHSTQD LFLPF FSNV TWFHAIHVSG TNGTKRFDNP VLPFNDGVYF ASTEKSNIIR GWIFGT TLD SKTQSLLIVN NATNVVIKVC EFQFCNDPFL GVYYHKNNKS WMESEFR VY SSANNCTFEY VSQPFLMDLE GKQGNFKNLR EFVFKNIDGY FKIYSKHT P INLVRDLPQG FSALEPLVDL PIGINITRFQ TLLALHRSYL TPGDSSSGW TAGAAAYYVG YLQPRTFLLK YNENGTITDA VDCALDPLSE TKCTLKSFTV EKGIYQTSN FRVQPTESIV RFPNITNLCP FGEVFNATRF ASVYAWNRKR I SNCVADYS VLYNSASFST FKCYGVSPTK LNDLCFTNVY ADSFVIRGDE VR QIAPGQT GKIADYNYKL PDDFTGCVIA WNSNNLDSKV GGNYNYLYRL FRK SNLKPF ERDISTEIYQ AGSTPCNGVE GFNCYFPLQS YGFQPTNGVG YQPY RVVVL SFELLHAPAT VCGPKKSTNL VKNKCVNFNF NGLTGTGVLT ESNKK FLPF QQFGRDIADT TDAVRDPQTL EILDITPCSF GGVSVITPGT NTSNQV AVL YQDVNCTEVP VAIHADQLTP TWRVYSTGSN VFQTRAGCLI GAEHVNN SY ECDIPIGAGI CASYQTQTNS PGSASSVASQ SIIAYTMSLG AENSVAYS N NSIAIPTNFT ISVTTEILPV SMTKTSVDCT MYICGDSTEC SNLLLQYGS FCTQLNRALT GIAVEQDKNT QEVFAQVKQI YKTPPIKDFG GFNFSQILPD PSKPSKRSP IEDLLFNKVT LADAGFIKQY GDCLGDIAAR DLICAQKFNG L TVLPPLLT DEMIAQYTSA LLAGTITSGW TFGAGPALQI PFPMQMAYRF NG IGVTQNV LYENQKLIAN QFNSAIGKIQ DSLSSTPSAL GKLQDVVNQN AQA LNTLVK QLSSNFGAIS SVLNDILSRL DPPEAEVQID RLITGRLQSL QTYV TQQLI RAAEIRASAN LAATKMSECV LGQSKRVDFC GKGYHLMSFP QSAPH GVVF LHVTYVPAQE KNFTTAPAIC HDGKAHFPRE GVFVSNGTHW FVTQRN FYE PQIITTDNTF VSGNCDVVIG IVNNTVYDPL QPELDSFKEE LDKYFKN HT SPDVDLGDIS GINASVVNIQ KEIDRLNEVA KNLNESLIDL QELGKYEQ G SGYIPEAPRD GQAYVRKDGE WVLLSTFLGR SLEVLFQGPG HHHHHHHHS AWSHPQFEKG GGSGGGGSGG SAWSHPQFEK |
-分子 #2: NA8 Fab heavy chain
| 分子 | 名称: NA8 Fab heavy chain / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  |
| 配列 | 文字列: VQLLEESGGG AVQPGRSLRL SCEASGFSFN SYGMHWVRQA PGKGLEWVAA IWYSGSDRDY ADSVKGRFS ISRDNSKNTL YLQMNSLRAE DTAVYYCARD PHCTGGVCDA FDLWGQGTMV T VSSASTKG PSVFPGAPSS KSTSGGTAAL GCLVKDYFPE PVTVSWNSGA ...文字列: VQLLEESGGG AVQPGRSLRL SCEASGFSFN SYGMHWVRQA PGKGLEWVAA IWYSGSDRDY ADSVKGRFS ISRDNSKNTL YLQMNSLRAE DTAVYYCARD PHCTGGVCDA FDLWGQGTMV T VSSASTKG PSVFPGAPSS KSTSGGTAAL GCLVKDYFPE PVTVSWNSGA LTSGVHTFPA VL QSSGLYS LSSVVTVPSS SLGTQTYICN VDHKPATPRW TRKLSPNLVT KL |
-分子 #3: NA8 Fab light chain
| 分子 | 名称: NA8 Fab light chain / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  |
| 配列 | 文字列: ELQMTQSPSS LSASVGDRVT ITCRASQSIS SYLNWYQQKP GKAPKLLIYA ASSLQSGVPS RFSGSGSGT DFTLTISSLQ PEDFATYYCQ QSYSTPYTFG QGTKLEIKRT VAAPSVFIFP P SDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN SQESVTEQDS ...文字列: ELQMTQSPSS LSASVGDRVT ITCRASQSIS SYLNWYQQKP GKAPKLLIYA ASSLQSGVPS RFSGSGSGT DFTLTISSLQ PEDFATYYCQ QSYSTPYTFG QGTKLEIKRT VAAPSVFIFP P SDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN SQESVTEQDS KDSTYSLSST LT LSKADYE KHKVYACEVT HQGLSSPVTK SFNRGEC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 / 詳細: PBS |
|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: GOLD / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.039 kPa |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)